18.3: RNA processing en turnover
1/64
There's no tags or description
Looks like no tags are added yet.
Name | Mastery | Learn | Test | Matching | Spaced | Call with Kai |
|---|
No analytics yet
Send a link to your students to track their progress
65 Terms
slide dogma
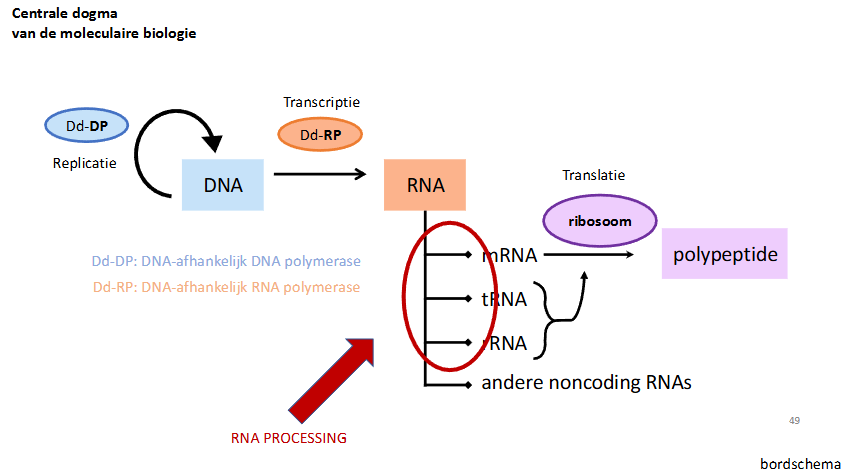
tabel met functies RNA’s

grootste deel van totale cellulaire RNA
rRNA (70-80%)
aantal verschillende rRNA’s bij bacteriën en eukarya
bact: 3 verschillende rRNA
euk: 4 verschillende rRNA

welke ribosomale subeenheden bij pro- en eukaryoten
Bacteriën: 70S
Grote subeenheid: 50S
23S
5S
Kleine subeenheid: 30S
16S
Eukarya: 80S
Grote subeenheid: 60S
28S
5.8S
5S
Kleine subeenheid: 40S
18S
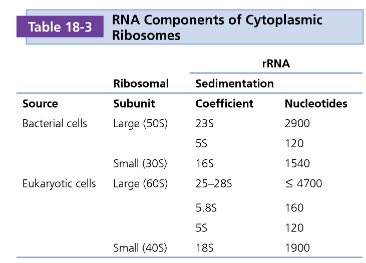
Wat betekent die S
Svedberg, sedimentatie coëfficiënt
→ zwaardere partikels sedimenteren eerst en dan de andere.
Ze sedimenteren volgens de sedimentatiecoëfficiënt (gecorreleerd met de massa, vorm en massadichtheid van het partikel)
waar vind eukaryotische rRNA synthese plaats
nucleolus
waaruit bestaat de nucleolus en wat deon alle eenheden
fibrillen en granulen zonder membraan
fibril: transcriptie rRNA en pre-rRNA processing
granulen: pre-ribosomale subeenheden vormen
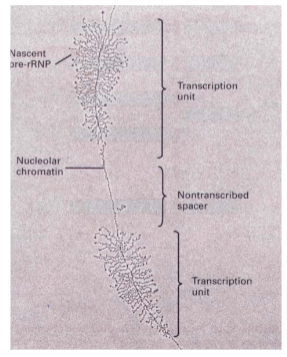
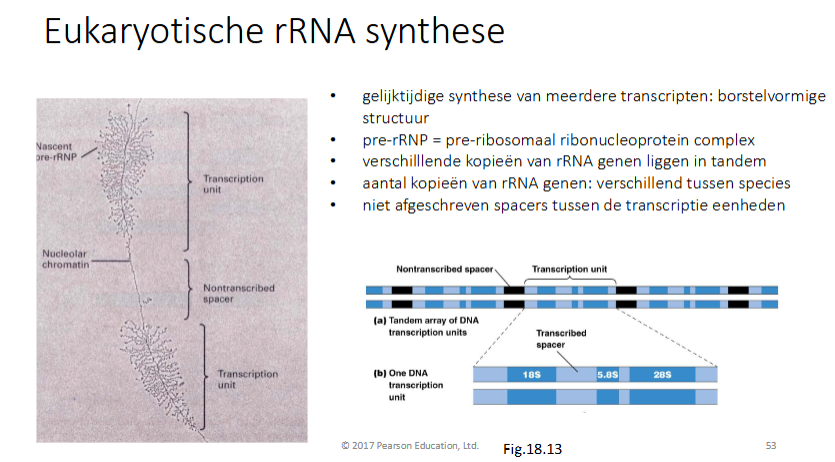
wat zie je hier
Gelijktijtide synthese van meerdere transcripten waardoor je een borstelvormige structuur krijgt.
We krijgen pre-RNP’s: pre-ribonulceoproteïne complex
Dit doordat de verschillende kopieën van RNA genen in tandem liggen, het aantal kopiën is verschillend tussen species
Er liggen ook niet afgeschreven spacers tussen de transcriptie eenheden
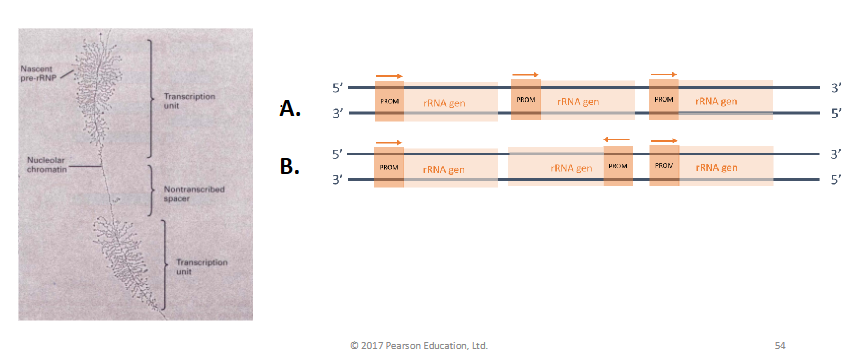
hoe liggen de promotoren van de rRNA genen tov elkaar
A, in dezelfde richting
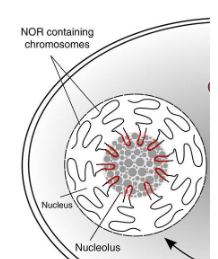
wat zijn NOR’s
nucleolus organisator regio’s → DNA regio dat rRNA genen bevat dei in tandem liggen en gelegen id i de nucleolus
liggen alle NORs op zelfde chromosoom
hoeveel bij mens
meerdere kunnen op verschillende chromosomen liggen
bij mens 5 (dus in tot 10 door diploïd)
wat met nucleolus tijdens mitose
verdwijnt
blijft nucleolus hele tijd zelfde grote
nee, grootte corrreleert met activiteit
als hoge snelheid van proteinsynthese hebben we veel ribosomen nodig en kan to t25% van nucleair volume innemen.
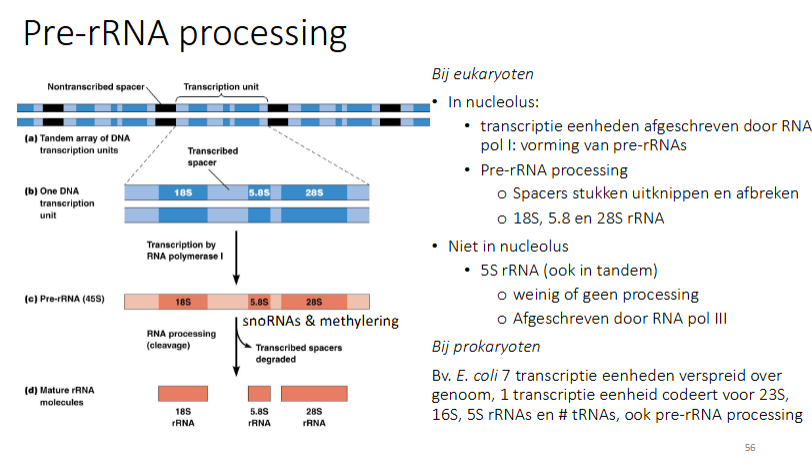
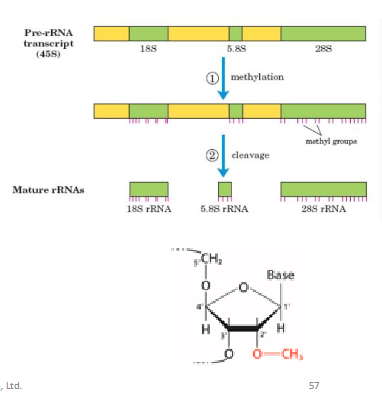
hoe gebeurt pre-rRNA processing bij eukarya
in de nucleolus:
de transcriptie-eenheden worden afgeschreven door RNA pol I: pre'-rrNA wordt gevormd
pre-rRNA processing:
de spacer stukken uitknippen en afbreken
dit geldt voor 18S, 28S, 5.8S rRNA
iet in nucleolus: 5S rRNA (behoort niet tot de NOR’s)
weinig tot geen processing
afgeschreven door RNA pol III
Hoe is de pre-rRNA processing geregeld
snoRNA: small nucleolar RNA: korte noncoding RNA hoofdzakelijk in nucleolus
ze binden aan complementaire regio’s in pre-rRNA en coördineren de pre-rRNA processing bv bepalen plaatsen van methylering en knipping
Methyleringen: op 2’ OH van ribose
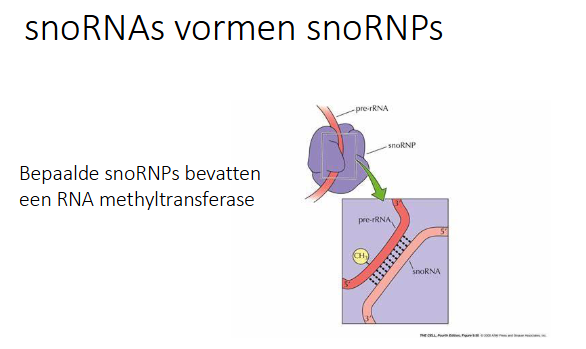
hoe bepaalt snoRNA de plaats van methylering
Bepaalde snoRNA’s vormen snoRNP’s die een RNA methyltransferase bevatten, zo wordt het pre-rRNA gemethyleerd
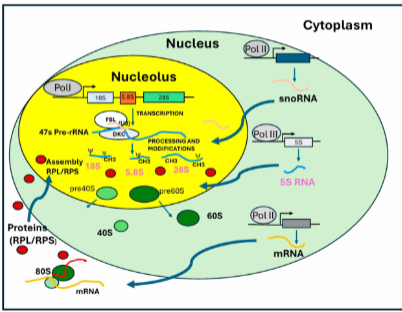
rol van de verschillende eukaryotische RNA polymerase in rRNA en ribosomen maken
RNA pol I: pre-rRNAA na processing: 18S, 5.8S, 28S rRNA
RNA pol II:
synthese van pre-mRNAs, na processing mRNA export naar cytosol → translatie in eiwitten (RPL en RPS: ribosomale proteins, large en small)
synhtese snoRNA
RNA pol III: 5S RNA
In de nucleolus krijgen we dan de assemblage van pre-ribosomale eenheden → import van de RPs op rrNAs tvv de (pre)ribosomale eenheden
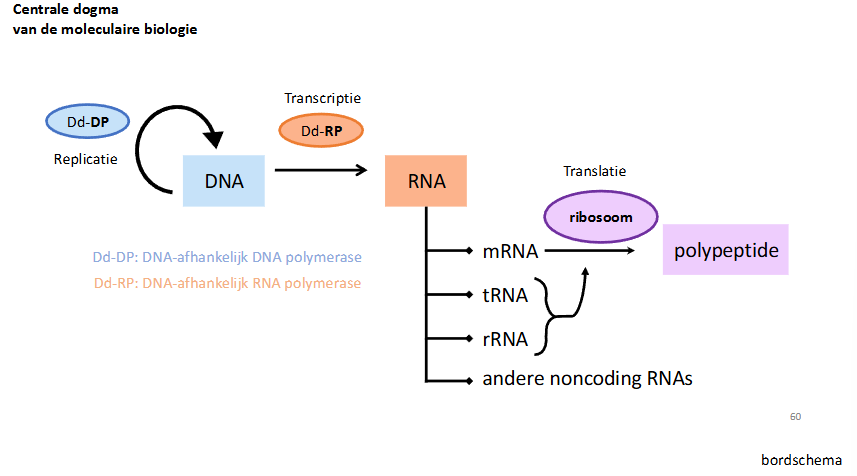
slide centrale dogma
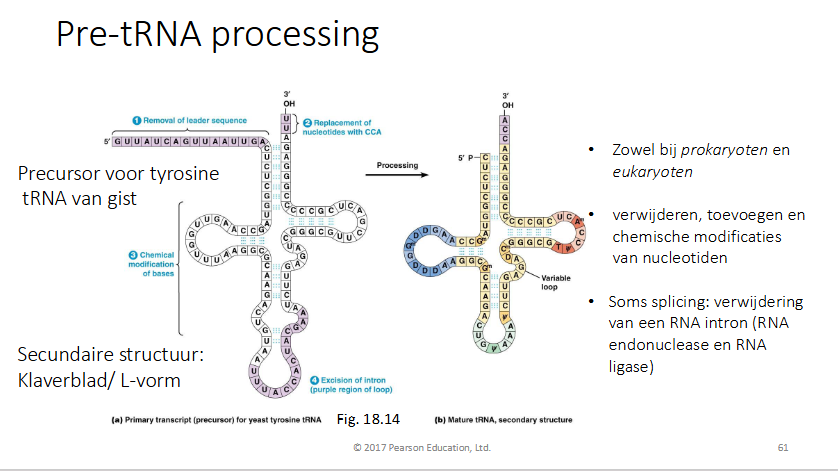
in welke 4 stappen verloopt pre-tRNA processing
bij welke organismen verloopt dit
Bij eu en prokarya
Leidersequentie wordt verwijderd aan 5’ kant
nucleotiden aan 3’ verwijderen en CCA toevoegen
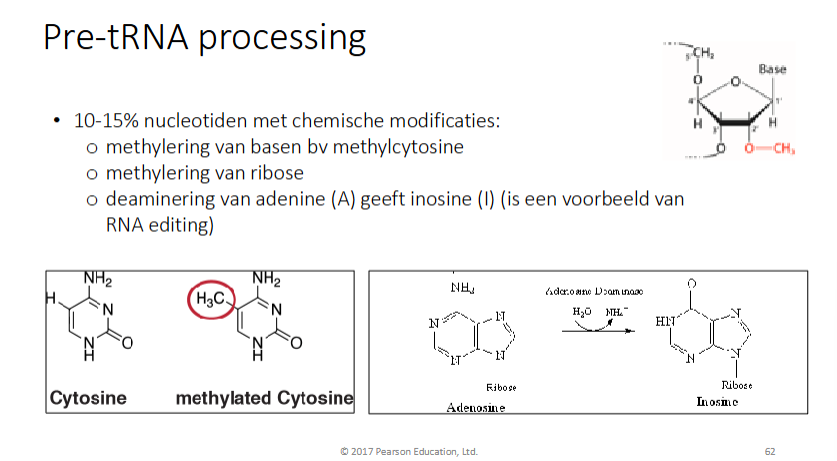
Chelmische modificatie van de basen:
methyleringen van basen (bv methylcytosine)
methyleringen van ribose
dealinering van A geeft iosine (I) → reactie gekatalyseerd door adenosine deaminase
soms gebeurt er splicing: verwijderen van een RNA intron (door RNA endonuclease en dan ligase)
komt inosine ook voor in ds DNA
nee, wordt verwijderd door BER
bij pre-tRNA processing komt soms splicing voor, was dit ook bij rRNA
nee, de non transcrubed dingen werden weggedaan, maar werden niet terug aan elkaar gedaan
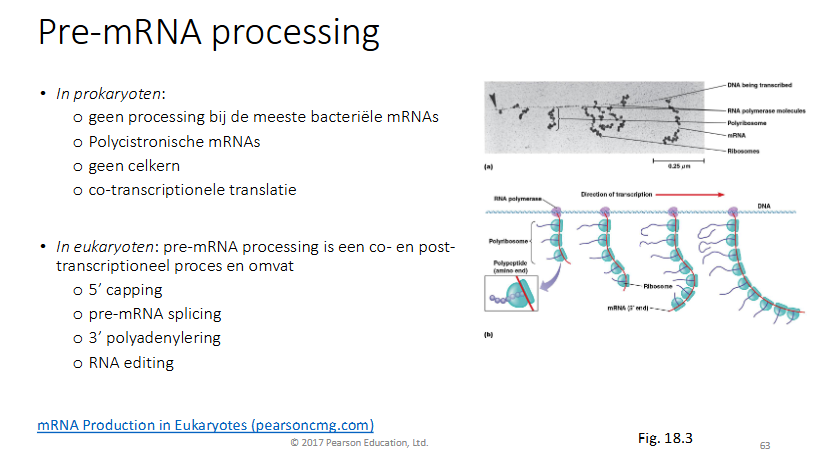
Hoe gebert pre-mRNA processing bij eukarya en prokarya
pro
geen processing (mRNA wordt gemaakt en meteen door ribosomen vertaald), tijdens de transcriptie kan al translatie gebeuren (polyribosoom)
polycicstronische mRNAs (draagt code voor meerdere eiwitten)
geen celkern
co-transcriptionele translatie
Eu: pre-mRNA processing is een co- en post-transcriptioneel proes en omvat
5’ capping
pre-mRNA splicing
3’ polyadenylering
RNA editing
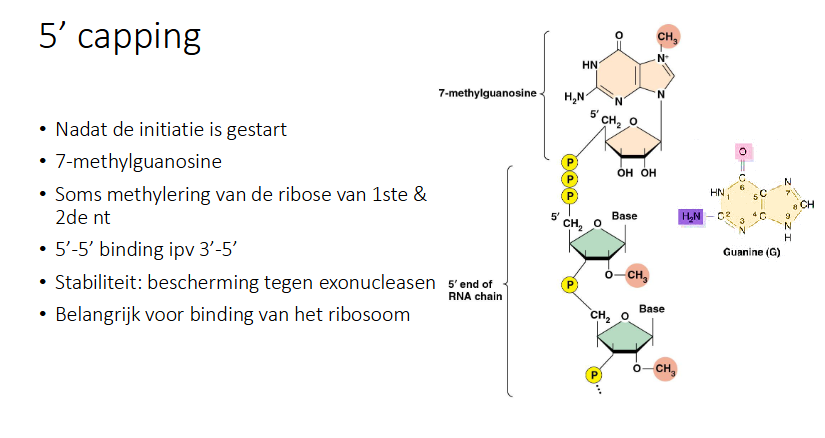
Hoe gebeurt 5’ capping van pre-mRNA en wat is de functie ervan
Nadat de initiatie is gestart wordt een 7-methylguanosine covalent gebonden aan uiteinde
Soms is er ook een methylering van de ribose van het 1e en 2e nt
RNA pol kan de novo starten en dys heeft het eerste nucleotide 3 fosfate hangen aan uiteinde, deze worden dan neit aan de 3’ OH van 7-methylguanosine gebonden, maar aan de 5’ waardoor je een 5’-5’ binding hebt ipv een 3’-5’ zoals normaal
Functie: stabiliteit bieden en beschermen tegen exonucleasen
belangrijk voor binding ribosoom omdat deze de 5’ capping gebruikt om mRNA te herkennen
wanneer start 5’ capping
vanaf transcriptie start en je een vrij 5’ uiteinde hebt
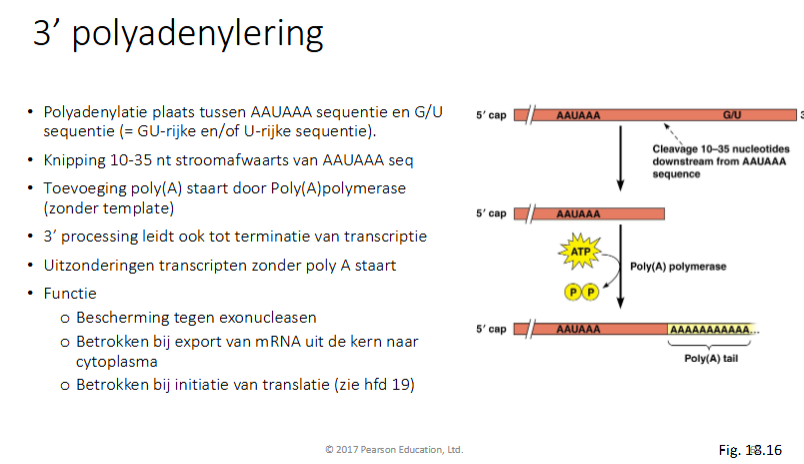
hoe gebeurt 3’ polyadenylering en wat is de functie
polyadenylatie plaatst tussen AAUAAA seq een G/U seq (GU-rijke en / of U)rijke sequentie)
knipping 10-35 nt stroomafwaarts van AAUAAA seq
toevoeging poly-A-staart door poly(A)polymerase (zonder template) en gebruikt ATP
3’ processing leid ook tot terminatie transcriptie (RNA pol II dissocieert)
uitzonderingen: transcripten zonder polyAstaart (zoals mRNA van histonen)
Functie
beschermen tegen exonucleasen
betrokken bij export mRNA uit kern naar cytoplasma
betrokken bij initiatie van trasnlatie
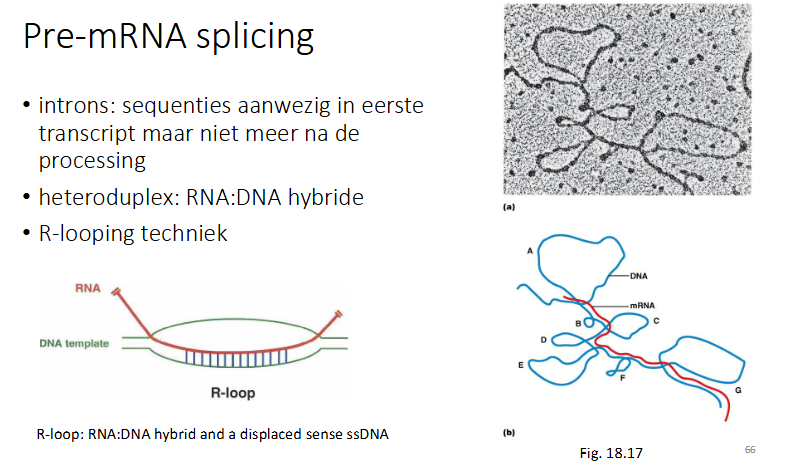
wat zijn introns
seqenties aanwezig in eerste transcript, maar niet na processing
hoe gebeurt pre-mRNA splicing
er wordt een hetroduplex gevormd: DNA:RNA hybride
R-looping techniek: het RNA hybridiseert met de matrijs streng, er wordt een complex gevorm van 2DNA en 1RNA strengen
functie spliceosomen
verwijderen van introns en samenvoegen van de exonen
weetje!
15% van de erfelijke aandeoningen zijn fouten in slpicing van pre-mRNA
wat zijn exonen
sequenties die overblijven en aanwezig zijn in matuur RNA
wanneer vidnt splicing plaats
tijdens de transcriptie en ook nog wat erna

voorbeeld van een splicing-related aandoening
Hutchinson-Gilford progeria syndrome (HGPS)

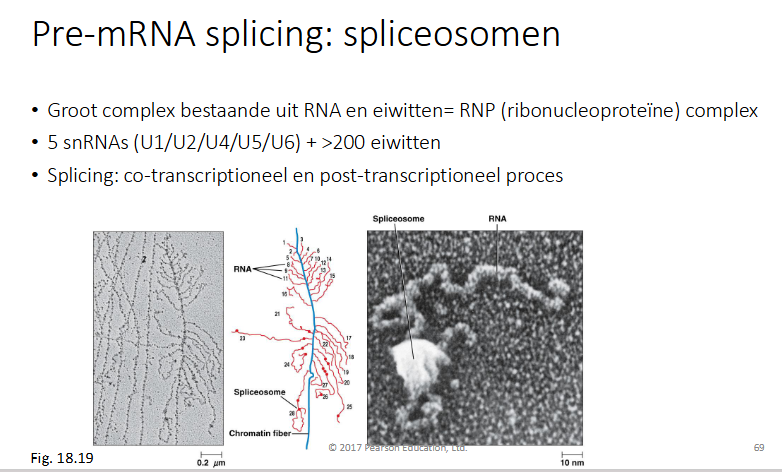
Waaruit bestaan spliceosomen
Groot complex bestaande uit RNA en eiwitten = RNP (ribonucleoprotein) complex
5snRNA’s (small nuclear RNA’s) (U1/U2/U4/U5/U6) + >200 eiwitten
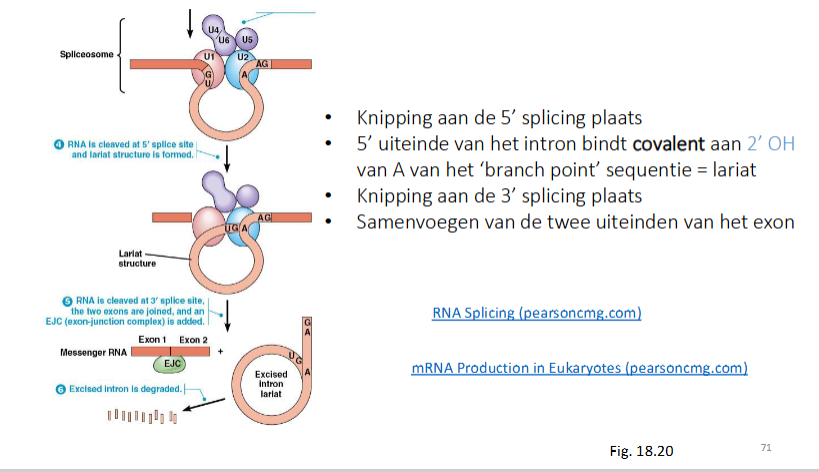
hoe gebeurt assemblage van spliceosoom
Consesus sequenties op intron: 5’ GU en 3’ AG → splicing plaatsen
er is op het intron ook een branch point seq
Opeenvolgende binding van snRNP’s op pre-MRNA
U1 snRNP bindt aan 5’ splice site (GU)
U2 snRNP bindt aan branch point
U4/U6 en U5 binden op U1 en U2 snRNP’s
knipping van 5’ splice site
5’ uiteinde (net geknipt) bidnt aan 2’OH van A van branch point seq = lariat
knipping 3’ splice site
samenvoegen 2 uiteinden van exon
overgang van exon 1 naar 2 wordt gemarkeerd (exon boundary) → EJC bindt
uitgeknipte intronen worden afgebroken

slide erna
wat zijn exon junction complexen
Multiproteine complex bindt op elk nieuw gevormde exon-exon verbiding
heeft een rol bij
non-sense gemedieerde mRNA afbraak (NMD)
mRNA export → EJC complex bindt nucleaire export factor 1 (NXF1) → export door kernporie
mRNA lokalisatie
mRNA translatie

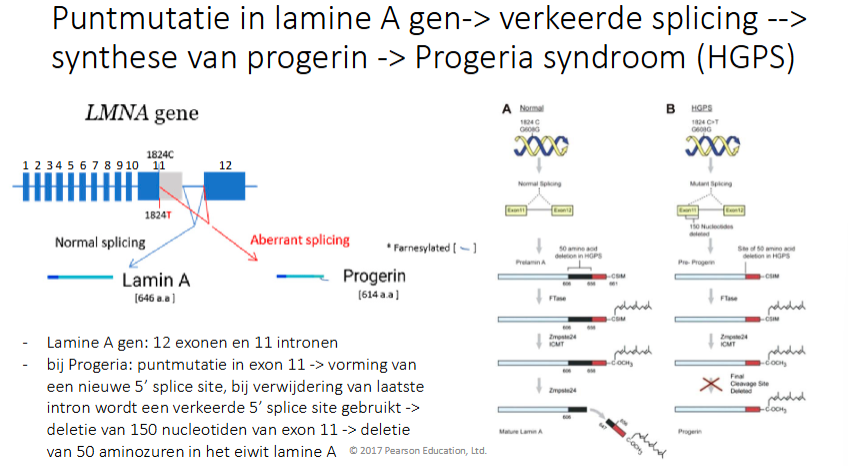
Wat gebeurt er bij progeria
Normaal:
lamine A eiwit gevormd → wordt gefarnesyleerd (signaal om naar nucleaire membraan te gaan) → wordt dan afgeknipt
Bij progeria:
Puntmutatie in lamine A gen → 50 AZ’en verwijderd
De ferneslyering treedt nog op → knippen gebeurt niet meer omdat de knippplats voor het protease in de 50 AZ’en aanwezig waren. D>oordat het niet geknipt wordt, blijft het aanwezig in de nucleaire membraan en krijg je daar geen mooie vezels.
Het lamine A gen heeft 12 exonen en 11 intronen
Door de puntmutatie in exon 11 wordt er een alternatieve 5’ splice site gegenereerd waardoor 150nt (zijn dus 50 AZ’en) worden verwijderd
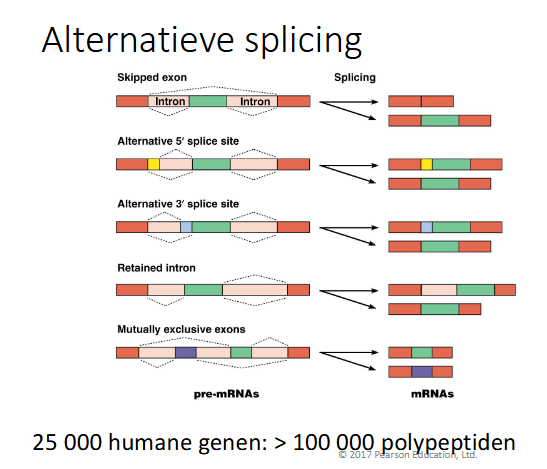
op welke manieren kan alterntieve splicing gebeure
skipped exon: een exon wordt mee verwijderd
alternatieve 5’ slice site: kan resulteren in een groter of kleiner mRNA
alternatieve 3’ splice site: verandert lenge mRNA
retained intron: een intron wordt behouden
mutually exclusive exons: 2 soorten mRNAs mogelijk omdat er 2 exonen zijn die nooit samen voorkomen
waardoor worden GU-AG introns herkend
GU-AG spliceosoom
waardoor worden AU-AC introns herkend
AU-AC spliceosoom
wat zijn self splicing introns
waar komt het voor
knippen zichzelf uit RNA zonder eiwitten
het RNA werkt als een enzyme → ribozyme
Komt voor in mitochondiren (gist / pplanten en sommige bacterien)
wat zijn splicing enhancers en silencers
Stukjes RNA waar eiwittten of snoRNA omsplicing aan/uit ze zetten en regelen zo pre-mRNA splicing
wat gebeurt er met de introns na splicing
meestal afgebroken, soms vorming van een functioneel product zoals een RNA (bv een sno RNA) of helpen ze bij evolutie (bv via exon shuffling of exon duplicatie)

waar start de translatie en waar stopt
startcodon: AUG
stop aan stopcodon
slide bordschema
Wat is exon shuffling
Genetische reconminatie (uitwisselong van DNA) tussen de intronen van 2 verschillende genen leidt tot genen met nieuwe combos van exonen, gekend als exon shuffling
Bv homologe recombinatie tussen retrotransposons die gelegen zijn in intronen van twee verschillende genen
wat zijn Alu sequenties
retrotransposons (SINEs) en het zijn repeats
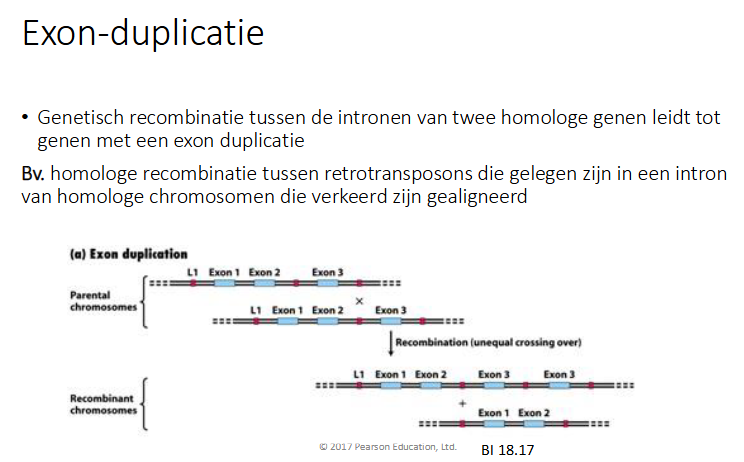
Wat is exon duplicatie
genetische recombinatie tussen de intronen van twee homologe genen leidt tot genen met een exon duplicatie
bv homologe recombinatie tussen retrotransposon die gelegn zijn in een intron van homologe chromosomen die verkeerd zijn gealigneerd
Welke subnucleaire structuren in de celkern
Nucleolus + verschillende andere kleine structuren, zonder membraan
Belangrijk voor processing en verdere afhandeling van RNA in de kern
bv
Cajal bodies: rol in processing (maturatie) van snoRNA en snRNA
Nucleaire spleckles = interchromatin granule clusters: rijk aan RNA’s, pre-mRNA splicing factors/snRNPs en niet-snRNPs splicing factor, stockage plaats, dynamisch, heeft een rol in pre-mRNA splicing

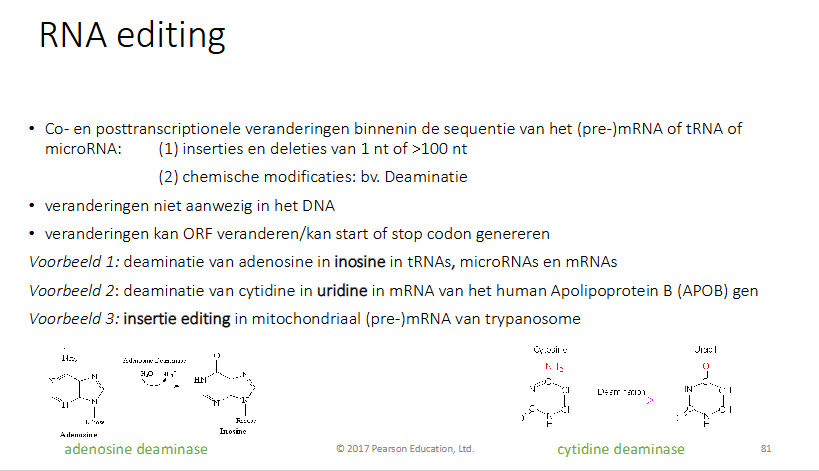
Wat gebeurt er bij RNA editing
Co- en posttranslationele veranderingen binnenin de sequentie van (pre)mRNA of tRNA of microRNA
inserties en deleties van 1nt of >100 nt
chemische modificaties bv deaminatie
veranderingen zijn niet aanwezig in DNA (zoals bij polyAstaart)
veranderingen kan ORF (open reading frame) / kan een start of stop codon genereren
vb1: deaminatie van adenine in inosine in tRNA, microRNA en mRNA door adenosine deaminase
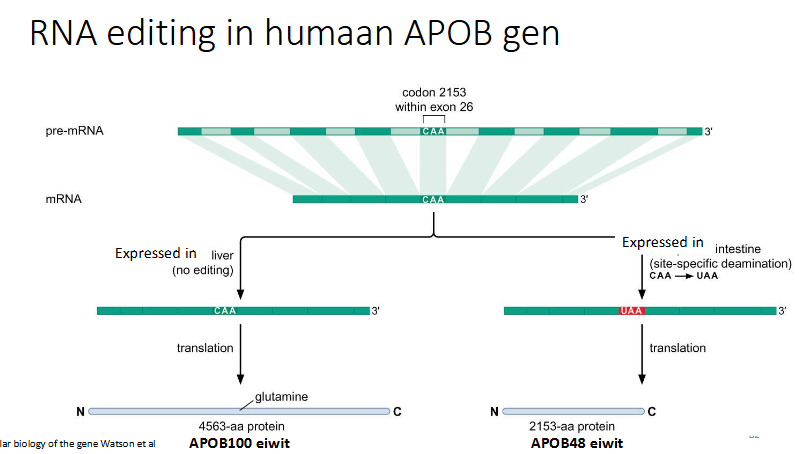
vb2: deaminatie van cytidine in uridine in mRNA van human apolipoportein B → APOB gen) door cytidine deaminase
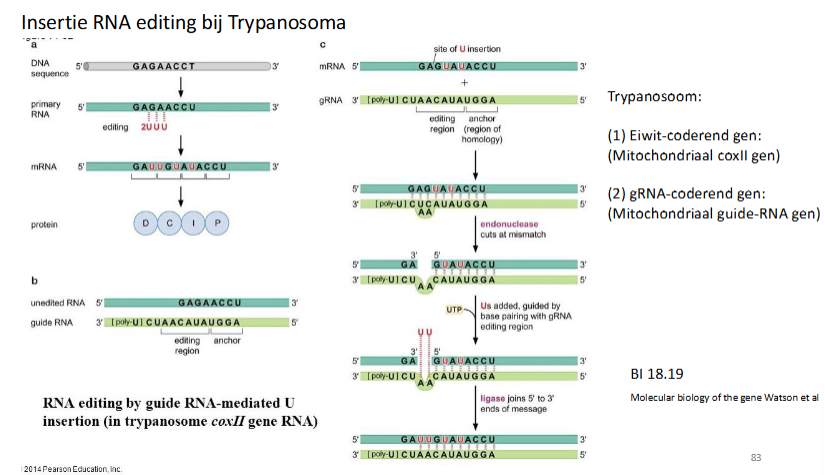
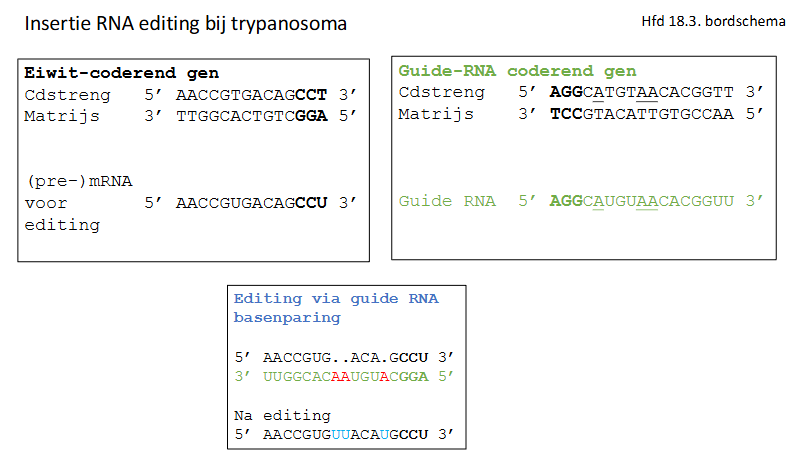
vb3: insertie editing in mitochondriaal (pre)mRNA van trypanosome
functie APOB
belangrijke rol transport vetten in bloed
hoe gebeurt de cytidine deaminase in humaan APOB gen
hoe gebeurt isnertie RNA editing bij Trypanosoma
Trypanosoom:
Eiwit-coderend gen (mitochondriaal coxII gen)
gRNA-coderend gen (mitochondriaal gRNA gen)
Het gen zorgt voor aanmaak van een onberwerkt mRNA.
Een gRNA wordt ook aangemaakt en bindt eraan.
Waar ze niet op elkaar passen weet de cel dat hij dingen (bv U) moet toevoegen.
Enzymen zullen het mRNA knippen → voegen juiste dingen toe → plakken mRNA weer aan elkaar.
→ gRNA dient voor mRNA te editen en gRNA is reverse complement aan het finaal matuur mRNA.
slide bordschema
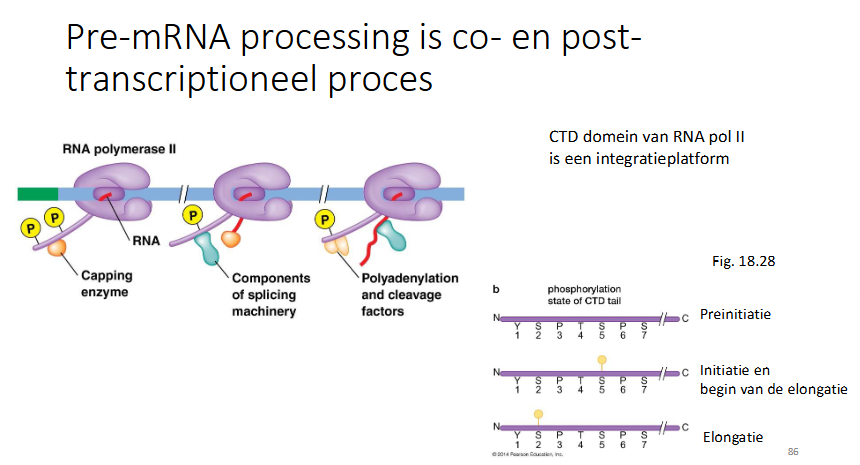
Hoe wordt ervoor gezorgd dat pre-mRNA processing een co- en posttranscriptioneel proces is
enzyme vertanwoordelijk voor de capping bindt op CTD domein van RNA pol II en zorgt dat RNA dat gemaakt wordt meteen wordt gecapt.
Door verandering van de fosforyleringcode van RNA pol II wordt spliceosoom gerecruteerd
dan worden ook polyadenylering (voor 3’ staart) en andere factoren gerecruteerd
→ RNA pol II is een integratieplatform
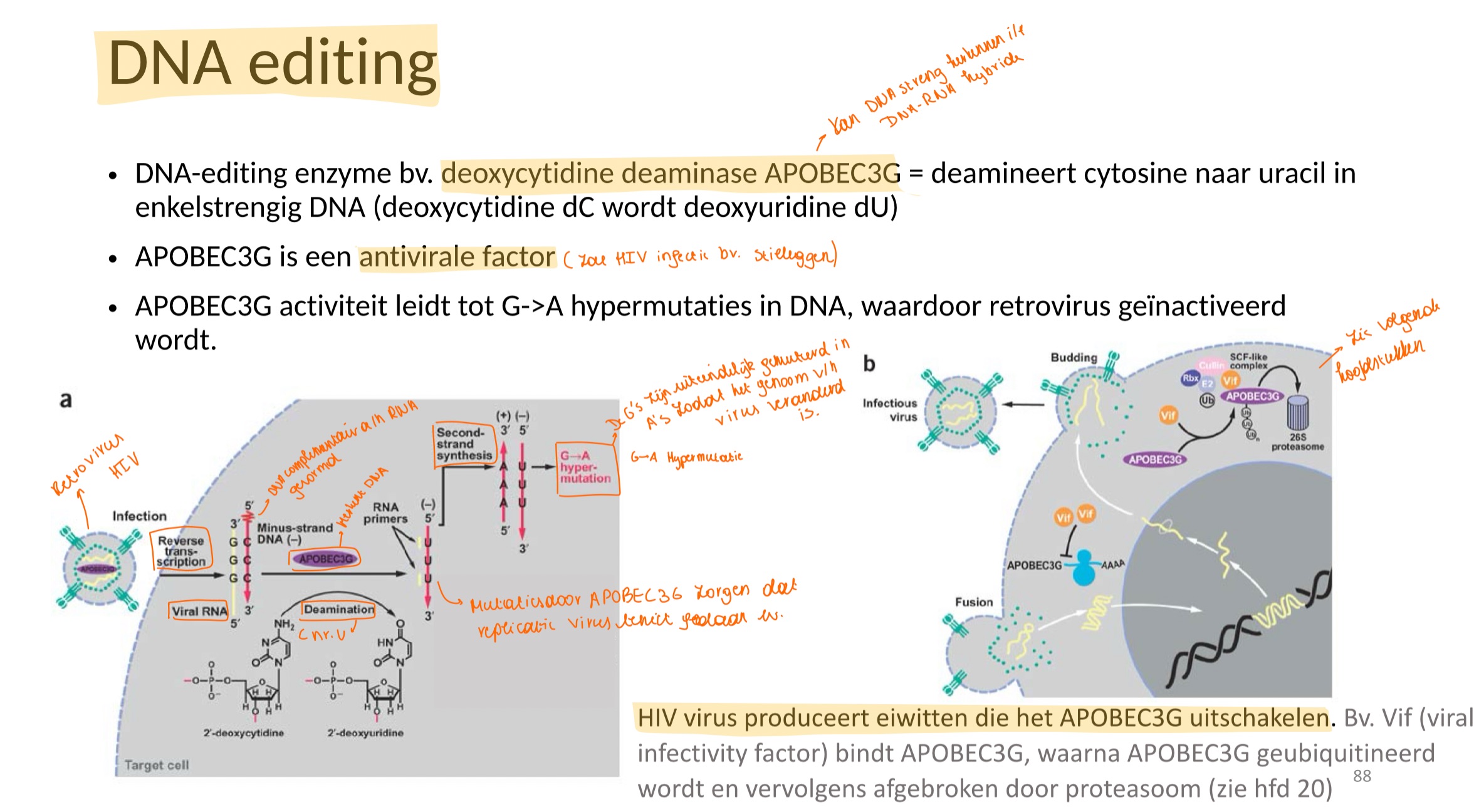
Wat is DNA editing
Een DNA-editing enzyme (bv deoxycytidine deaminase APOBEC3G = deamineert cytosine naar uracil in ssDNA).
Zo is APOBEC3G een antivirale factor: HIV komt in de cel en er wordt een ssDNA gevormd complementair aan het virale RNA (reverse transcriptase activiteit) → APOBEC3G herkent ssDNA en zorgt voor mutaties → replicaite van virus wordt teniet gedaan → genoom van virus is verandert
Wat is halfwaarde tijd van mRNA en hoveel bedraagt het
Tijd die nodig is om 50% van dat mRNA af te breken: <30min - 10 uur
prokaryoten: enkele minuten
eukarya: uren-dagen
hoe halfwaardetijd RNA meten
Pulse-chase experimanten: radioactief maken door NTP, radioactief NTP voor half uur aan cel toevoegen endan wegnemen en kijken hoelang duurt voordat radioactiviteit voor helft weg is
wat te gebeuren met halfwaardetijd bij mRNA vaccins
voor mRNA vaccins dus halfwaardetijd verlengen (stabieler maken)
verschil is stabiliteit mRNA en rRNA/tRNA
mRNA: hoge turnover → worden gemaakt en weer afgebroken
rRNA en tRNA zijn meer stabiel
wat bepaalt levensduur mRNA
oa door lengte polyAstaart (want beschermt tegen exonucleasen) en aantal AU-rijke elementen in 3’UTR

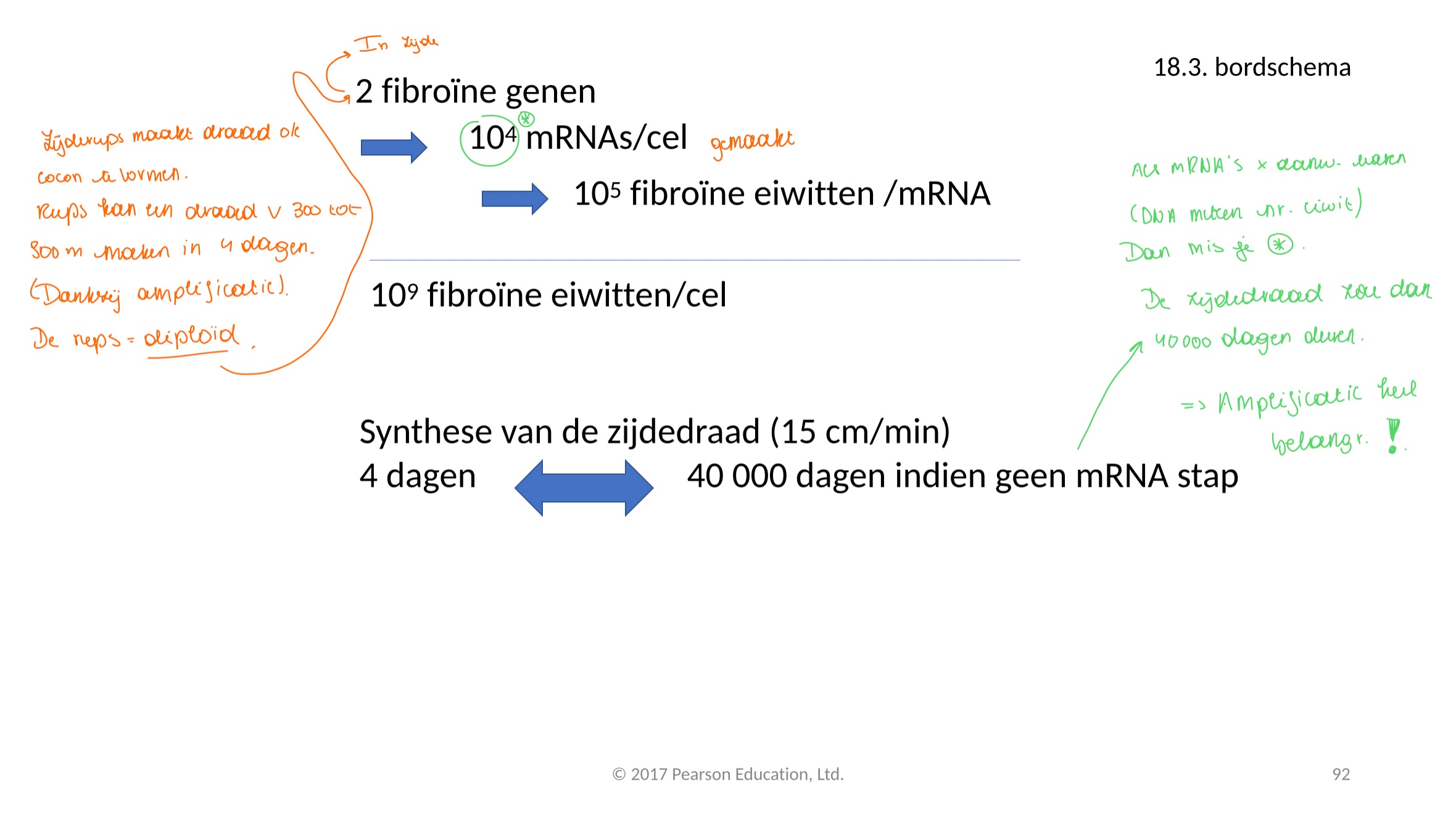
amplificatie van mRNA en rRNA / tRNA
DNA-mRNA-eiwit: sterke amplificatie (meestal 2 genen voldoende) → een gen geeft meerdere mRNA’s en mRNA geeft meerdere eiwitten
DNA-rRNA/tRNA: minder amplificatie → RNA is het eindproduct, er zijn bv meerdere kopieën van de rRNA genen
waar vinden we fibroïne terug
in zijde
De autoimmuun ziekte ‘systemic lupus erythematosus ‘kan ontstaan
als het immuunsysteem van de patiënt zijn snRNPs aanvalt. Waarom
leidt de uitschakeling van deze complexen tot ernstige effecten?
snRNPs; small nuclear ribonucleoproteins zijn essentieel voor correcte splicing, ze
vormen samen een spliceosoom.
Minder snRNPs: splicing loopt mis, introns blijven behouden, dus groot effect op
het ORF: resulteert dikwijls in verkeerde eiwitten (verkeerde aminozuren worden
toegevoegd aan een eiwit of ook vroegtijdige stopcodons, waardoor het mRNA al
dan niet wordt afgebroken (NMD)