13- Reconocimiento molecular inmunidad innata receptores
1/14
Earn XP
Description and Tags
Name | Mastery | Learn | Test | Matching | Spaced |
|---|
No study sessions yet.
15 Terms
Receptores
PRR= Receptores que reconocen patrones
Patrones= moleculas de patógenos (PAMP) o daño (DAMP)
PAMPs= patrones moleculares asociados a patogenos
DAMPs= patrones moleculares asociados a daño
Proceso: reconocen patrones con los receptores de las celulas innatas, y estas decodifican la señal dando factores de transcripción.
1) Reconocimiento:
2) Decodificacion de señales
3) Mecanismos efectores
4) Eliminación de patogeno
Mecanismos efectores del sistema inmune innato:
Fagocitosis
Lisis osmotica (mediada x complemento)
Apoptosis (NK, con perforina, gaslina, FAS y FASL)
Opsonización (complemento)
En membrana: TLR y CLR
En citosol: NOD y RIG
Reconocimiento de patrones
PAMPs: patrones moleculares asociados a patógenos. Son motivos conservados por patógenos (no puede cambiarlo y nuestras células no lo tienen)
DAMPs: patrones moleculares asociados a daño. Nuestras moléculas, pero normalmente están escondidas (ADN, Ac úrico, ATP, etc). Se muestran en muerte celular.
MAMPs: moléculas que la microbiota libera ante patógenos. Varios receptores siempre expresados.
Tipos:
1) De membrana
2) Intracelulares membranarios
3) Intracelulares citosólicos
4) Secretados (MBL)
ALTA INESPECIFICIDAD, no reconocen cual microorganismo es.
Innato vs Adaptativo
Innato
Línea germinal: proviene de los antecesores, codificado x la línea germinal
Muchos x célula: muchas copias del mismo receptor x celula y se expresan varios x célula (en monocitos, macrófagos, neutrófilos, células dendríticas y NK)
No clonal: cada célula tiene los mismos receptores, y son heredados.
SIN recombinación
NO MEMORIA, entrenamiento x 1 año de vida
Reconoce patrones moleculares (PAMPs/DAMPs)
Repetición de patrón (mismo patrón puede están en distintas bacterias)
Adaptativo
Recombinación génica: cada Linfocito B forma su propia especificidad, exclusivo en cada linfocito
1 x célula (Diferentes): cada célula tiene un tipo de receptor BCR (Linfocitos B) o TCR (Linfocito T) y son diferentes de: ALTA ESPECIFICIDAD
Clonal: cada célula tiene un receptor único x recombinación genética y cada antígeno es único y genera una respuesta específica.
TIENE MEMORIA: desarrolla memoria tras el contacto con antígenos
Reconoce antígenos específicos mediante BCR y TCR

Secuencia luego del reconocimiento
Reconocen PAMP y ➕ ️Proteinas adaptadoras.
↪ Desencadena: Cascada de señalizacion con ➕️ Factores de transcripción de:
Moleculas proinflamatorias (cotoquinas y quimioquinas)
📢Reclutamiento de Leucocitos⬆Permeabilidad de endotelio vascular
Algunos PRR se unen al patogeno y fagocitan x endocitosis (MBL)
Receptores membranarios
TLR: Receptores TOLL, reconocen⏩ PEPTIDOS, LPS
CLR: Receptores tipo LECTINA C, reconocer⏩ CARBOHIDRATOS de patógenos
SCRAVENGERS: Barrenderos a diferentes cosas limpian restos
Receptores intracelulares solubles
NLRs RECEPTORES NOD reconocen ⏩peptidoglicanos (pared bacteriana) ATP, ác. úrico, daño lisosomal UV forman inflamosomas
RLRs RECEPTORES RIG reconocen⏩ ARN VIRAL
AIM2 STING reconocen⏩ ADN bacteriano y VIRAL en citosol (CDSs)
Receptores solubles secretados
PENTRAXINAS⇢ PROTEINA C REACTIVA⏩ reconocen fosforilcolina (fosfolipidos) de M.O
COLECTINAS⇢ MBL reconocen manosa y fructosa (hidratos de carbono)🍄
PRRs RECONOCEN PÉPTIDOS (peptidoglicanos glucopéptidos lipopeptidos)
LÍPIDOS (lipopolisacáridos LPS)
CARBOHIDRATOS (manosa mananos glucanos)
ARN doblecadena ADN bacteriano ETC
DOMINIOS de Receptores membrenarios: TOLL (TLRs)
Domino membrana: Anclados a la membrana plasmática y otros a la endosomal con
Dominio extracelular: rico en leucinas
Dominio citosolico (TIR): que une proteínas y activa señalización
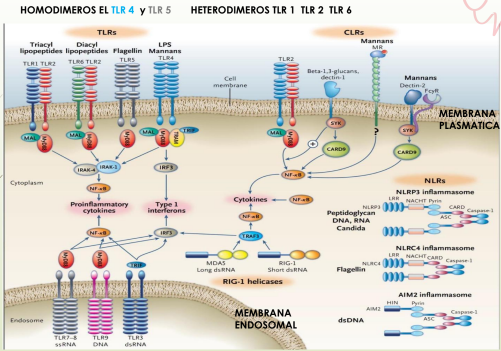
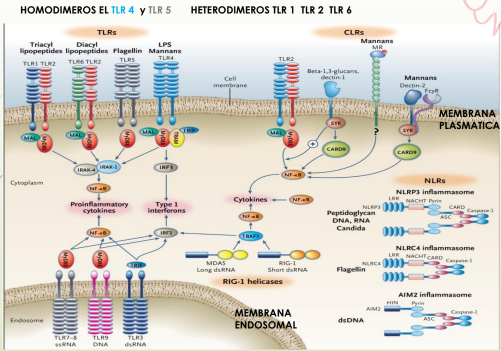
Receptores membrenarios: TOLL (TLRs)
EN LA MEMBRANA PLASMATICA
Son dímeros: Homo o heterdimeros (1 2 y 6)
MEMBRANA PLASMÁTICA:
TLR 1⏩ Lipopeptidos unidos a lípidos y péptidos
de membrana bacteriana
TLR 2⏩ Glucolípidos, peptidoglicanos, lipoproteínas de membrana bacteriana
TLR 6⏩ Lipopeptidos de membrana bacteriana
TLR 4⏩ Lipopolisaridos (LPS, Gram Negativas)
TLR 5⏩ Proteína estructurales (Flagelina, proteína del flagelo bacteriano)
Receptores membrenarios: TOLL (TLRs)
EN LA MEMBRANA ENDOSOMAL
TLR 3 ARN doble cadena
TLR 7 ARN simple cadena
TRL 8 ARN simple cadena
TRL 9 ADN CpG bacteriano
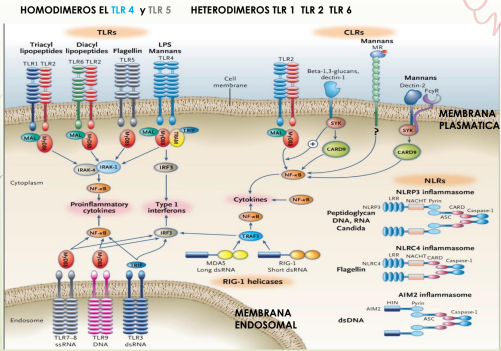
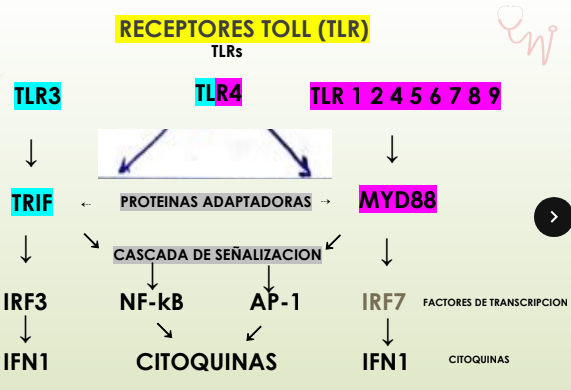
SEÑALIZACION DE TLRs
TLR (Dominio extracelular) Reconoce un patrón genera cambios en el receptor:
➕Dominio citosolico, recluta: PROTEINAS ADAPTADORAS MyD88 Y TRIF
Reclutan QUINASAS que ACTIVAN proteínas por fosforilación (➖FOSFATASAS inhiben quitando fosforo (desfosforilando)
La CASCADA DE SEÑALIZACION se activan FACTORES DE TRANSCRIPCION NF-kB que van al nucleo se unen al ADN y transcriben:
-CITOQUINAS PROINFLAMATORIAS
-MOLECULAS DE ADHESION ⏩permiten migracion
-QUIMIOQUINAS⏩ atraen linfocitos
-IFN 1 inhibe replicación ARN viral
-CO-ESTIMULADORAS (B7 para activar linfocitos T)
RECEPTORES MEMBRANARIOS CLR (LIKE LECTINA C)
Características
CLRs son membranarios necesitan Ca+
Todos son diferentes pero todos reconocen carbohidratos.
Con o sin domino citosólico
Receptores que pueden regular la respuesta inflamatoria
Dectin 1: Reconoce β GLUCANOS
Cadenas de glucosa con enlaces β1-4 1-6 en hongos, dominio de señalización con proteína adaptadora SYK (TLR tienen proteína adaptadora TRIF o MYD88)
Dectin 2: renoce MANANOS
Cadenas de manosas POLISACARIDOS en hongos
(no tiene señalización propia) recluta quinasa SYK pero no directamente, luego da la cascada de señalización y
activa los factores de transcripción NF-κβ Y AP-1
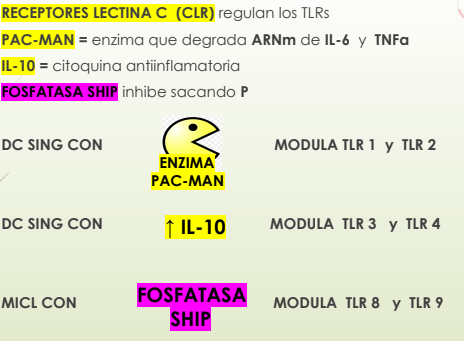
RECEPTORES CLRs DC-SING
Características:
Algunos CLR son moduladores activando o inhibiendo a los TLR
Patógenos pueden activar ambos receptores TLR Y CLR
DC-SING: con una enzima que destruye ARNm regula los TLR1 Y TLR2 (ARNm es destruido x la enzima)
TLR 1 y TLR2⏩ ➕factores de transcripción para producir IL6 y TNFα
IL 10 modula TLR3 y TLR4
MICL:
CLR de los macrófagos necesita Ca
Inhibidor recluta FOSFATASA SHIP que saca P (desactiva el trabajo de la quinasa)
CON FOSFATASA modula los TLR8 Y TLR9
MINCLE: similar a DECTIN 2
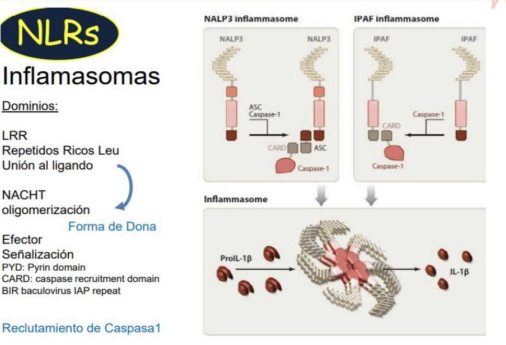
RECEPTORES INTRACELULARES NOD O NLR
Citoplasmaticos son los NOD Y LOS RIG
NOD (NLR) tiene dominio RRL rico en leucinas (aminoácidos)
están en citosol son solubles, reconocen:
Proteínas
Toxinas bacterianas
ADN doble cadena
FLAGELINA
También derivadas de daño ATP RADIACIONES UV
Tienen un–DOMINIO NATCH QUE SE OLIGOMERIZA y forma INFLAMOSOMA
Con proteina CARD: activan caspasas que clivan PRO-IL1β e PRO-IL18, al cortarlas liberan IL1 e IL18
Inflamasoma además del ligando necesita ↑ EFLUJO DE K Y ENTRADA DE Ca ↑ de RADICALES LIBRES (especies reactivas de O) y ATP
RECEPTORES RIG RLR
Son citoplasmaticos tienen :
1)RD= dominio de reconocimiento al ligando ARN doble cadena viral
2)Su proteina adaptadora es MAVS de la membrana mitocondrial
3)Dominio CARD como el inflamasoma reclutan caspasas y cortan como un NOD NECESITA ATP para actuar
RIG reconoce ARN VIRAL y activa dominio CARD (igual al del inflamasoma) y activa factores de transcripcion IRF3 e IRF7 que producen IFN 1 IL6 e TNFα
RECEPTORES CGAS-STING intracelular
1) Reconoce ADN de patogenos se une al ADN VIRAL (ligando)
2) Modifica ATP DANDO cGAMP (que es GMP Y AMP ciclico)
3) cGAMP + STING del reticulo endoplasmico (proteina adaptadora)
reclutan proteinas que activan: IRF3 que da IFN 1.