Forensische biologie II
5.0(1)
Studied by 3 peopleCard Sorting
1/143
Earn XP
Description and Tags
HvA, Forensisch Onderzoek, Jaar 2 blok 4
Last updated 2:09 PM on 6/21/23
Name | Mastery | Learn | Test | Matching | Spaced | Call with Kai |
|---|
No analytics yet
Send a link to your students to track their progress
144 Terms
1
New cards
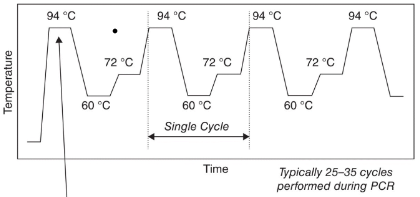
Polymerase Chain Reaction (PCR)
Enzymatisch proces waarbij een specifieke sequentie op het DNA geïsoleerd en geamplificeerd wordt. De ‘normale’ variant bestaat uit 3 dingen:
1. **Denaturatie** (94-97℃): separatie van de DNA-helix in 2 aparte strengen.
2. **Annealing** (50-60℃): binding van de primers aan het DNA aan het 5’ einde.
3. **Extensie** (70-72℃): Taq-polymerase bouw nucleotiden in bij de target fvanaf de primer.
Deze cyclus wordt 25-35 keer herhaald
1. **Denaturatie** (94-97℃): separatie van de DNA-helix in 2 aparte strengen.
2. **Annealing** (50-60℃): binding van de primers aan het DNA aan het 5’ einde.
3. **Extensie** (70-72℃): Taq-polymerase bouw nucleotiden in bij de target fvanaf de primer.
Deze cyclus wordt 25-35 keer herhaald
2
New cards
Primers
Korte sequenties (18-24) enkelstrengs DNA die binden aan naastgelegen vastgestelde sequenties van de targetsequentie op een complementair stuk ten opzichte van hun eigen sequentie. Ze worden gebruikt in PCR-reacties en zijn vaak gelabeld met fluorescerende dyes. Ze moeten specifiek zijn, mogen geen interne secundaire structuren hebben en mogen geen herhalende stukken hebben. Bij een multiplex moet erop gelet worden dat primers niet binden aan elkaar (=primer dimers)
3
New cards
Bleed through/pull up
Wanneer de kleuren van de fluorescerende dyes in elkaar overlopen waardoor ze niet goed/fout geïnterpreteerd worden
4
New cards
Gelelektroforese/capillaire elektroforese
Scheidingsmethode waarbij de PCR-producten (amplicons) gescheiden worden op lengte. Dit gebeurt alleen bij een multiplex-PCR of bij het sequencen
5
New cards
Multiplex-PCR
Type PCR waarbij er meerdere, verschillende sequenties tegelijkertijd worden geamplificeerd met elk hun eigen primers. Het wordt oa gebruikt om een DNA-profiel te maken
6
New cards
Stotterpiek
Een artefact in het DNA-profiel waarbij er een kleiner piekje net voor of na de echte piek zit. Het ontstaat omdat taq-polymerase tijdens het inbouwen ‘slipt’.
7
New cards
qPCR/Real-time PCR
Type PCR waarbij het target DNA zowel gekwantificeerd als geamplficeerd wordt. Er wordt dan live meegekeken naar de DNA-concentratie bij elke cyclus tijdens de __**exponentiële**__ amplificatie (alles is dan nog in overvloed aanwezig). Hiervoor worden fluorescerende dyes (zoals SYBR Green) of Taqman probes gebruikt waarbij de fluorescentie tegen het cyclusnummer wordt uitgezet. De fluorescentie neemt toe bij de amplificatie van het DNA en is dus een maat voor de concentratie. Een cyclus bestaat uit:
1. **Denaturatie** (95℃)
2. **Annealing** (afhankelijk van Tm van de primer)
3. **Extensie** (70-72℃)
1. **Denaturatie** (95℃)
2. **Annealing** (afhankelijk van Tm van de primer)
3. **Extensie** (70-72℃)
8
New cards
Fluorescerende dyes
Dyes die aan het dsDNA binden en dan een fluorescerend signaal uitzenden. Omdat ze binden aan al het dsDNA, zijn ze niet specifiek voor de target sequentie. Er kan wel een melt-curve van gemaakt worden.
9
New cards
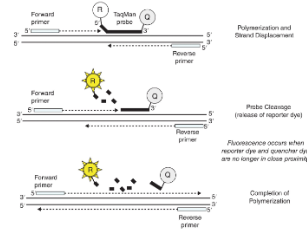
Taqman probes/Taqman assay
Een oligonucleotide probe bindt aan een specifiek stuk aan het DNA tussen de forward en reverse primer in. De probes bestaan uit een reporter dye op het 5’ einde (met hoge energie) en quencher dye op het 3’ einde (lagere energie). De reporter kan in nabijheid van de quencher geen signaal uitstralen omdat de quencher de uitgestraalde energie opneemt. Tijdens de PCR-reactie bouwt taq-polymerase de nucleotiden in, en omdat de probe in de weg zit wordt deze doorgeknipt. Hierdoor zitten de dyes niet meer bij elkaar in de buurt en kan de reporter dye het fluorescerende signaal uitstralen.
Het is specifiek omdat er speciale primers voor gemaakt worden en het is ook erg sensitief. Er kan alleen geen melt-curve van gemaakt worden omdat het doorknippen van de assay geen omkeerbare reactie is en de fluorescentie dan dus niet geremd kan worden.
Het is specifiek omdat er speciale primers voor gemaakt worden en het is ook erg sensitief. Er kan alleen geen melt-curve van gemaakt worden omdat het doorknippen van de assay geen omkeerbare reactie is en de fluorescentie dan dus niet geremd kan worden.
10
New cards
Pyrosequencing
Sequentiemethode door middel van de productie van licht. De methode is snel, accuraat, kwantitatief en makkelijk te automatiseren. Echter kan het alleen gebruikt worden om korte sequenties te analyseren.Het proces is als volgt:
1. Sequencing primer bindt aan het ssDNA
2. Incubatie met DNA-polymerase + ATP sulphurylase + luciferase (= een chemiluminescent) + apyrase + adenosine 5’ fosfosulfaat + luciferin
3. Toevoegen van 1 van de 4 basen (A,C,T of G)
4. Bij een match met een base wordt een reactie geïnitieerd: binding van base aan ssDNA → verlies van trifosfaat als PPi
5. ATP sulphurylase combineert PPi met adenosine 5’ fosfosulfaat →Vorming van ATP
6. Luciferase gebruikt ATP voor afbraak van luciferin
7. Uitstraling van energie in de vorm van licht
8. Detectie + analyse
9. Toevoegen van een andere base
10. Stappen 4 t/m 8 worden herhaald
Het is kwantitatief omdat de lichthoeveelheid gerelateerd kan worden aan de hoeveelheid gebonden basen in het template.
1. Sequencing primer bindt aan het ssDNA
2. Incubatie met DNA-polymerase + ATP sulphurylase + luciferase (= een chemiluminescent) + apyrase + adenosine 5’ fosfosulfaat + luciferin
3. Toevoegen van 1 van de 4 basen (A,C,T of G)
4. Bij een match met een base wordt een reactie geïnitieerd: binding van base aan ssDNA → verlies van trifosfaat als PPi
5. ATP sulphurylase combineert PPi met adenosine 5’ fosfosulfaat →Vorming van ATP
6. Luciferase gebruikt ATP voor afbraak van luciferin
7. Uitstraling van energie in de vorm van licht
8. Detectie + analyse
9. Toevoegen van een andere base
10. Stappen 4 t/m 8 worden herhaald
Het is kwantitatief omdat de lichthoeveelheid gerelateerd kan worden aan de hoeveelheid gebonden basen in het template.
11
New cards
Next Generation Sequencing (NGS)
Sequentiemethode waarbij meerdere, verschillende DNA-sequenties parallel aan elkaar geanalyseerd worden. Het kan gebruikt worden voor zowel STR’s als SNP’s. Het is snel en goedkoop
12
New cards
Fourth Generation Sequencing (FGS)
Sequentiemethode dat de opvolger is van Next Generation Sequencing (NGS). Het bestaat uit 2 kamers met een nanopore membraan ertussen. Door een elektrisch stroompje wordt het sample van de ene kamer naar de andere geleidt. Door het passeren van het membraan komt er een verandering in de frequentie, duur en amplitude van het stroompje. Elke base zorgt voor een andere verandering. Het grootste voordeel is dat er vooraf geen PCR nodig is. Het grootste nadeel is de betrouwbaarheid omdat de moleculen snel door het membraan gaan.
13
New cards
Identificatie van soorten
Meestal wordt hier mitochondriaal DNA (mtDNA) voor gebruikt. Er wordt dan gekeken naar het CO1-gen, cytochrome *b*, 12S rRNA, 16S rRNA of de D-loop, afhankelijk van de gewervelde soort
14
New cards
Stappenplan voor soortidentificatie
1. DNA-isolatie
2. DNA-amplificatie
3. Sequencen van het DNA
4. Vergelijken met een database
Meestal wordt er mtDNA gebruikt, mede omdat de databases daarvoor het uitgebreidst zijn.
15
New cards
Intraspecies variatie
Variatie **binnen** 1 soort
16
New cards
Interspecies variatie
Variatie tussen soorten
17
New cards
Haplotype
De combinatie van allelen zoals die voorkomen op een uniek chromosoom. Er kan hier binnen een soort verschillen in zitten, waardoor ze soms gezien kunnen worden als 2 verschillende soorten terwijl dit niet zo is. Het is dus belangrijk om meerdere van deze combinaties in een database van een soort toe te voegen
18
New cards
Nunts
Translocaties van het mtDNA in het nucleaire DNA. Hierdoor kan er misidentificatie van een soort voorkomen
19
New cards
Bushmeat
Het vlees van dieren die normaal **niet** gezien worden als ‘game animals’. De jacht hierop is niet gereguleerd, wat kan leiden tot extinctie van een soort. Diverse invloeden hebben invloed op de jacht:
\- Toename van de populatie → meer mensen om te voeden
\- Economische en sociale factoren waardoor mensen van het dorp naar de stad verhuizen → voor ‘nostalgie’ eten ze dit vlees
\- Internet & telefoon → handelaren en kopers komen makkelijker in contact
\- Betere infrastructuur en vliegtuigen
\- Corruptie in arme landen en tekort aan spullen en prioriteiten in de rijkere landen → weinig moeite om de handel te bestrijden
\- Toename van de populatie → meer mensen om te voeden
\- Economische en sociale factoren waardoor mensen van het dorp naar de stad verhuizen → voor ‘nostalgie’ eten ze dit vlees
\- Internet & telefoon → handelaren en kopers komen makkelijker in contact
\- Betere infrastructuur en vliegtuigen
\- Corruptie in arme landen en tekort aan spullen en prioriteiten in de rijkere landen → weinig moeite om de handel te bestrijden
20
New cards
Identificatie van een individu
Hiervoor worden nucleaire STR’s gebruikt. Indien hier niet genoeg van is kan in sommige gevallen ook de D-loop gebruikt worden in het mtDNA
21
New cards
Mermaid ivory
De botten van de Steller’s zeekoe (een uitgestorven diersoort). Om deze te identificeren wordt er gebruikgemaakt van het stappenplan voor soortidentificatie, waarbij er gebruikgemaakt wordt van specifieke primers.
22
New cards
Mitochondriën
Organel in het cytoplasma van een cel dat zijn eigen energie genereert en zijn eigen DNA (zo’n 4-5 kopieën per organel), RNA en transcriptie- en translatiesysteem heeft. Het wordt meestal eenouderlijk doorgegeven waardoor er geen recombinatie ontstaat. Het DNA kan gebruikt worden bij (zeer) gedegradeerde samples of wanneer nucleair DNA niet voldoende resultaat oplevert. Het wordt toegepast in de forensic wildlife analysis
23
New cards
Mitochondriaal DNA (mtDNA)
dsDNA dat bestaat uit 37 genen:
\- 22 tRNA genen
\- 2 rRNA genen: 12S en 16S
\- 13 eiwitten, waaronder het **cytochrome** ***b***, **cytochrome oxidase I**, II en III en ND’s → cyt b en CO1 worden gebruikt bij de soortidentificatie
De buitenste ring is de H-streng (=Heavy). De binnenste is de L-string (=Light). De totale lengte is gemiddeld 16,569 bp maar dit kan tussen soorten verschillen. Het is bijna geheel coderend, muv de D-loop (=oorsprong van replicatie) dat intraspecies variatie bevat omdat er geen selectiedruk is waardoor mutaties ‘vrij’ kunnen optreden.
De grootste __voordelen__ zijn:
\- Snellere evolutie dan nucleair DNA door de grotere hoeveelheid mutaties en de afwezigheid van een error-reading enzym
\- Er zit meer in een cel dan nucleair DNA (dus grotere slagingskans als er maar weinig celmateriaal is)
\- Kan gebruikt worden bij gedegradeerd DNA
\- Grotere discriminerende waarde bij heteroplasmie
\
De grootste __nadelen__ zijn:
\- Minder discriminerend dan STR’s en bij individuen die via de moederlijke lijn verwant zijn omdat er geen recombinatie plaatsvindt
\- Heteroplasmie kan de interpretatie vermoeilijken
\- 22 tRNA genen
\- 2 rRNA genen: 12S en 16S
\- 13 eiwitten, waaronder het **cytochrome** ***b***, **cytochrome oxidase I**, II en III en ND’s → cyt b en CO1 worden gebruikt bij de soortidentificatie
De buitenste ring is de H-streng (=Heavy). De binnenste is de L-string (=Light). De totale lengte is gemiddeld 16,569 bp maar dit kan tussen soorten verschillen. Het is bijna geheel coderend, muv de D-loop (=oorsprong van replicatie) dat intraspecies variatie bevat omdat er geen selectiedruk is waardoor mutaties ‘vrij’ kunnen optreden.
De grootste __voordelen__ zijn:
\- Snellere evolutie dan nucleair DNA door de grotere hoeveelheid mutaties en de afwezigheid van een error-reading enzym
\- Er zit meer in een cel dan nucleair DNA (dus grotere slagingskans als er maar weinig celmateriaal is)
\- Kan gebruikt worden bij gedegradeerd DNA
\- Grotere discriminerende waarde bij heteroplasmie
\
De grootste __nadelen__ zijn:
\- Minder discriminerend dan STR’s en bij individuen die via de moederlijke lijn verwant zijn omdat er geen recombinatie plaatsvindt
\- Heteroplasmie kan de interpretatie vermoeilijken
24
New cards
Polymorfisme
Een mutatie dat bij meer dan 0,1% van de populatie aanwezig is
25
New cards
Single Nucleotide Polymorphism (SNP)
Een mutatie in 1 nucleotide dat voorkomt in meer dan 0,1% van de populatie
26
New cards
Pyrimidines
Aromatische ring met 2 stikstofatomen: Cytosine en Thymine in DNA en Uracil in het RNA
27
New cards
Purines
Aromatische ring met 3 stikstofatomen: Guanine en Adenine
28
New cards
Error-reading enzymen
Enzymen die na het inbouwen van de nucleotiden door DNA-polymerase checken of er geen verkeerde basen zijn ingebouwd. Indien dit wel zo is worden deze eruit gehaald en worden de juiste basen erin gebouwd. Hierdoor worden mutaties voorkomen.
29
New cards
Heteroplasmie
Het voorkomen van verschillende DNA-sequenties binnen 1 cel. Dit komt voornamelijk voor omdat er meerdere mitochondriën zijn in 1 cel en deze allemaal geen error-reading enzymen hebben waardoor mutaties sneller optreden. Dit kan verwarrend zijn in de interpretatie, maar wordt ook gebruikt om iemand te kunnen individualiseren met een grotere bewijskracht.
30
New cards
Neutrale selectie
Selectie dat geen invloed heeft op het fenotype. Het komt dan ook voor in niet-coderende delen van het DNA
31
New cards
Selectiedruk voor mutaties
Deze druk is er omdat er door een mutatie een ander eiwit geproduceerd kan worden. Dit kan leiden tot een ongewenst resultaat, zoals het niet goed kunnen uitvoeren van de celfunctie, waardoor de cel afsterft. De mutatie sterft dan ook uit.
32
New cards
Criteria voor soortidentificatie
Er zijn 2 criteria:
1. Veel interspecies variatie → veel variatie tussen diverse soorten
2. Weinig intraspecies variatie → weinig verschil binnen dezelfde soort
1. Veel interspecies variatie → veel variatie tussen diverse soorten
2. Weinig intraspecies variatie → weinig verschil binnen dezelfde soort
33
New cards
Cytochroom b
Eiwit dat deel is van de elektronentransportketen in het binnenste mitochondriale membraan
34
New cards
CO1
Dit subunit is het laatste eiwit in de transportketen. Het wordt gecodeerd in het mtDNA en wordt gebruikt als universele regio voor soortidentificatie van voornamelijk dieren en protisten
35
New cards
rbcL en/of matK
Markers die gebruikt worden voor de soortidentificatie van planten
36
New cards
Barcoding
Het sequencen van een DNA-sequentie van een (onbekende) soort met (meestal) universele primers. Het is een ander woord voor ‘sequencing’. Vervolgens wordt het vergeleken met een database. Belangrijk is wel dat deze database genoeg uitgebreid is.
Het wordt meestal gedaan met korte DNA-sequenties (voor DNA 150-650 en voor mini 100-150). Nooit minder dan 100 bp omdat er dan niet voldoende intraspecies variatie is.
Het wordt meestal gedaan met korte DNA-sequenties (voor DNA 150-650 en voor mini 100-150). Nooit minder dan 100 bp omdat er dan niet voldoende intraspecies variatie is.
37
New cards
Allopatrische soortvorming
Door geografische is een populatie opgesplitst in meerdere populaties waardoor er genetische isolatie is ontstaan omdat ze onderling niet konden reproduceren. Hierdoor zijn ze opgesplitst in meerdere (sub)soorten
38
New cards
Taxonomie
De indeling en ordening van soorten. 2 leden van dezelfde soort delen het meest van hun DNA. Hoe hoger de groep, hoe minder match en hoe meer genetische variatie
39
New cards
Soort
Dit kan op 2 manieren gedefinieerd worden:
1. __Biologisch__: dit is op basis van morfologische eigenschappen → taxonomie indeling en de wet zijn hierop gebaseerd. Dit gaat er vanuit dat 1 soort niet kan reproduceren met een andere soort en levensvatbare jongen kan krijgen
2. __Fylogenetisch__: relatie tussen organismen door hun evolutionaire geschiedenis, waarbij gekeken wordt naar genetische markers van DNA, RNA en eiwitten → forensische soorten onderzoek is hierop gebaseerd.
Soms komen ze op dezelfde indeling uit. Er wordt aangeraden om een combi van beide te gebruiken
1. __Biologisch__: dit is op basis van morfologische eigenschappen → taxonomie indeling en de wet zijn hierop gebaseerd. Dit gaat er vanuit dat 1 soort niet kan reproduceren met een andere soort en levensvatbare jongen kan krijgen
2. __Fylogenetisch__: relatie tussen organismen door hun evolutionaire geschiedenis, waarbij gekeken wordt naar genetische markers van DNA, RNA en eiwitten → forensische soorten onderzoek is hierop gebaseerd.
Soms komen ze op dezelfde indeling uit. Er wordt aangeraden om een combi van beide te gebruiken
40
New cards
Convention on International Trade in Endangered Species of wild fauna and flora (CITES)
Bevat lijsten in 3 gradaties waarop beschermde diersoorten staan:
I. Dieren-/plantensoorten die het meest kwetsbaar zijn (bijna extinct). Ze hebben de meeste bescherming nodig en er mag niet commercieel in gehandeld worden (alleen onder speciale omstandigheden).
II. De populatie van de dieren/planten is verkleind tot op het punt dat ze een serieus probleem hebben. Er mag gelimiteerde handel plaatsvinden, maar met strikte regulatie.
III. Dieren-/plantenpopulaties die een specifiek verzoek hebben gekregen van een bepaald land waarvan zij zeggen dat de handel gereguleerd moet worden
I. Dieren-/plantensoorten die het meest kwetsbaar zijn (bijna extinct). Ze hebben de meeste bescherming nodig en er mag niet commercieel in gehandeld worden (alleen onder speciale omstandigheden).
II. De populatie van de dieren/planten is verkleind tot op het punt dat ze een serieus probleem hebben. Er mag gelimiteerde handel plaatsvinden, maar met strikte regulatie.
III. Dieren-/plantenpopulaties die een specifiek verzoek hebben gekregen van een bepaald land waarvan zij zeggen dat de handel gereguleerd moet worden
41
New cards
Universele primers
Primers die worden gedesigned op basis van actieve gebieden van coderende eiwitten omdat deze niet kunnen veranderen en hetzelfde zijn bij veel soorten.
42
New cards
12S en 16S rRNA
Genen die gebruikt worden in het translatieproces van nucleotidesequentie tot eiwit. Ze combineren 2 subunits met daartussen mRNA om de binding tussen 2 aminozuren te katalyseren. Er zit veel selectiedruk op
43
New cards
matK, rcbL (en tRNA-complexen) op het chloroplast genoom
Genen die gebruikt worden voor de identificatie van groene planten
44
New cards
ND2-gen
Gen dat gebruikt wordt voor de soortidentificatie van vogels
45
New cards
Sanger Sequencing
Bij deze sequentiemethode zijn de volgende stoffen aanwezig:
\- 1 Template DNA (de forward read)
\- 1 primer
\- Taq-polymerase
\- Mix van dNTP’s en ddNTP’s
Deze worden gebruikt in een speciale PCR waarbij de ketenextensie stopt als er een ddNTP ingebouwd wordt. Hierdoor ontstaan fragmenten van verschillende lengtes, welk gescheiden kunnen worden adhv gelelektroforese of capillaire elektroforese.
De methode kan gebruikt worden voor het aflezen van \~800 nucleotiden en is ook wel de *First Generation Sequencing*
\- 1 Template DNA (de forward read)
\- 1 primer
\- Taq-polymerase
\- Mix van dNTP’s en ddNTP’s
Deze worden gebruikt in een speciale PCR waarbij de ketenextensie stopt als er een ddNTP ingebouwd wordt. Hierdoor ontstaan fragmenten van verschillende lengtes, welk gescheiden kunnen worden adhv gelelektroforese of capillaire elektroforese.
De methode kan gebruikt worden voor het aflezen van \~800 nucleotiden en is ook wel de *First Generation Sequencing*
46
New cards
ddNTP’s (didesoxynucleotiden)
Moleculen die op normale moleculen lijken, maar geen OH-groep hebben aan het 3’ uiteinde. Hierdoor kunnen er na het binden geen nieuwe nucleotiden aan gebonden worden, waardoor de ketenextensie stopt. Ze worden gebruikt in diverse sequentiemethoden, zoals het Sanger-Sequencing
47
New cards
BLAST
Een programma waarin een verkregen sequentie vergeleken kan worden met diverse databases
48
New cards
e-value (expectation value)
Statistische waarde voor de kans dat een match is veroorzaakt door random kans. Hoe kleiner de waarde, hoe kleiner de kans dat het een random match is en hoe significanter de match dus wordt.
49
New cards
RT-PCR (Reverse Transcription Polymerase Chain Reaction)
Type PCR waarbij het monster RNA bevat. Hierbij wordt het RNA eerst omgezet naar cDNA dmv het enzym reverse transcriptase
50
New cards
Hot start
Een functie in de PCR die gestart kan wordt voordat de cycli beginnen. Taq-polymerase is bij lage temperaturen een beetje actief. Om dit te voorkomen wordt er een enzym toegevoegd zodat taq-polymerase nog niet actief is tijdens het opstarten van de reactie en de denaturatiestap.
51
New cards
dNTP’s
Nucleotiden die een deoxyribose en 3 fosfaatgroepen hebben. Hieraan kunnen weer andere basen ingebouwd worden. Bij de binding wordt er 1 fosfaatgroep afgesplitst
52
New cards
Magnesium
Dient als co-factor voor Taq-polymerase zodat het kan binden aan ssDNA tijdens de PCR. Ook stabiliseert het het dsDNA en het primer-template complex.
53
New cards
PCR-efficiëntie
De ratio tussen de hoeveelheid amplicons aan het einde van de reactie en de hoeveelheid target moleculen aan de start van de reactie. Indien het 100% is, is de hoeveelheid DNA steeds perfect verdubbeld bij elke cyclus. Het moet tussen de 90-110% voor een goed onderzoek. Het hangt af van de lengte, secundaire structuren, concentraties van de reagentia, kwaliteit van de enzymen etc.
54
New cards
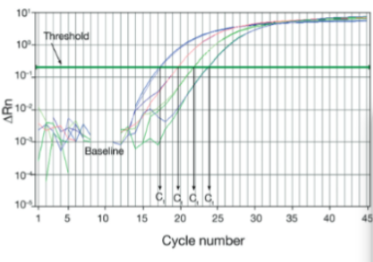
Baseline
Het signaalniveau waarbij er weinig verandering in de fluorescentie zit. Het is gelijk aan de ruis van de reactie. Dit wordt per reactie empirisch bepaald en op basis hiervan kan de **Ct (treshhold cyclus**) bepaald worden.
55
New cards
Threshold
Het niveau van het signaal dat een statistisch significante vermenigvuldiging heeft tov het baseline signaal. Hierbij wordt het signaal van het amplicom gescheiden van de ruis. Dit is vaak 10x de SD (standaard deviatie) en ligt (meestal) in het exponentiële gedeelte.
56
New cards
Threshold cyclus (Ct)
Het cyclusnummer waarbij het fluorescerende signaal van de reactie de threshold passeert. Het is omgekeerd evenredig met de startconcentratie aan DNA: bij een dubbele starthoeveelheid tov van een ander sample wordt de Ct met 1 cyclus eerder bereikt. Dit kan logaritmisch in een grafiek worden weergegeven.
57
New cards
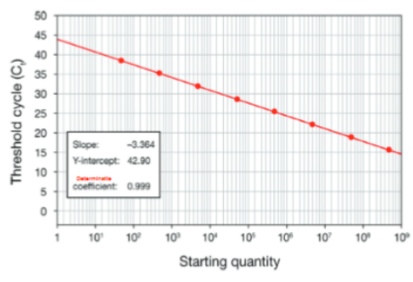
Verdunningsreeks (standaardscurve)
Dit kan gebruikt worden om de starthoeveelheid template of om de efficiëntie van de qPCR te bepalen. Het wordt weergegeven als logaritmische functie waarbij de concentratie (x-as) wordt uitgezet tegen de Ct waarde voor die concentratie (y-as). Op basis hiervan kan info over de helling, y-intercept en determinatiecoëfficiënt verkregen worden. Er kan wel geinterproleerd worden, maar niet extrapoleerd worden!
58
New cards
Y-intercept
Deel van de verdunningsreeks dat iets zegt over het theoretische detectielimiet, ofwel de verwachte Ct-waarde bij de laagste kopie aantal waarbij het signaal van het target molecuul boven de ruis uitkomt. Hierdoor kunnen verschillende systemen en targets met elkaar vergeleken worden
59
New cards
Helling (slope) van de verdunningsreeks
Dit zegt iets over de efficiëntie van de reactie. Als het gelijk is aan -3.32 is er 100% efficiëntie. Dit kan berekend worden met: Efficiëntie = 10^(-1/slope) -1
60
New cards
Dynamic range
De range waarin de toename van het startmateriaal leidt tot een bijbehorende toename van het amplificatieproduct
61
New cards
Absolute kwantificatie
Hierbij wordt er een verdunningsreeks met bekende concentraties gemaakt om een standaard curve te produceren. Samples met onbekende concentraties kunnen hiermee gekwantificeerd worden.
62
New cards
Relatieve kwantificatie
De expressie van een gen wordt uitgezet tegen de expressie van hetzelfde gen in een ander sample.
63
New cards
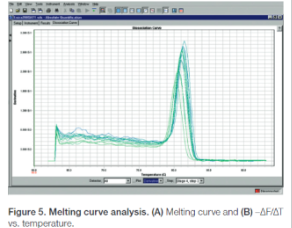
Melting cuve (dissociation curve)
Dit laat de verandering van het fluorescerende signaal zien wanneer dsDNA met daaraan dyes denatureert in ssDNA. De dyes laten dan los, wat voor een vermindering van het signaal zorgt. In de curve is (het verschil in) de fluorescentie (y-as) uitgezet tegen de temperatuur (x-as). Er kan dan gecheckt worden voor primer-dimers en de specificiteit van de reactie: bij 1 dunne, symmetrische piek zonder schouders is de reactie specifiek, omdat andere stoffen op een andere manier fluoresceren en een tweede piek zouden geven. Voor dit onderzoek is er een excitatiebron en detector nodig.
Belangrijk: alleen dyes die binden aan dsDNA kunnen gebruikt worden, en Taq-man probes kunnen dit niet!
Belangrijk: alleen dyes die binden aan dsDNA kunnen gebruikt worden, en Taq-man probes kunnen dit niet!
64
New cards
Fluorescence Resonance Energy Transfer (FRET)
De emissie van een fluorescerende dye (**reporter**) wordt verminderd in dichtbije aanwezigheid van een andere dye (**quencher**). Bv: rode en groene fluorescerende dyes. De groene dye heeft een hogere emissie energie (door de kortere golflengte) dan de rode. Wanneer deze geëxciteerd wordt zal de uitgestraalde energie worden opgenomen door de rode dye, waardoor de groene minder/geen licht uitstraalt dat gedetecteerd kan worden. Dit wordt gebruikt in het principe van de **Taqman probe.**
65
New cards
Passive reference dyes
Stoffen die dienen als een interne controle om te corrigeren voor schommelingen in het fluorescentiesignaal die niet PCR gebaseerd zijn
66
New cards
DNA-barcoding
Dit wordt gedaan in 12 stappen:
1. Alle spullen klaarleggen
2. Sample in stukjes snijden
3. Tissue lysis: afbraak van celmembranen en denaturatie van eiwitten dmv lysisbuffer en proteinase K
4. Incubatie
5. DNA-extractie: DNA wordt gebonden aan een kolom en adhv diverse wasbuffers wordt contaminatie weggespoeld. Vervolgens wordt het DNA met een elutiebuffer losgemaakt van de kolom
6. PCR-mastermix maken
7. PCR set-up: sample in epje en de negatieve en positieve controle voorbereiden
8. PCR instellen en runnen
9. Gelelektroforese gel maken
10. Gelelektroforese runnen waarbij de samples met een loading dye aangevuld worden. Ook wordt er een DNA-ladder meegenomen. De samples worden bekeken onder UV-licht
11. Post-PCR clean up: verwijderen van contaminatie (oa primers en dNTP’s)
12. Sequencing en data validatie
1. Alle spullen klaarleggen
2. Sample in stukjes snijden
3. Tissue lysis: afbraak van celmembranen en denaturatie van eiwitten dmv lysisbuffer en proteinase K
4. Incubatie
5. DNA-extractie: DNA wordt gebonden aan een kolom en adhv diverse wasbuffers wordt contaminatie weggespoeld. Vervolgens wordt het DNA met een elutiebuffer losgemaakt van de kolom
6. PCR-mastermix maken
7. PCR set-up: sample in epje en de negatieve en positieve controle voorbereiden
8. PCR instellen en runnen
9. Gelelektroforese gel maken
10. Gelelektroforese runnen waarbij de samples met een loading dye aangevuld worden. Ook wordt er een DNA-ladder meegenomen. De samples worden bekeken onder UV-licht
11. Post-PCR clean up: verwijderen van contaminatie (oa primers en dNTP’s)
12. Sequencing en data validatie
67
New cards
Iron Torrent
Dit is een type NGS waarbij er een halfgeleider chip is waar vele *wells* op de pixels liggen. Deze *wells* bevatten chemische informatie over het sequencen en vertalen dit naar digitale informatie.
Elk DNA-fragment bindt aan een kraal en wordt gekopieerd tot het de totale kraal dekt. Op elke kraal zit een verschillende template, en op deze wijze kunnen meerdere templates tegelijk geamplficeerd worden. Deze kralen vallen in de wells op de chip, die vervolgens gevuld worden met 1 van de 4 nucleotiden. Als deze nucleotide bindt aan het template DNA, komt er een H+ vrij, waardoor de pH in de well verandert. De sensitieve laag onder de well detecteert deze verandering en verandert het naar voltage (digitaal signaal). Elke 15 seconden wordt de well volgestroomd met een andere nucleotide, en op deze manier kan de streng gesequencet worden. Indien er 2 dezelfde opeenvolgende nucleotiden in de target streng zijn, binden er ook 2 nucleotiden uit de well oplossing, en worden er 2 H+ afgezet, wat weer een hoger stroomsignaal oplevert. Dit wordt dan geregistreerd als 2 dezelfde nucleotiden achter elkaar. Omdat dit in elke well gebeurt met diverse templates, wordt het ook wel MPS (Massively Parallel Sequencing) genoemd.
Elk DNA-fragment bindt aan een kraal en wordt gekopieerd tot het de totale kraal dekt. Op elke kraal zit een verschillende template, en op deze wijze kunnen meerdere templates tegelijk geamplficeerd worden. Deze kralen vallen in de wells op de chip, die vervolgens gevuld worden met 1 van de 4 nucleotiden. Als deze nucleotide bindt aan het template DNA, komt er een H+ vrij, waardoor de pH in de well verandert. De sensitieve laag onder de well detecteert deze verandering en verandert het naar voltage (digitaal signaal). Elke 15 seconden wordt de well volgestroomd met een andere nucleotide, en op deze manier kan de streng gesequencet worden. Indien er 2 dezelfde opeenvolgende nucleotiden in de target streng zijn, binden er ook 2 nucleotiden uit de well oplossing, en worden er 2 H+ afgezet, wat weer een hoger stroomsignaal oplevert. Dit wordt dan geregistreerd als 2 dezelfde nucleotiden achter elkaar. Omdat dit in elke well gebeurt met diverse templates, wordt het ook wel MPS (Massively Parallel Sequencing) genoemd.
68
New cards
Illumina sequencing
Dit is een type NGS dat bestaat uit 4 stappen:
1. Sample voorbereiding: binding van adapters aan het uiteinde waar de sequentie bindingsplaatsen weer aan vastbinden.
2. Cluster generatie: DNA-amplificatie in een flow cell. Deze cellen bestaan uit panelen dat bedekt is met 2 typen oligonucleotiden. 1 hiervan zorgt voor de binding tussen het fragment + oppervlak. DNA-polymerase maakt de complementaire streng. Het DNA denatureert hierna weer waardoor de originele streng weggespoeld wordt. De strengen worden gekloond door brug-amplificatie.
3. Sequencing: na binding van elke base wordt het aangestraald met een lichtbron, wat een specifiek signaal produceert. Als bijna de hele streng gesequencet is bindt er een nieuwe primer op het einde van de forward streng en worden de laatste nucleotiden ingebouwd. Deze worden weggewassen en worden er vanaf het andere uiteinde nucleotiden in gebouwd. De forward streng wordt weggewassen en de reverse streng wordt op dezelfde wijze gesequencet.
4. Data-analyse: forward + reverse sequences worden gepaard door vorming van aangrenzende sequences
1. Sample voorbereiding: binding van adapters aan het uiteinde waar de sequentie bindingsplaatsen weer aan vastbinden.
2. Cluster generatie: DNA-amplificatie in een flow cell. Deze cellen bestaan uit panelen dat bedekt is met 2 typen oligonucleotiden. 1 hiervan zorgt voor de binding tussen het fragment + oppervlak. DNA-polymerase maakt de complementaire streng. Het DNA denatureert hierna weer waardoor de originele streng weggespoeld wordt. De strengen worden gekloond door brug-amplificatie.
3. Sequencing: na binding van elke base wordt het aangestraald met een lichtbron, wat een specifiek signaal produceert. Als bijna de hele streng gesequencet is bindt er een nieuwe primer op het einde van de forward streng en worden de laatste nucleotiden ingebouwd. Deze worden weggewassen en worden er vanaf het andere uiteinde nucleotiden in gebouwd. De forward streng wordt weggewassen en de reverse streng wordt op dezelfde wijze gesequencet.
4. Data-analyse: forward + reverse sequences worden gepaard door vorming van aangrenzende sequences
69
New cards
Traditionele Chinese Medicijnen (TCM)
Medicijnen op basis van ‘natuurlijke’ stoffen die afkomstig zijn uit China. Hierin worden vaak bedreigde soorten (op CITES lijsten) of giftige stoffen verwerkt. Ook wordt er vaak gelogen op de verpakking. Door de inhoud te sequencen kan achterhaald worden welke soorten erin verwerkt zitten om te kijken of het illegaal/gevaarlijk is.
70
New cards
Autosomale STR’s
STR’s in het nucleaire DNA.
\- Voordelen: kleine hoeveelheid nodig, klein beetje degradatie is geen probleem en grote discriminerende waarde.
\- Nadelen: discriminerende waarde wordt zeer verlaagd bij (zeer) gedegradeerd DNA
\- Voordelen: kleine hoeveelheid nodig, klein beetje degradatie is geen probleem en grote discriminerende waarde.
\- Nadelen: discriminerende waarde wordt zeer verlaagd bij (zeer) gedegradeerd DNA
71
New cards
Autosomale SNP’s
SNP’s in het nucleaire DNA.
\- Voordelen: er is maar een hele kleine hoeveelheid nodig, kan discriminerend zijn en gebruikt worden bij erg gedegradeerd DNA, afkomst onderzoek is mogelijk en ze zijn stabieler dan STR’s.
\- Nadelen: lagere discriminatiewaarde tov STR’s en kan niet gebruikt worden bij mengprofielen (behalve het als gaat om een man en vrouw). Er zijn namelijk maar 4 mogelijkheden (mutaties in A,C,T of G) en ze hebben een lagere mutatiesnelheid
\- Voordelen: er is maar een hele kleine hoeveelheid nodig, kan discriminerend zijn en gebruikt worden bij erg gedegradeerd DNA, afkomst onderzoek is mogelijk en ze zijn stabieler dan STR’s.
\- Nadelen: lagere discriminatiewaarde tov STR’s en kan niet gebruikt worden bij mengprofielen (behalve het als gaat om een man en vrouw). Er zijn namelijk maar 4 mogelijkheden (mutaties in A,C,T of G) en ze hebben een lagere mutatiesnelheid
72
New cards
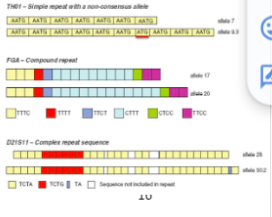
Short Tandem Repeats (STR’s)
Korte lengten (
73
New cards
Primer Binding Site Mutation (PBSM)
Een mutatie op het DNA waardoor de primer slecht/niet goed kan binden aan een specifieke locus, waardoor de marker slecht/niet geamplficeerd wordt en ontbreekt in het DNA-profiel
74
New cards
Y-STR’s
Dit wordt voornamelijk gebruikt om onderscheid te kunnen maken tussen mannelijk en vrouwelijk DNA. Het kan ook gebruikt worden om mannelijke **families** van elkaar te onderscheiden, wat gebruikt wordt voor vaderschapstesten en verwantschapsonderzoek. Het kan geen individuen identificeren (wel uitsluiten) en is daardoor minder discriminerend dan autosomale STR-markers.
75
New cards
D-loop
Hypervariabele gedeelte van het mtDNA van \~1100 bp door de hoge mutatiegraad en de afwezigheid van het reparatie mechanisme/error-reading enzymen. Het bestaat uit 2 delen: HV1 en HV2
76
New cards
Messenger RNA (mRNA)
Dit bevat de info van een gen op het DNA die nodig is om een specifiek eiwit te maken. Het draagt deze info naar het ribosomale RNA (rRNA).
77
New cards
Ribosomaal RNA (rRNA)
Dit zit in de ribosomen in het cytoplasma. Tijdens translatie bindt het aan het transfer RNA (tRNA), waardoor de formatie van peptidebindingen tussen aminozuren gekatalyseerd wordt. Hierdoor worden de eiwitten gemaakt.
78
New cards
Transfer RNA (tRNA)
Dit vervoert specifieke aminozuren naar het rRNA tijdens de eiwitsynthese. Het plaatst ze in de correctie oriëntatie op het mRNA.
79
New cards
MicroRNA (miRNA)
Dit zijn kleine moleculen van \~22 bp die niet-coderend zijn en worden geproduceerd door de intronen in het DNA in de celkern. Dit gebeurt in 2 stappen:
1. Door het eiwit drogo wordt er in de celkern pre-miRNA geproduceerd
2. Door het eiwit dicer wordt er in het cytoplasma miRNA geproduceerd
Hun functie is om het **mRNA uit te schakelen** en om de **genexpressie te reguleren** nadat transcriptie plaats heeft gevonden. Dit gebeurt doordat AGO eiwitten binden aan miRNA, waarbij er een RISC (RNA-Induced Silencing Complex) gevormd wordt. Dit zoekt naar complementaire stukjes op het mRNA, en binden hieraan. Hierdoor wordt het mRNA gedegradeerd of kan het niet goed afgelezen worden, waardoor het eiwit waarvoor het mRNA codeerde niet geproduceerd kan worden. Hierdoor wordt de productie van specifieke eiwitten gereduceerd of gestopt.
1. Door het eiwit drogo wordt er in de celkern pre-miRNA geproduceerd
2. Door het eiwit dicer wordt er in het cytoplasma miRNA geproduceerd
Hun functie is om het **mRNA uit te schakelen** en om de **genexpressie te reguleren** nadat transcriptie plaats heeft gevonden. Dit gebeurt doordat AGO eiwitten binden aan miRNA, waarbij er een RISC (RNA-Induced Silencing Complex) gevormd wordt. Dit zoekt naar complementaire stukjes op het mRNA, en binden hieraan. Hierdoor wordt het mRNA gedegradeerd of kan het niet goed afgelezen worden, waardoor het eiwit waarvoor het mRNA codeerde niet geproduceerd kan worden. Hierdoor wordt de productie van specifieke eiwitten gereduceerd of gestopt.
80
New cards
RNA
Molecuul dat chemisch gezien dezelfde eigenschappen heeft als DNA, maar slechts bestaat uit 1 streng en de base Uracil ipv Thymine. Het bestaat uit 4 soorten:
1. mRNA
2. rRNA
3. tRNA
4. miRNA
Het is minder stabiel dan DNA en wordt sneller afgebroken na de dood. mRNA en miRNA zijn celspecifiek en kunnen gebruikt worden om de herkomst van lichaamsvloeistoffen en geslacht te bepalen (forensische indicatoren). Ze zijn celspecifiek omdat elke cel verschillende eiwitten produceert en de mRNA profielen dus anders zijn.
1. mRNA
2. rRNA
3. tRNA
4. miRNA
Het is minder stabiel dan DNA en wordt sneller afgebroken na de dood. mRNA en miRNA zijn celspecifiek en kunnen gebruikt worden om de herkomst van lichaamsvloeistoffen en geslacht te bepalen (forensische indicatoren). Ze zijn celspecifiek omdat elke cel verschillende eiwitten produceert en de mRNA profielen dus anders zijn.
81
New cards
Massively Parallel Sequencing (MPS)
Techniek waarbij verschillende DNA-templates/loci tegelijkertijd (parallel) worden gesequencet. Voorbeelden zijn de Ion Torrent en de Illumina sequencers.
82
New cards
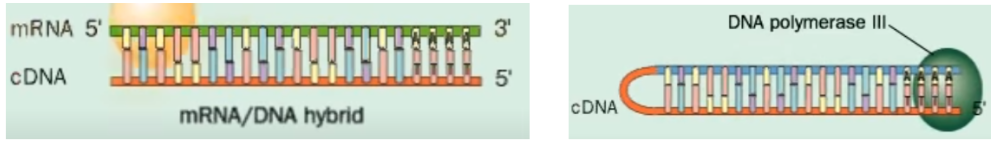
cDNA maken van mRNA
Dit werkt als volgt:
1. Binding van een primer aan de **3’-poly A staart** op het mRNA
2. Inbouwen van complementaire nucleotiden door **reverse transcriptase** → ontstaan van mRNA-DNA hybride molecuul
3. Degradatie van mRNA streng door loog (=OH-)
4. Vorming van hairpin loop aan het vrije 3’-einde van het DNA-molecuul
5. Inbouwen van complementaire nucleotiden aan het DNA-molecuul door **DNA-polymerase III**
6. S1-nuclease knipt de hairpin loop door
7. Eindresultaat: ds-cDNA
1. Binding van een primer aan de **3’-poly A staart** op het mRNA
2. Inbouwen van complementaire nucleotiden door **reverse transcriptase** → ontstaan van mRNA-DNA hybride molecuul
3. Degradatie van mRNA streng door loog (=OH-)
4. Vorming van hairpin loop aan het vrije 3’-einde van het DNA-molecuul
5. Inbouwen van complementaire nucleotiden aan het DNA-molecuul door **DNA-polymerase III**
6. S1-nuclease knipt de hairpin loop door
7. Eindresultaat: ds-cDNA
83
New cards
3’-poly A staart
Dit is een sequentie van adenine (A)- nucleotiden achter elkaar op de 3’ kant van het mRNA-molecuul. Hier bindt de primer aan zodat reverse transcriptase er cDNA van kan maken.
84
New cards
Rapidly Mutating Y-STR’s (RM-Y-STR’s)
STR’s op het Y-chromosoom met een 10-100x hogere mutatiegraad dan ‘normale’ Y-STR’s. Dit komt door een of meer van de volgende kenmerken:
\- Grote hoeveelheid repeats
\- Andere sequentiestructuur
\- __Multi-copy markers__ (verschillende kopieën van hetzelfde STR die in verschillende delen van het Y-chromosoom voorkomt)
Ze zijn hierdoor meer discriminerend en kan er onderscheid gemaakt worden tussen nauwverwante mannen. De beste Y-STR-kit heeft zowel diverse normale Y-STR’s als RM-Y-STR’s. De normale Y-STRs worden geidentificeerd op populatiediversiteit en RM-Y-STR’s op mutatiesnelheden
\- Grote hoeveelheid repeats
\- Andere sequentiestructuur
\- __Multi-copy markers__ (verschillende kopieën van hetzelfde STR die in verschillende delen van het Y-chromosoom voorkomt)
Ze zijn hierdoor meer discriminerend en kan er onderscheid gemaakt worden tussen nauwverwante mannen. De beste Y-STR-kit heeft zowel diverse normale Y-STR’s als RM-Y-STR’s. De normale Y-STRs worden geidentificeerd op populatiediversiteit en RM-Y-STR’s op mutatiesnelheden
85
New cards
Housekeeping marker
Genen die tot expressie komen in alle cellen omdat het nodig is voor het functioneren van de cel. Het dient als positieve controle in onderzoeken naar bepaalde markers.
86
New cards
Mobiele elementen
DNA-sequenties die hun positie in het genoom kunnen veranderen. De meest gebruikte zijn de SINEs (Short INterspersed Elements), met *Alu* als subsoort. Sommige subfamilies zijn polymorfisch en kunnen gebruikt worden voor het bepalen van genetische relaties tussen populaties en verwantschappen
87
New cards
*Alu*-elementen
Mobiele elementen uit de SINE-soort van \~300 bp lang. De meeste zitten echter wel vast op een specifieke locus, voornamelijk in de intronen. Het kan gebruikt worden om de kwantiteit van DNA te bepalen. Ze hebben een high-copy nummer binnen het DNA (1,5 \* 10^6 per persoon)
88
New cards
Degradatie-index (DI)
Dit kan gebruikt worden om de kwantiteit en kwaliteit (mate van degradatie → hoeveelheid amplificeerbare DNA) te bepalen aan de hand van de verhouding tussen een kort (voor kwantiteit) en lang (voor kwaliteit) fragment: (\[kort\]/\[lang\]). Voor het korte fragment wordt meestal een *Alu*-fragment gebruikt, en voor de lange het SVA (YB8). Als het groter is dan 1, dan is er degradatie. Vooral langere fragmenten zijn hier gevoeliger voor.
In de praktijk wordt het gebruikt om vooraf te kijken of een spoor kansrijk is voor een STR-profiel, of dat er andere keuzes gemaakt dienen te worden. Dit scheelt een hoop tijd, geld en sample hoeveelheid.
In de praktijk wordt het gebruikt om vooraf te kijken of een spoor kansrijk is voor een STR-profiel, of dat er andere keuzes gemaakt dienen te worden. Dit scheelt een hoop tijd, geld en sample hoeveelheid.
89
New cards
Pigmentatie
Dit wordt beïnvloed door 120 verschillende genen. Er zit in caucasische mensen veel variatie in de melanocortin 1 receptor (MC1R), dat op het oppervlak van melanocyten zit en de productie van de pigmenten eumelanin (zwart-bruin) en pheomelanin (rood-geel) reguleert.
90
New cards
Bepaling van uiterlijk/Forensic DNA Phenotyping (FDP)
Om dit te bepalen wordt er gebruikgemaakt van een SNP-analyse, gevolgd door statistische modellen en berekeningen. Echter kan een persoon hun haar verven, en wordt gewicht en lengte grotendeels beïnvloed door iemands dieet.
91
New cards
Bepaling van ethniciteit
Dit kan bepaald worden door SNP’s en mtDNA omdat bepaalde SNP’s meer voorkomen in bepaalde bevolkingsgroepen dan andere. Echter gaan veel commerciële testen ervanuit dat rassen 100% ‘puur’ zijn, terwijl dit niet zo is. Ook betekent afwezigheid van een bepaalde SNP niet altijd dat iemand niet bij een bepaalde bevolkingsgroep hoort.
92
New cards
Mini-sequencing
Sequentiemethode waarbij de volgende stoffen aanwezig zijn:
\- 1 template DNA
\- 1 primer
\- ALLEEN ddNTP’s
Eerst wordt er een (multiplex) PCR uitgevoerd. Daarna wordt er op het template-DNA (de amplicons uit de PCR) een interne primer (met een tag aan het 5’-einde) ingebouwd die net stopt voor de SNP. Omdat er alleen fluorescerende ddNTP’s aanwezig zijn en geen dNTP’s, wordt vervolgens bij de SNP een ddNTP ingebouwd, waardoor de ketenextensie direct stopt. Met CE wordt dit vervolgens geanalyseerd.
De commerciële naam is ook wel ‘SNapShot’ en er is hier sprake van een single base extension (SBE).
\- 1 template DNA
\- 1 primer
\- ALLEEN ddNTP’s
Eerst wordt er een (multiplex) PCR uitgevoerd. Daarna wordt er op het template-DNA (de amplicons uit de PCR) een interne primer (met een tag aan het 5’-einde) ingebouwd die net stopt voor de SNP. Omdat er alleen fluorescerende ddNTP’s aanwezig zijn en geen dNTP’s, wordt vervolgens bij de SNP een ddNTP ingebouwd, waardoor de ketenextensie direct stopt. Met CE wordt dit vervolgens geanalyseerd.
De commerciële naam is ook wel ‘SNapShot’ en er is hier sprake van een single base extension (SBE).
93
New cards
Epigenetica
De studie die bekijkt hoe DNA interacties aangaat met diverse kleine moleculen in cellen, welke genen aan of uit kunnen zetten. Dit gebeurt door de aanwezigheid en de concentratie waarin ze aanwezig zijn in een cel. Hierdoor wordt het DNA strakker of losser opgewonden. Het verandert het DNA zelf **niet**.
94
New cards
Epigenoom
Totaal van alle chemische labels (zoals methyl) in een cel. Hierdoor kan het DNA beter of slechter afgelezen worden waardoor genen uit of aangezet kunnen worden. Ze worden beïnvloed door voeding, medicatie, blootstelling aan chemische stoffen of sociale belevenissen. Ze kunnen doorgegeven worden aan het nageslacht, en soms ook ongedaan gemaakt worden.
95
New cards
DNA-methylatie
Dit is de binding van een methylgroep aan het DNA. Dit wordt gedaan door het DNMT3a en b die de overdracht van methylgroepen naar specifieke CpG-groepen in het DNA katalyseren. Hierdoor kunnen de bindingsplaatsen van de transcriptiefactoren geblokkeerd worden, waardoor het niet afgelezen/getranscribeerd kan worden en het gen gesilenced wordt.
Dit gebeurt random en vindt steeds meer plaats naarmate we ouder worden.
Dit gebeurt random en vindt steeds meer plaats naarmate we ouder worden.
96
New cards
Chromosoom 15 met OCA2, HERC2 en MATP
Markers in het DNA die coderen voor oogkleur
97
New cards
Epigenetisch profiel
‘Vingerafdruk’ van DNA-methyleringen waar informatie van een persoon uit gehaald kan worden, zoals drugsgebruik. Het is voor nu nog onderontwikkeld maar gaat in de toekomst waarschijnlijk wel gebruikt worden.
98
New cards
Gouden standaard
Een uitgebreide **gevalideerde** methode die de grootste **betrouwbaarheid** en **zekerheid** geeft. STR-analyse, tegenwoordig met 27 markers, is hier een voorbeeld van. Alle nieuwe ontwikkelde methodes worden hiermee vergeleken.
99
New cards
Minor Allel Frequency (MAF)
De ena meest voorkomende SNP. In een onderzoek is het belangrijk dat dit een groot percentage heeft (>40% in dit onderzoek) omdat de kans anders te groot is dat bij het uitkiezen van een random persoon in de populatie deze persoon dezelfde SNP heeft als andere mensen, wat betekent dat de discriminerende waarde laag is. Bij een waarde >40% is de SNP het meest **polymorf**.
100
New cards
Microbioom
Honderden tot duizenden soorten of stammen micro-organismen (=microben). Om het te analyseren wordt er (shotgun sequencing gevolgd met) NGS met universele primers gebruikt:
\- 16S: voor archaea en bacteriën
\- 18S: eukaryoten
\- ITS: schimmels
De grootste __voordelen__ zijn:
\- Het is altijd aanwezig
\- Het kan info geven over levende en dode organismen en samples van de omgeving
\- Het kan info geven over identiteit, gezondheid, ecosysteem, geografie etc.
Het __nadeel__ is dat de methode nog niet gestandaardiseerd, gevalideerd en erg duur is.
\- 16S: voor archaea en bacteriën
\- 18S: eukaryoten
\- ITS: schimmels
De grootste __voordelen__ zijn:
\- Het is altijd aanwezig
\- Het kan info geven over levende en dode organismen en samples van de omgeving
\- Het kan info geven over identiteit, gezondheid, ecosysteem, geografie etc.
Het __nadeel__ is dat de methode nog niet gestandaardiseerd, gevalideerd en erg duur is.