Cours 15 - L’ origine des mutations
1/41
There's no tags or description
Looks like no tags are added yet.
Name | Mastery | Learn | Test | Matching | Spaced | Call with Kai |
|---|
No analytics yet
Send a link to your students to track their progress
42 Terms
Deux principaux processus responsables des variations génétiques
Recombinaison (enjambement)
Mutations
Recombinaison
Est le résultat de processus cellulaires qui entraînent le regroupement d'allèles de gènes différents dans de nouvelles combinaisons.
Vrai ou Faux. Chaque méiose est sujet a des recombinaisons différentes.
Vrai
Mutation
Chaque nucléotide peut changer pendant un processus appelé…
Mutation génique
Si une mutation se situe au niveau d’un gène on parle de ….
Mutations ponctuelles
Changement d’ une seule base
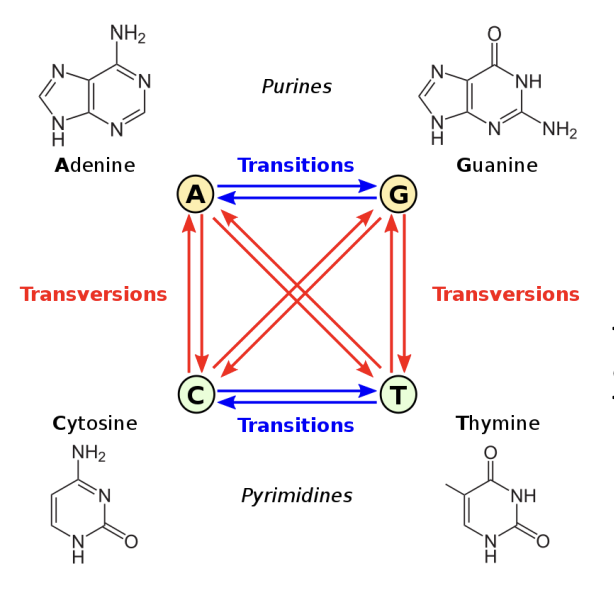
Substitution de base
Transition
La liaison Purine-pyrimidine est conservée
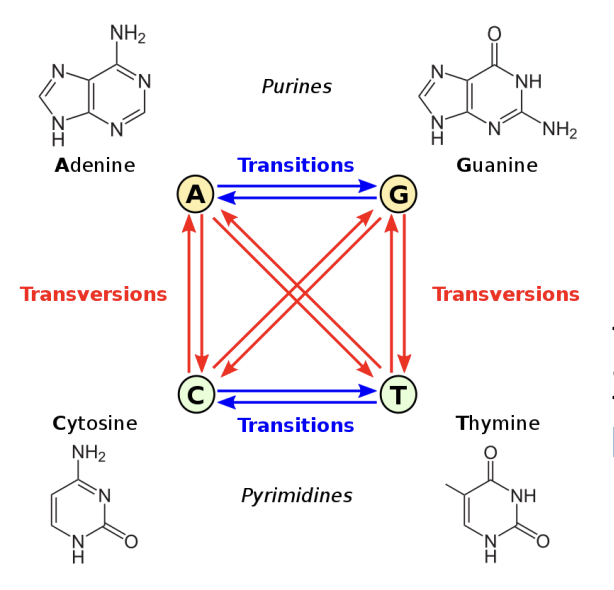
Transversion
La liaison purine - pyrimidine est inversée
Mutations dans la région codante
Synonyme
Faux-sens (conservative)
Faux-sens (non-conservative)
Non-sens
Indel
Mutation synonyme
Mutation dans la région codante
Codon modifié spécifie pour le même acide aminé

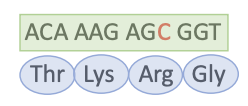
Mutation Faux-sens (conservative)
Mutation dans la région codante
Codon modifié spécifie pour un acide aminé diffèrent mais ayant des propriétés chimiques similaires

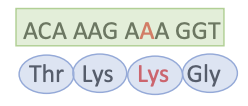
Mutation Faux-sens (non conservative)
Mutation dans la région codante
Codon modifié spécifie pour un acide aminé Diffèrent et ayant des propriétés chimiques différents

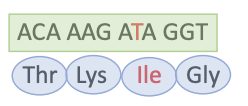
Mutation non-sens
Mutation dans la région codante
Codon modifié spécifie pour un codon STOP


Indel
Mutation dans la région codante
Modification du cadre de lecture


Mutations dans un région non codante
Mutations dans ces séquences peuvent supprimer ou créer un site de liaison:
• Modification de l’ expression d’ un gène
• Modification des niveaux de protéine
Vrai ou Faux. Dans les cellules, les molécules d’ADN sont complètement stables.
Faux
Vrai ou Faux. Mutations peuvent être un changement d’ une seule base ou des chromosomes entiers.
Vrai
Mutations spontanées
Le dommage a l’ADN vient par l’environnement cellulaire et par des erreurs de l’ADN polymérase pendant la réplication.
Se vérifient naturellement et peuvent toucher toutes les cellules
Dommages causés par l’eau (hydrolyse) conduisent à la dépurination et à la désamination
Les réactions avec des molécules réactives contenant de l'oxygène entraînent plusieurs types de dommages à l'ADN
Mutations induites
Le dommage a l’ADN est produit par des agent appelés mutagènes.
Tautomères des bases
Isomères différant par la position de leurs atomes
Forme céto
Tautomère de bases
Forme normalement présente
Formes imino ou énol
Tautomère de bases
Peuvent s’ apparier avec une base inadéquate
Dépurination
Lésion spontanée
Mène à des sites apuriniques
Ne peuvent pas spécifier la base complémentaire
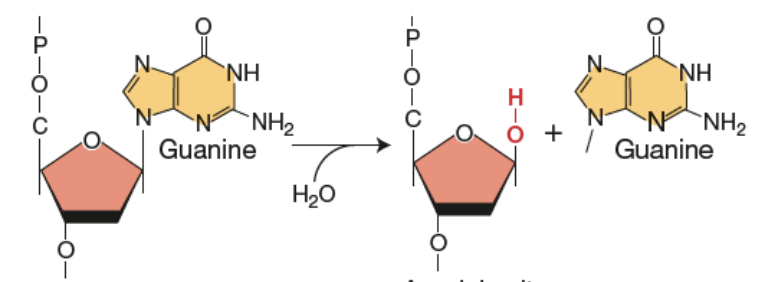
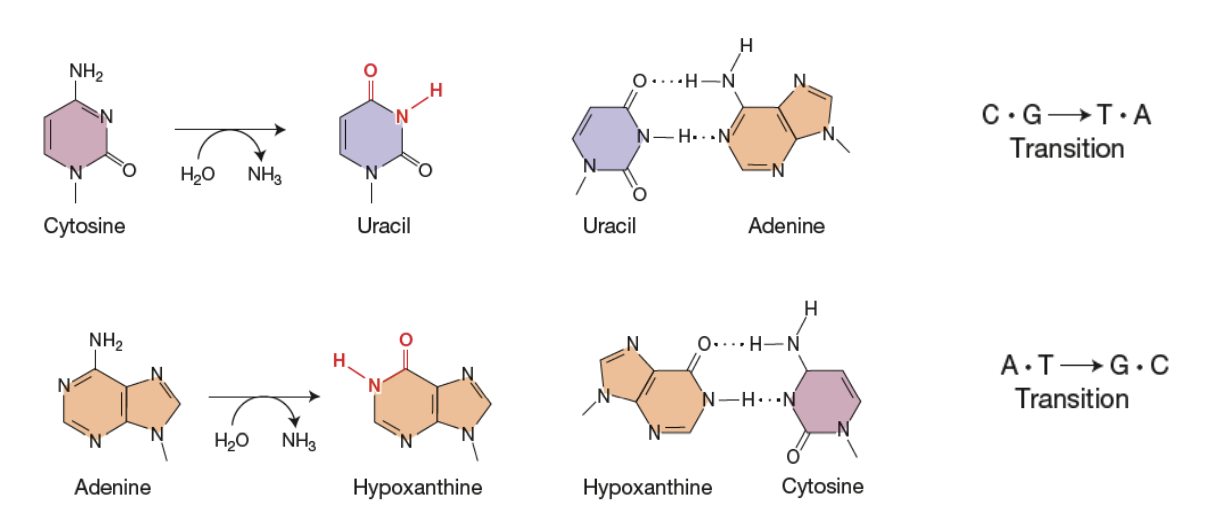
Désamination
Lésion spontanée
Groupement amine enlevé
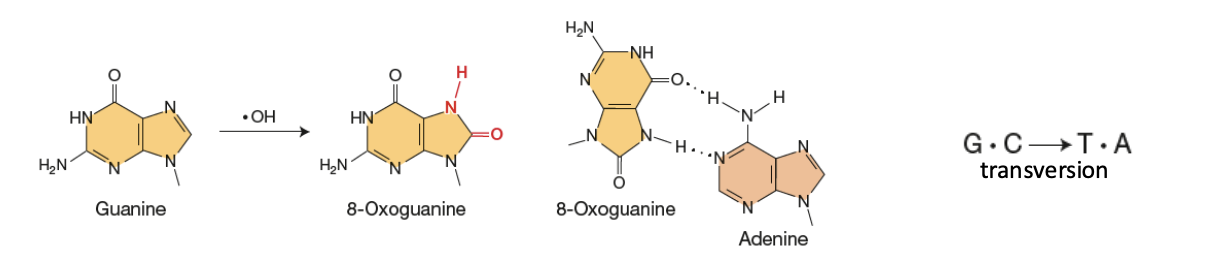
Dommage d’oxydation
Lésion spontanée
Ajout d’oxygène
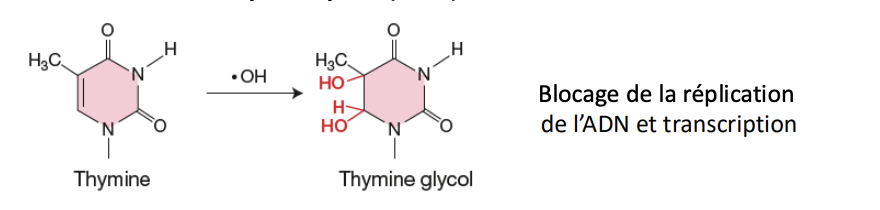
Espèces réactives de l'oxygène (ROS)
• radicaux superoxydes (⋅O2- )
• peroxyde d'hydrogène (H2O2)
• radicaux hydroxyles (⋅OH)
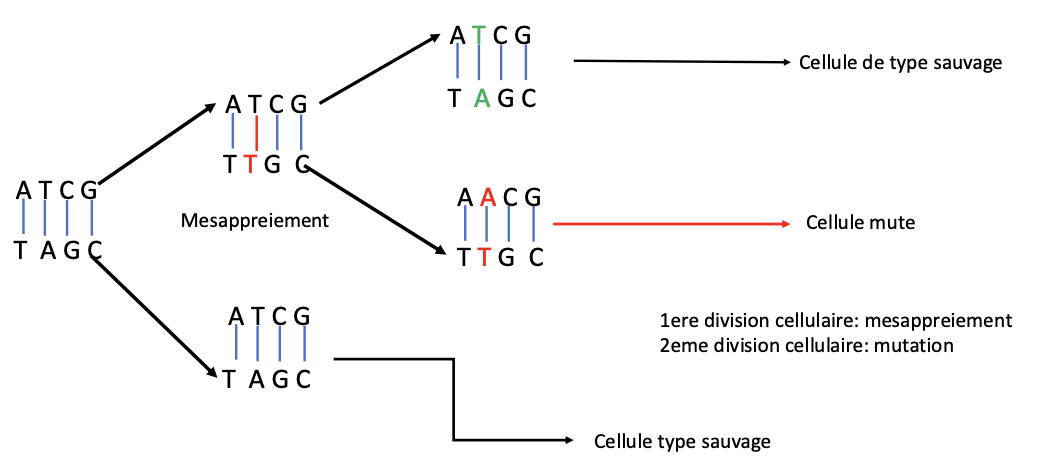
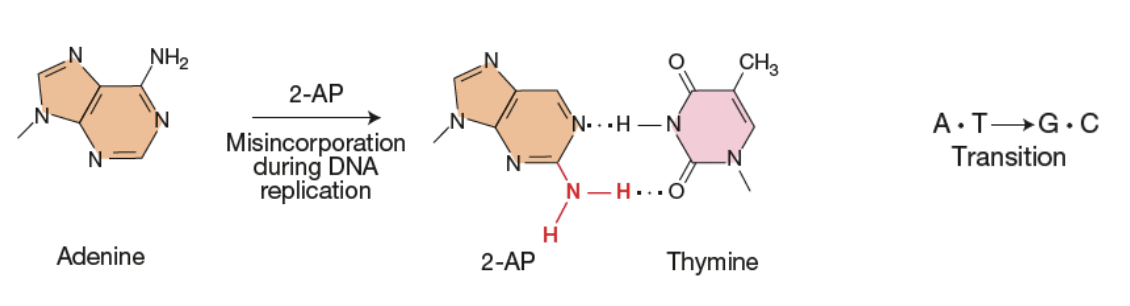
Mésappariement
Lésion induite
1. Remplacement d’une base avec analogues
Modification d’ une base avec agents alkylants
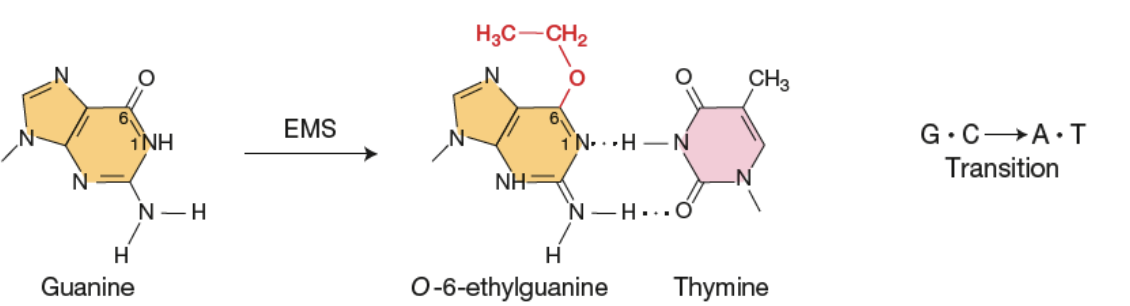
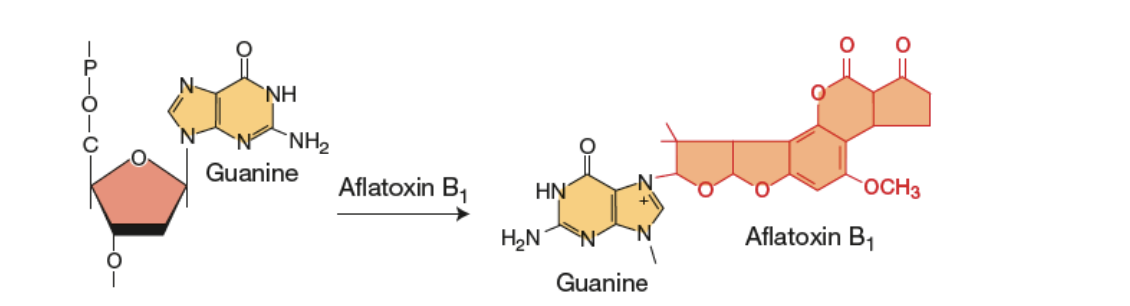
Endommagement d’une base
Causent un blocage de la réplication de l’ ADN
Agents intercalants
• Ils ressemblent aux paires de bases
• Causent insertions et délétions
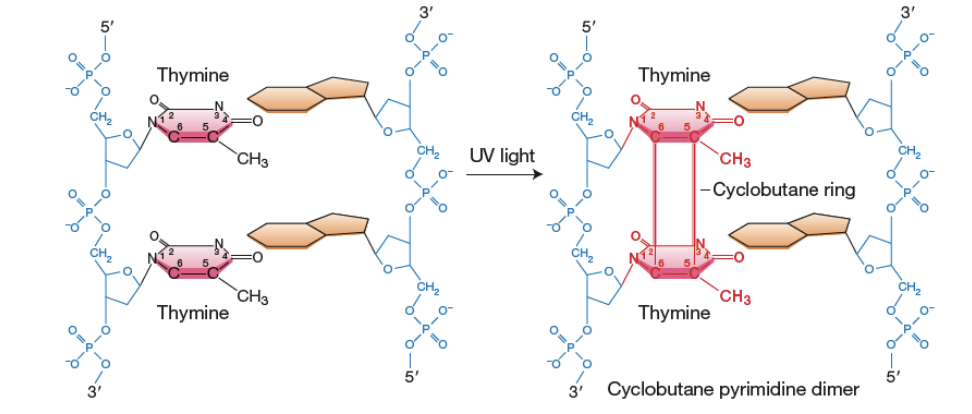
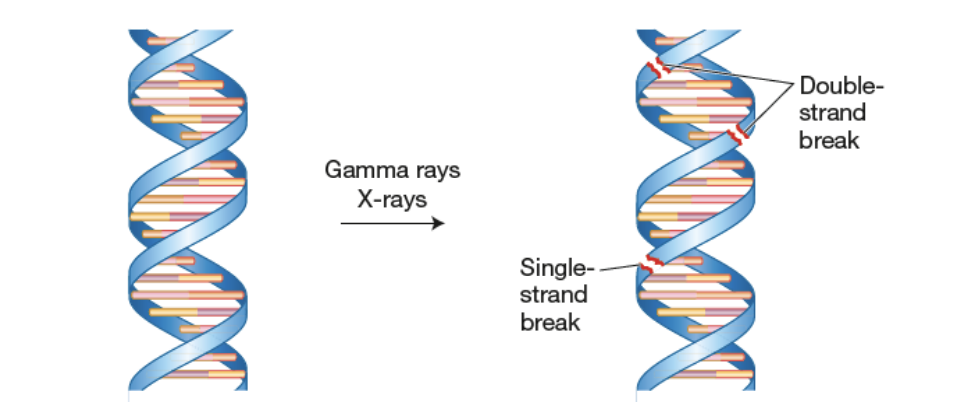
Agents physiques
Rayons UV
Rayons Gamma
Rayons X
Mécanismes de réparation de l’ADN (6)
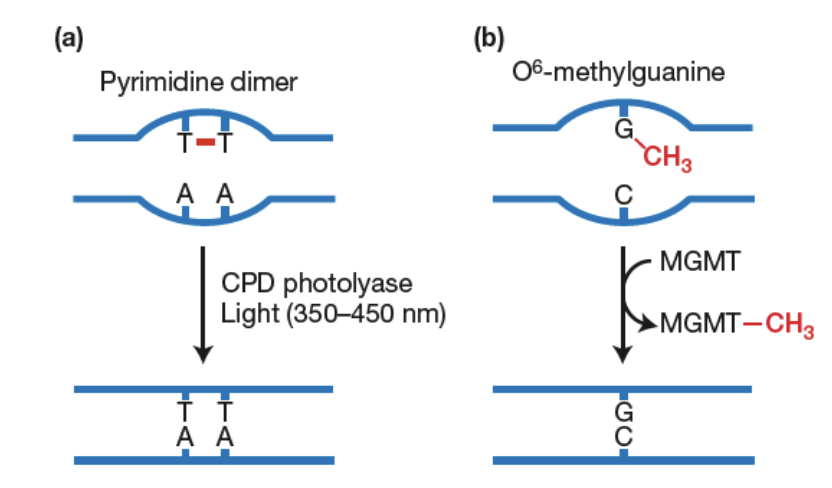
Réparation directe
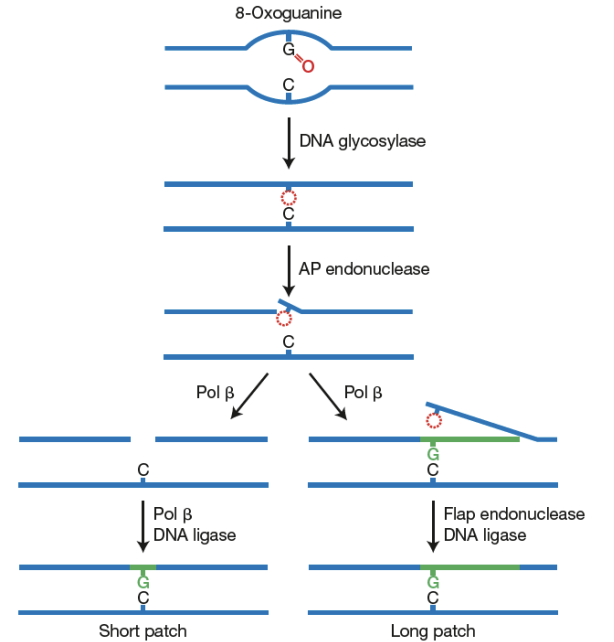
Réparation par excision de base (REB)
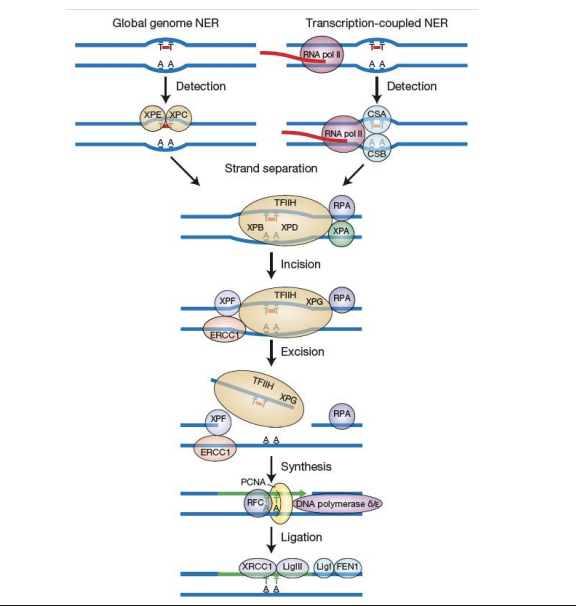
Réparation par excision de nucléotide (REN)
Réparation des mésappariements (RMA)
Synthèse translésionnelle (STL)
Recombinaison homologue (RH)
Réunion d’ extrémités non homologues (RENH)
Réparation directe
Réparation par excision de base (REB)
ADN glycosylase
Réparation par excision de base (REB)
Excise la base → site apurinique ou apyrimidinique
AP endonucléase
Réparation par excision de base (REB)
Coupe un brin
Polymérase β (Pol β)
Réparation par excision de base (REB)
Excise le site AP et synthétise la base complémentaire
Synthétise 2-10 nucléotides
Réparation par excision de nucléotide (REN)
Détection du dommage:
→ Pendant la transcription ou pas
Séparation des brins:
→ Recrutement le complexe multiprotéique TFIIH pour séparer les brins
Incision:
→ L'endonucléase XPF clive une liaison phosphodiester à 5′ de la lésion
→ L'endonucléase TFIIH XPG clive à 3′ de la lésion
Excision
Polymérisation
Ligation
Recombinaison homologue (RH)
• A besoin de la présence d’un molécule d’ ADN non endommagé
• Utilisé seulement dans cellules en cours de division
Après la formation des CDB, les extrémités brisées de l'ADN sont traitées par les exonucléases pour générer des régions simple brin terminant avec un 3’ libre
Invasion de brin: l’ extrémité 3’ d’ un brin déplace un brin de l'ADN homologue.
Cela crée une structure appelée boucle de déplacement (boucle D).
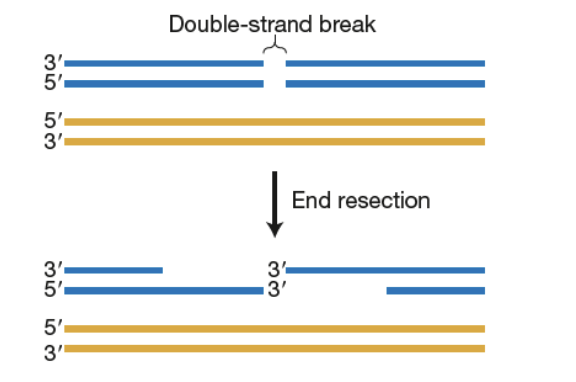
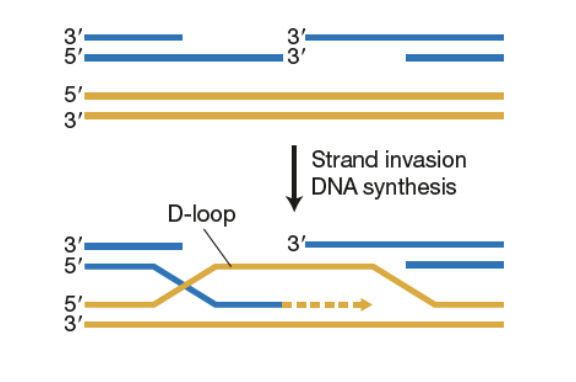
Réparation des cassures de double brin - RCDB
Dans la recombinaison homologue (RH)
Nouvelle synthèse d’ ADN commence a partir de l’extrémité 3’
Le brin se sépare de sa matrice et s’hybride
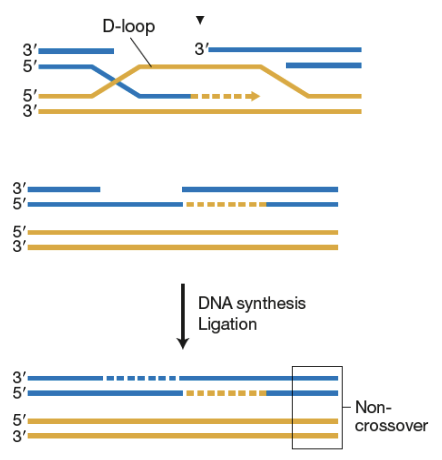
Réparation dépendant de la synthèse (RDS)
Dans la recombinaison homologue (RH)
Les deux brins envahissent les homologues, créant un intermédiaire à quatre branches et à double croisement appelé double jonction de Holliday (HJ).
Les endonucléases appelées résolvases clivent les jonctions de Holliday pour produire des segments d'ADN non croisés ou croisés.
Ligase répare les nicks
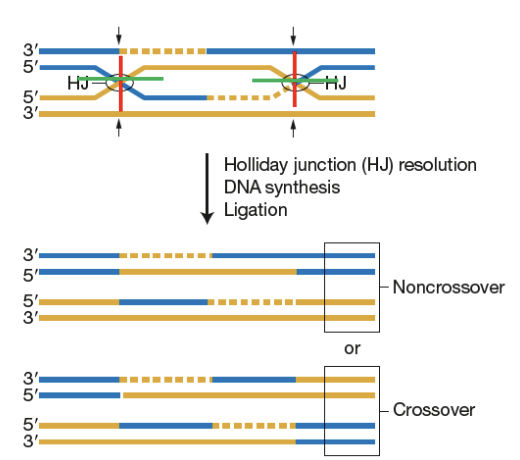
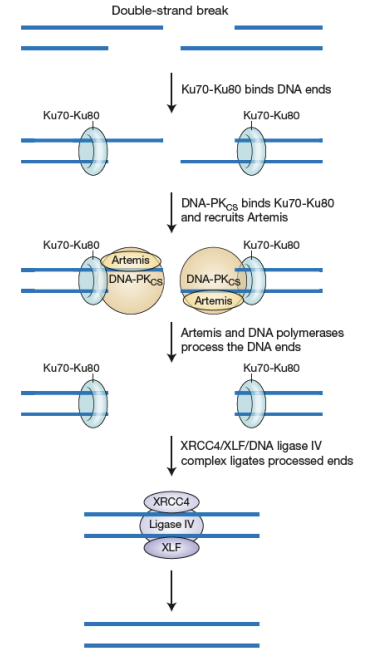
Réunion d’ extrémités non homologues (RENH)
Peut créer des petites délétions
Détection du dommage:
élimination des brins simples: Artemis
Les petits gaps de l'ADN sont comblés par l'ADN polymérase μ ou λ.
ADN ligase répare les nicks