Chapitre 4 : Réplication et traduction du génome des virus ARN
1/90
There's no tags or description
Looks like no tags are added yet.
Name | Mastery | Learn | Test | Matching | Spaced | Call with Kai |
|---|
No analytics yet
Send a link to your students to track their progress
91 Terms
Quelles sont les trois classes principales de virus à ARN et donne un exemple pour chacune ?
Classe 3 : Virus à ARN double brin → Exemple : Rotaviridae
Classe 4 : Virus à ARN simple brin positif (ARN+) → Exemples : Flaviviridae, Picornaviridae, Coronaviridae
Classe 5 : Virus à ARN simple brin négatif (ARN–) → Exemples : Filoviridae, Orthomyxoviridae, Rhabdoviridae → Ils doivent emmener l’ARN polymérase dans le virion
Quelle est la particularité des virus de la classe 6 (ARN+) par rapport aux autres virus à ARN ?
Bien qu'ils aient un ARN+, ils ne peuvent pas être directement traduits en protéines.
Leur génome n’est pas reconnu comme ARNm.
Ils utilisent une transcriptase inverse (RT) pour produire un ADN double brin, qui sera ensuite transcrit en ARNm.
Ils passent donc par un stade ADN, contrairement aux classes 3, 4 et 5.
Pourquoi ne parle-t-on pas de transcription au sens classique pour les virus à ARN ?
La transcription classique est basée sur l’ADN → ARNm.
Chez les virus à ARN, les messagers sont créés directement à partir de l’ARN.
La "transcription" devient une forme de réplication.
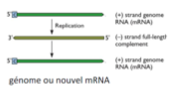
On parle de transcription pour produire les ARNm, et de réplication pour produire de nouveaux génomes viraux.
Qu’est-ce qui caractérise un ARNm viral fonctionnel dans une cellule eucaryote ?
Une séquence codante avec un codon START et un codon STOP.
Présence de régions UTR.
Une coiffe 5’ (cap) pour reconnaissance par les ribosomes.
Une queue poly(A) à l’extrémité 3’.
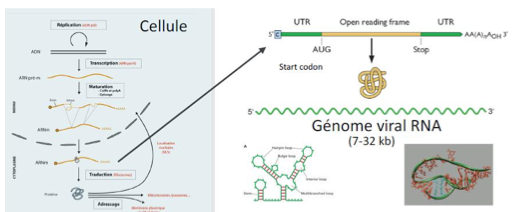
Quelle est la taille typique des génomes des virus à ARN et leur structure générale ?
Taille : 7 à 32 kilobases (kB).
Généralement plus petits que les génomes des virus à ADN.
Bien qu'ils paraissent linéaires, ils présentent souvent des repliements structuraux → nécessaires à la réplication et à la production des ARNm.
Quelles sont les conséquences du fait d’avoir un génome ARN (et non ADN comme les cellules) ?
Il n’existe pas de RNA polymérase RNA-dépendante cellulaire capable de copier de longs segments.
Ces virus doivent donc coder leur propre ARN polymérase, et parfois même l’emporter dans le virion (classe 5 notamment).
Exception : Virus de l’hépatite D, qui utilise une ARN polymérase ARN-dépendante cellulaire.
Les séquences doivent être copiées fidèlement malgré l'absence de correction d'erreurs.
Quels virus à ARN peuvent être directement traduits dès leur entrée dans la cellule ?
Virus à ARN+ (classe 4)
Leur ARN est nu (sans protéines), sauf exceptions : rétrovirus et coronavirus.
Leur génome est soit :
coiffé et polyadénylé (poly-A)
ou contient une IRES (Internal Ribosome Entry Site) pour être reconnu par les ribosomes sans la coiffe et la queue
Tous les virus à ARN codent-ils leur propre ARN polymérase ?
Oui, sauf le virus de l’hépatite D, qui utilise une ARN polymérase cellulaire.
Les virus des classes 3 et 5 emportent leur ARN polymérase dans le virion car leur ARN ne peut pas être directement traduit.
Caractéristiques des virus à ARN double brin (classe 3) ?
Exemple : Reoviridae (rotavirus) responsables de gastro-entérites
La cellule ne peut pas synthétiser d’ARNm à partir de ce génome.
Le virion contient une ARN polymérase dans sa capside.
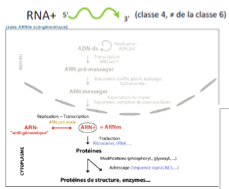
Caractéristiques des virus à ARN simple brin positif (classe 4) ?
Leur génome peut être immédiatement traduit.
Reconnus par les ribosomes car ils possèdent :
une coiffe et queue poly(A)
ou une IRES
Génome nu sans protéines associées sauf exceptions (Coronavirus, Rétrovirus).
Ils produisent un ARN– anti-génomique servant de matrice pour répliquer le génome. (toujours avec une ARN polymérase virale)
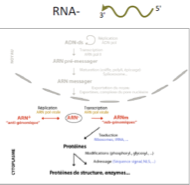
Caractéristiques des virus à ARN simple brin négatif (classe 5) ?
Génome toujours associé à des protéines (ARN polymérase et protéines de capsides).
Nécessitent d’avoir l’ARN polymérase virale dans le virion.
Produisent :
un ARN+ anti-génomique → matrice pour le génome
un ARN subgénomique (plus court que la séquence complète du génome) → traduit en protéines virales, dont l’ARN polymérase qui doit être emmené dans le virion.
Où se passe le cycle de la majorité des virus à ARN ? Quelle est l’exception ?
La majorité du cycle se passe dans le cytoplasme → là où se fait la traduction. Ils n’ont donc normalement pas besoin de la machinerie cellulaire
Exception : Orthomyxoviridae (grippe) → le cycle passe par le noyau.
Quelles similarités structurelles observe-t-on entre les différentes types de polymérases (RNA-polymérases et DNA-polymérases) ?
Elles partagent des motifs structuraux communs (motifs de A à D) visible en cristallographie
Ces similitudes sont telles qu’il est difficile de les distinguer par leur structure seule.
Le site catalytique (zone où s’incorporent les nucléotides) est très similaire entre les polymérases, bien qu’elles utilisent des substrats différents (ARN ou ADN).
Les polymérases ont donc une origine évolutive commune, avec une conservation du mécanisme enzymatique.
Quelles sont les différences de substrat et de produit entre l’ADN polymérase et l’ARN polymérase ?
L’ADN polymérase utilise de l’ADN comme matrice et produit de l’ADN.
L’ARN polymérase utilise de l’ARN comme matrice et produit de l’ARN.
L’ARN contient de l’uracile à la place de la thymine.
Le sucre est un ribose dans l’ARN (vs désoxyribose dans l’ADN).
L’élongation de la chaîne se fait dans le sens 5’ → 3’ pour les deux.
Quelle est la fidélité de l’ARN polymérase virale par rapport à l’ADN polymérase ?
Peu fidèle : 1 erreur / 10⁴ à 10⁵ nt.
Pas de correction d’erreur.
ADN polymérase : bien plus fidèle (1 / 10⁸ à 10⁹ nt).
Conséquences de cette faible fidélité ?
Plus de mutations.
Variabilité génétique élevée.
Meilleure adaptation, échappement immunitaire.
Effet d’une ARN polymérase rendue plus fidèle ?
Pas d’impact majeur sur le virus.
Grande production de particules → au moins une fonctionne.
Quelle propriété favorise les recombinaisons ?
L’ARN polymérase peut changer de matrice pendant la réplication (template switching).
Ex : poliovirus.
Début de la synthèse d’ARN : comment ?
Démarre à des sites précis.
Avec ou sans amorce.
Parfois sans matrice (rare, ne concernent que quelque nucléotide).
Quelles familles de virus de la classe 4 (ARN+) infectent l’homme ?
Flaviviridae : virus enveloppés → Hépatite C, fièvre jaune, dengue
Togaviridae : virus enveloppés → Rubéole, Chikungunya (présent en République Dominicaine et aux Caraïbes)
Coronaviridae : virus enveloppés → SARS-CoV, MERS-CoV (respiratoires aigus et potentiellement mortels), HCoV (rhumes ou grippes)
Picornaviridae : virus nus → Hépatite A, rhinovirus (rhume), poliovirus (poliomyélite)
Calciviridae : virus nus → Norovirus (gastroentérites)
Hepeviridae : virus nus → Virus de l’hépatite E (endémique en Asie et certaines régions d’Afrique)
Quelle est la particularité des virus à ARN+ par rapport à la présence de protéines liées au génome ?
Les virus à ARN+ ne sont pas recouverts par des protéines (contrairement à la classe 5)
Exception : Coronaviridae, qui ont une capside hélicoïdale avec des nucléoprotéines entourant le génome
Structure : majoritairement icosaédrique pour les virus ARN+ infectant l’homme
D’autres virus (comme les Lolavirus, qui infectent les plantes) peuvent ne pas avoir cette structure et contenir des protéines liées au génome
Comment se fait la traduction du génome des virus à ARN+ ?
Le génome ARN+ peut être directement traduit par les ribosomes cellulaires
Le virus code pour sa propre ARN polymérase, indispensable à la réplication
La synthèse d’un brin ARN- anti-génomique est nécessaire pour :
Réplication du génome
Production de nouveaux ARNm
Le génome code aussi pour des protéines de capside, de matrice et, pour certains, d’enveloppe
Comment s’organise le génome des Flaviviridae ?
Le génome est un long ARNm polycistronique (contrairement à l’ARNm cellulaire monocistronique qui ne code pour une seule protéine) car toutes les parties codantes sont à la suite l’un de l’autre.
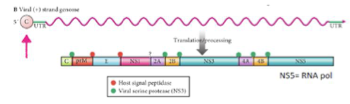
Comment le génome des Falviviradae est-il traduit ?
Traduction donne une polyprotéine, ensuite clivée en protéines fonctionnelles par des protéases virales et cellulaires
Traduction se fait via la machinerie cellulaire
Coiffe + queue polyA → reconnaissance par les eIF (eukaryotic translation initiation factors)
Le complexe de traduction se forme avec :
eIF4E (reconnaît la coiffe)
eIF3 (lie la petite sous-unité ribosomale 40S)
Scanning jusqu’au codon start AUG → grande sous-unité 60S s’associe → début de la traduction grâce à l’intervention d’un premier ARNt
Tous les Flaviviridae possèdent-ils une coiffe ?
Non !
West Nile virus et Zika virus : possèdent une coiffe → traduction classique
Virus de l’hépatite C : pas de coiffe, utilise un IRES (internal ribosome entry site)
Permet la liaison directe à la 40S sans protéines accessoires
Repliement structurel reconnu par les ribosomes
IRES ≠ séquence, c’est une structure ARN tridimensionnelle
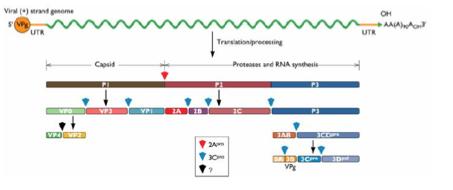
Comment se déroule la traduction et réplication chez les Picornaviridae (ex : poliovirus, rhinovirus) ?
Génome contient une protéine VPg liée à l’ARN +
Queue poly A présente
VPg est éliminée avant traduction → Ne sert qu’à la réplication
Pas de coiffe → Utilisation d’un IRES pour recruter les ribosomes
Traduction d’une polyprotéine, clivée uniquement par des protéases virales
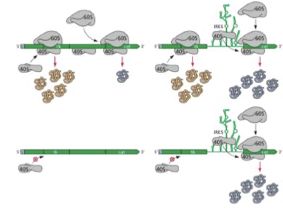
Comment a-t-on mis en évidence que certains ARN viraux peuvent être traduits sans coiffe ?
En observant des structures repliées sur certains ARNm viraux appelées IRES (internal ribosome entry site)
On a utilisé un ARNm bicistronique (2 séquences codantes) :
La 40S se fixe à la coiffe → production de la 1re protéine
Peu de production pour la 2e sans IRES
Ajout d’un IRES entre les deux → production de la 2e protéine
En modifiant la sous-unité 40S pour empêcher la fixation à la coiffe :
Plus de production du tout
Ajout d’un IRES → production uniquement de la 2e protéine
→ Preuve d’une entrée interne indépendante de la coiffe et du scanning
Qu’est-ce qu’un IRES ?
Structure repliée de l’ARN
Permet le recrutement direct de la 40S ribosomale
Ce n’est pas une séquence spécifique, mais une structure tridimensionnelle
Il existe de nombreux types d’IRES, sans similarité de séquence
Structure essentielle dans les vecteurs viraux pour exprimer plusieurs protéines simultanément
Quel est le rôle de l’IRES dans les Picornaviridae ?
Permet la liaison directe de la 40S
Ne nécessite pas la protéine eIF4E (qui reconnaît la coiffe)
Recrutement facilité par les protéines cellulaires eIF4G et eIF3 qui reconnaissent IRES
Recrutement ribosomes qui scanne jusqu’au codon d’initiation
Quel est l’avantage du virus de la polio avec l’IRES ?
Le virus clive la protéine eIF4G
Cela bloque la traduction des ARNm cellulaires où la protéine EiF4G est indispensable au recrutement des ribosomes
Mais l’IRES peut toujours recruter la 40S → traduction virale privilégiée
Quand commence la réplication chez les Picornaviridae ?
Après la traduction de la polyprotéine
Celle-ci est clivée pour former :
Des protéines de structures
Des protéines nécessaires à la réplication
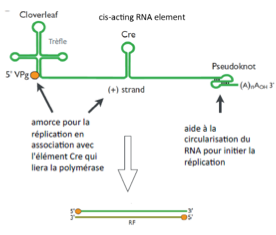
Quels éléments structuraux de l’ARN viral sont essentiels à la réplication ?
Repliements en trèfle → fixation de l’ARN polymérase
Élément CRE (cis-acting RNA element) :
Repliement ARN spécifique
Liaison à la propolymérase 3CD et à la polymérase 3D
Recrutement de VPg
Noeud en 3’
Aide à la circulation de l’ARN pour initier la replication
Quel est le rôle du VPg dans la réplication ?
Il sert d’amorce
Il est uridyllé → reconnaît une séquence d’AA au niveau de CRE
Cette séquence UU peut aussi reconnaitre la queue polyA
Permet la synthèse du brin ARN - à partir de cette queue
Comment est produite la nouvelle ARN+ chez les Picornaviridae ?
Le brin ARN - sert de matrice
VPg sert à amorcer la synthèse du nouveau brin positif
Ce brin pourra être :
Encapsidé comme génome
Ou traduit comme ARN messager
Quelles protéines cellulaires et virales initient la réplication de l’ARN viral des Picornaviridae ?
PCbp (protéine cellulaire) : se fixe à la boucle en trèfle de l’ARN viral
Recrute 3AB : domaine hydrophobe s’ancrant à une membrane issue du RE (vésicules d’autophagie)
Ce complexe stabilise le site de traduction et amorce la réplication
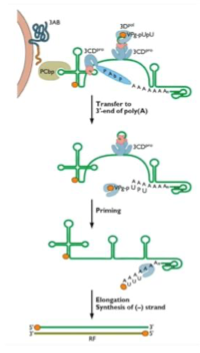
Quel est le rôle de la protéine 3CDpro dans la réplication ?
Se fixe aussi à la boucle trèfle de l’ARN
Recrute PABP (protéine cellulaire liant la polyA)
PABP rapproche l’extrémité 3’ (polyA) de l’extrémité 5’ → circularisation de l’ARN
Permet le recrutement de VPg
Quel est le rôle du repliement CRE dans la réplication ?
Permet à 3CDpro de recruter 3Dpol (ARN polymérase)
Ce site contient une séquence AA reconnue par VPg
3Dpol synthétise un court di-nucléotide UU → amorçage de la polymérase
Comment VPg devient-il apte à amorcer la synthèse du brin ARN- ?
VPg est uridylilé au niveau du CRE (repliement cis-acting)
Cette uridylation permet à VPg de se lier à la queue polyA
À quoi sert la queue polyA pendant la réplication ?
Sert de matrice à partir de laquelle la polymérase initie la synthèse du brin ARN-
VPg-UU se lie à la queue polyA → amorce la synthèse du brin complémentaire
Quelles protéines virales de la région P3 participent à cette réplication ?
3AB : ancrage membranaire
3CDpro : clivage des polyprotéines + recrutement de 3Dpol
3Dpol : polymérase ARN-dépendante
VPg : amorce uridylilée
Comment s’effectue la synthèse du brin ARN- ?
VPg uridylilé (VPg-pUpU) se fixe à la queue polyA
3Dpol commence l’élongation à partir de ce site
Le brin ARN- est synthétisé complètement complémentaire au brin + initial
Quels rôles ont les protéines cellulaires dans la réplication virale ?
Permettent l’ancrage de l’ARN virales sur des membranes endosomiales
Participent à l’organisation des complexes de réplications
Pourquoi les ARN viraux ne sont-ils pas copiés comme les ARNm cellulaires ?
Les ARNm cellulaires n’ont pas les structures de repliement spécifiques (CRE, trèfles)
Ces structures sont essentielles à la fixation de l’ARN polymérase virale
Où se fait la réplication des Picornaviridae ?
À la surface de vésicules issues de l’autophagie
Le virus induit l’autophagie pour créer un microenvironnement favorable
Ces vésicules permettent de concentrer les facteurs de réplication
Comment prouve-t-on que le virus induit l’autophagie pour sa réplication ?
Observation par microscopie :
Cellules HeLa infectées par poliovirus → plus de vésicules
Ces vésicules ne sont pas présentes dans des cellules non infectées
Quel est l’avantage de cette stratégie ?
Concentration de l’ARN polymérase uniquement sur les génomes viraux
Évite la copie d’ARNm cellulaires
Quels autres virus utilisent une réplication similaire à celle des Picornaviridae ?
Calciviridae
Comment fonctionne la traduction chez les Togaviridae ?
Génome avec coiffe + queue polyA
Traduction démarre par reconnaissance de la coiffe (eIF4E)
Le ribosome 40S commence le scanning
Initiation non classique : grâce à une structure appelée DLP (au lieu de AUG)
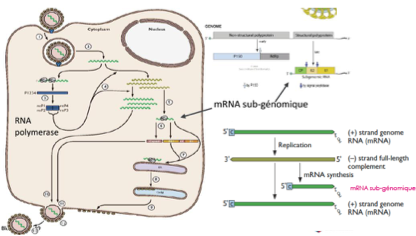
Comment se déroule le cycle des Togaviridae ?
Comment se déroule le cycle des Togaviridae ?
Entrée par fusion avec un endosome (virus enveloppé)
Libération de l’ARN+ → traduction directe
Traduction de la polymérase virale
Synthèse d’un ARN- anti-génomique
Production de :
ARN+ complets (nouveaux génomes ou pour la polymérase)
ARN+ subgénomiques (protéines de structure)
Comment le génome des Togaviridae code-t-il deux types de protéines ?
Une polyprotéine non structurale (ARN polymérase)
Une polyprotéine structurale (capside, glycoprotéines)
Quel est le rôle du codon STOP chez les Togaviridae ?
Coupe la traduction de la polyprotéine non structurale (donc traduit juste l’ARN polymérase et les protéines accessoires nécessaires à la traduction)
Permet ensuite la production d’un ARN+ plus court
Cet ARNm est coiffé → traduit en protéines de structure
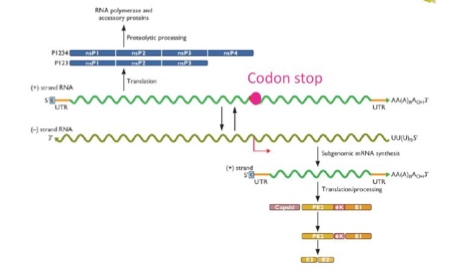
Comment se déroule la réplication chez les Coronaviridae ?
Le plus grand génome ARN connu
Après entrée : traduction de la polymérase
Synthèse d’un brin ARN- anti-génomique
Production à partir de ce brin de plusieurs ARNm subgénomiques
Ces ARNm codent pour différentes protéines structurales (dont la capside)
Les virus à ARN– peuvent-ils être directement traduits à leur entrée dans la cellule ?
Non
l’ARN ne peut pas être reconnu par les ribosomes
Il faut d’abord produire un ARN + grâce à une ARN polymérase virale
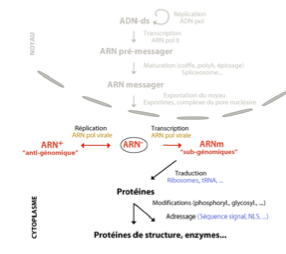
Quels types d’ARN+ sont produits par les virus ARN– ?
ARN + anti-génomique : sert de matrice pour répliquer le génome
ARNm subgénomique : traduit par les ribosomes cellules pour produire les protéines virales
Ces deux types d’ARN sont produits par l’ARN polymérase virale
Quels virus ARN– infectent l’Homme ?
Non segmentés
Paramyxovirdae (rougeoles, oreillons)
Filoviridae (Ebola)
Rhabdoviridae (Rage transmis du renard à l’homme)
Segmentés
Orthomyxoviridae (Influenza)
Bunyaviridae (hantavirus) présents en Belgique peut provoquer des problèmes rénaux
Arenaviridae (Lassa virus), ne sont pas présents en Belgique, responsables de fièvres hémorragiques
Autre cas :
HDV (Hépatite D), virus satellite
Quelle est la particularité commune à tous les virus de la classe 5 ?
Ils contiennent une ARN polymérase virale dans le virion
Pour les virus segmentés, chaque segment est accroché à la polymérase
Tous ont une forme hélicoïdale
Le génome est étroitement associé à des nucléoprotéines (NP ou N)
Quelle exception existe parmi les virus ARN– ?
HDV (Hépatite D) :
N’emmène pas sa propre polymérase
Utilise la polymérase cellulaire
Virus satellite, dépendant du virus de l’Hépatite B (classe 7)
Pourquoi les ARNm subgénomiques des virus ARN– sont-ils plus courts que le génome ?
Ils doivent avoir une coiffe et queue polyA
Ils servent à être traduits, pas à répliquer le génome
On ne peut pas répliquer le génome à partir de ces ARNm
🦠 Rhabdoviridae (rage)
Comment fonctionne la transcription du génome ARN– des Rhabdoviridae ?
Le brin ARN– est transcrit en plusieurs petits ARNm
Chaque ARNm est monocistronique (code une ou deux protéines)
Chaque ARNm est doté :
D’une coiffe en 5’
D’une queue polyA en 3’
→ Similaire au paramyxoviridae
🦠 Rhabdoviridae (rage)
Ces ARNm permettent-ils la réplication du génome ?
Non, ils servent uniquement à la traduction des protéines
Pour la réplication du génome, un brin ARN + complet est produit comme matrice
🦠 Rhabdoviridae (rage)
Qu’est-ce qui déclenche le passage de la transcription à la réplication ?
L’accumulation de protéines N
Une concentration suffisante en N bloque la transcription segmentaire
La polymérase commence alors à produire un brin ARN + complet
🦠 Rhabdoviridae (rage)
Comment fonctionne la polymérase virale pendant la transcription ?
Elle démarre au début du génome ARN-
Elle transcrit un segment d’ARNm
Elle s’arrête à une séquence intergénomique pour
Ajouter une queue polyA
Puis redémarrer une nouvelle protéine
🦠 Rhabdoviridae (rage)
Quelle est la première protéine traduite chez les Rhabdoviridae ?
La protéine N
Son accumulation régule le switch transcription / régulation
🧬 Orthomyxoviridae (Influenza)
Quelle est la particularité des Orthomyxoviridae parmi les virus ARN– ?
Ce sont des virus segmentés
Leur réplication se déroule dans le noyau (exception)
🧬 Orthomyxoviridae (Influenza)
Comment les segments viraux pénètrent-ils dans le noyau ?
Grâce à un signal de localisation nucléaire (NLS)
→ Ce signal est porté par les nucléoprotéines (NP) associés à chaque segment
🧬 Orthomyxoviridae (Influenza)
Que produit chaque segment viral dans le noyau ?
Un ARNm - coiffé et polyadénylé.
Un ARN + anti-génomique servant de matrice pour répliquer le génome qui finira par sortir du noyau pour être encapsidé
Pour rappel, chaque segment est attaché avec son complexe RNA polymérase
🧬 Orthomyxoviridae (Influenza)
Où a lieu la traduction des protéines virales influenza ?
Dans le cytoplasme
🧬 Orthomyxoviridae (Influenza)
Comment la polymérase virale ajoute-t-elle un primer à un ARN+ viral ?
Par cap snatching
Elle a une activité endonucléase et clive l’extrémité 5’ d’un ARNm cellulaire = coiffe (10-13 nucléotides terminaux)
Cette coiffe est utilisée comme primer pour initier la transcription virale
Tous les ARNm du virus de la grippe ont une petite portion d’ARNm cellulaire
🧬 Orthomyxoviridae (Influenza)
Pourquoi les ARNm viraux(ARN+) influenza sont-ils plus courts que le génome ?
Ils sont tronqués d’environ 20 nucléotides en 3’ par rapport à l’ARN - d’origine alors que la queue polyA est bien transcrite
Un autre ARN + est nécessaire pour la réplication complète
🧬 Orthomyxoviridae (Influenza)
Comment la concentration en NP influence-t-elle la réplication ?
NP élevé (stabilise le brin)→ Permet la transcription de l’ARN complet (anti-génomique)
Ce brin complètement sert à produire une nouveau génome ARN-
🧬 Orthomyxoviridae (Influenza)
Un segment influenza code-t-il toujours une seule protéine ?
La plupart : oui
Certains segments : deux protéines par épissage alternatif
Virus à génome ambisens (Bunyaviridae, Arenaviridae)
Qu’est-ce qu’un génome ambisens ?
ARN simple brin qui code dans les deux sens de lecture
→ Un gène en orientation + , l’autre en orientation -
Virus à génome ambisens (Bunyaviridae, Arenaviridae)
Quels virus humains ont un génome ambisens ?
Arenaviridae (ex. Lassa virus : 2 segments)
Bunyaviridae (ex. Phlébovirus : 3 segments)
Virus à génome ambisens (Bunyaviridae, Arenaviridae)
Pourquoi ces virus doivent-ils contenir une ARN polymérase virale ?
Le génome ne peut pas être directement traduits car ils ne peuvent pas s’accrocher aux ribosomes
Il faut donc que l’ADN polymérase se trouve dans le virion
Virus à génome ambisens (Arenaviridae)
Que code chaque segment chez le Lassa virus (Arenaviridae) ?
Segment S (Small-sens)
Une glycoprotéine précurseur (GP)
Une nucléoprotéine
Segment L (Large - antisens)
Une protéine Z (liaison au zinc, agit comme une protéine matrice)
Une protéine L (ARN polymérase virale)
Virus à génome ambisens (Arenaviridae)
Comment sont séparés les deux gènes sur chaque segment ?
Par une région intergénomique en forme d’épinglette à cheveux
Quelle est la première étape de réplication des Arenaviridae ?
Transcription et traduction des gènes à orientation négative (NP et L)
Les ARNm produits ont une coiffe mais pas de queue polyA
Que permet l’accumulation de la protéine NP ?
Formation d’un brin ARN anti-génomique
Ce brin permet la transcription des gènes à orientation positive (GP et Z)
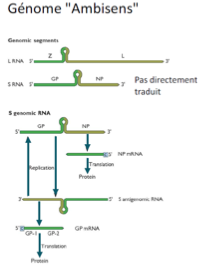
Que deviennent les ARNm issus du brin anti-génomique ?
Ils sont traduits en protéines de structure, notamment de capside
Virus de la classe 3 : ARN double brin (dsRNA)
Quelles familles virales appartiennent à la classe 3 ?
Reoviridae (ex : rotavirus → gastroentérites)
Seadonavirus (→ encéphalites en Asie du Sud-Est)
Coltivirus (→ fièvre à tiques au Colorado, transmis par tiques et moustiques)
Virus de la classe 3 : ARN double brin (dsRNA)
Quelle est la structure du génome des virus de la classe 3 ?
Génome composé de plusieurs segments d’ARN double brin
Un brin ARN+
Un brin ARN–
Chaque segment code pour une protéine
Virus de la classe 3 : ARN double brin (dsRNA)
Les brins ARN+ des virus dsRNA peuvent-ils être directement traduits ?
Non
Bien qu’ils soient en polarité +, ils ne sont pas accessibles aux ribosomes
La traduction commence uniquement à partir des ARNm produits dans la capside
Virus de la classe 3 : ARN double brin (dsRNA)
Que contiennent les virions des virus de la classe 3 pour permettre la transcription ?
Une ARN polymérase virale
Présente dans le virion, une par segment
Virus de la classe 3 : ARN double brin (dsRNA)
Quelle est la particularité structurale du rotavirus (Reoviridae) ?
Il possède de nombreuses protéines de capside
Ces protéines forment plusieurs couches de protection autour du génome
Virus de la classe 3 : ARN double brin (dsRNA)
Comment les Reoviridae entrent-ils dans la cellule ?
Par endocytose
Le virus est d’abord partiellement dégradé dans les endosomes
Mais la capside n’est jamais complètement détruite avant d’arriver dans le cytoplasme
Virus de la classe 3 : ARN double brin (dsRNA)
Dans quel état la capside virale reste-t-elle dans le cytoplasme ?
Elle reste partiellement intacte
La transcription de l’ARNm se fait à l’intérieur de cette capside
Virus de la classe 3 : ARN double brin (dsRNA)
À partir de quel brin est transcrit l’ARNm chez les Reoviridae ?
Toujours à partir du brin ARN–
Virus de la classe 3 : ARN double brin (dsRNA)
Quel est le type de réplication des virus à ARN double brin ?
Réplication conservative
Le brin ARN– sert à produire :
Des ARNm viraux
Des nouveaux brins ARN+
Virus de la classe 3 : ARN double brin (dsRNA)
Comment les ARNm viraux sont-ils exportés vers le cytoplasme ?
Ils sortent de la capside par des pores
Une fois dans le cytoplasme, ils sont traduits en :
ARN polymérase virale
Protéines de capside
Virus de la classe 3 : ARN double brin (dsRNA)
Comment se forme un nouveau génome dsRNA ?
Quand une capside est en formation, un brin ARN+ y pénètre
Une ARN polymérase virale forme alors le brin ARN– complémentaire
Cela crée un nouveau segment double brin
Virus de la classe 3 : ARN double brin (dsRNA)
Où se passent la transcription et la réplication chez les Reoviridae ?
À l’intérieur de la capside virale
→ C’est une caractéristique unique de ces virus