biokemiska processer KEMI
1/26
Earn XP
Description and Tags
prov v19
Name | Mastery | Learn | Test | Matching | Spaced | Call with Kai |
|---|
No analytics yet
Send a link to your students to track their progress
27 Terms
Vad är stegen för proteinsyntesen övergripligt? (anabola reaktionen som återbildar proteiner)
Process? | trans(K)ription | trans(L)ation | färdigställande |
Vad? | DNA → mRNA | mRNA → Polypeptid | Polypeptid → 3D protein |
Plats? | Cellkärnan → skickas ut i cytoplasman | I ribosomen | I golgiapparaten |
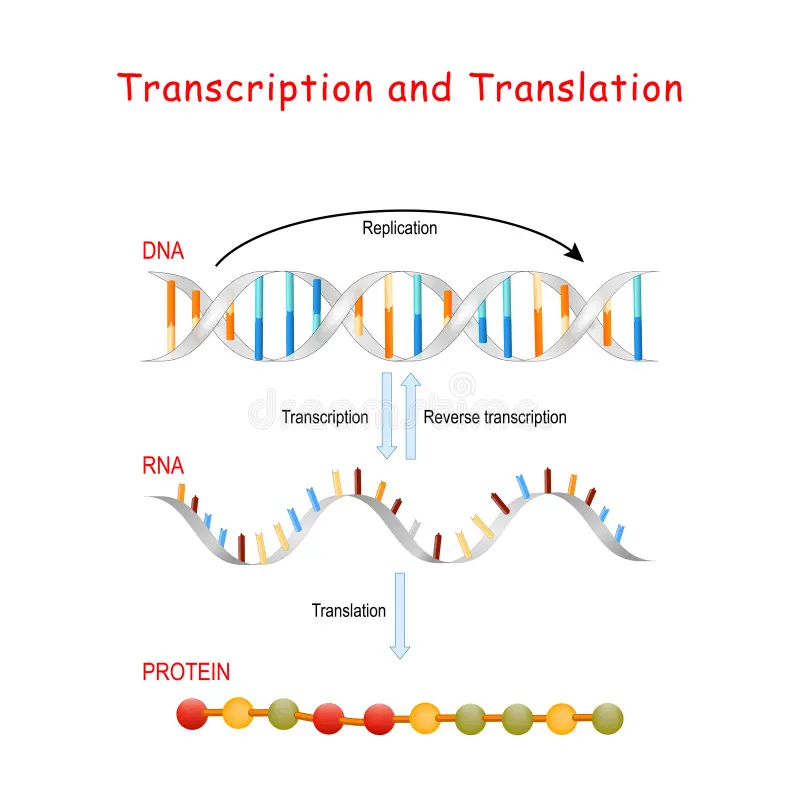
Hur går transkription till? (anabol reaktion som återbildar proteiner)
RNA polymeras öppnar upp dubbelhelixen och kommer tillsammans med transkriptionsfaktorer fästa sig på DNA-molekylen
Då börjar RNA polymeras läsa av kvävebaserna hos DNA och para kvävebaserna med fria mRNA nukleotider (AUGC) som byggs ihop till en mRNA sträng (denna mRNA sträng blir komplementär till DNA:t)
När (pre-)mRNA:t är byggt kommer den genomgå splitsning av intronerna(dock inte skräp DNA!) och blir ett färdigt/moget mRNA.
sedan åker mRNA strängen ut ur cellkärnan
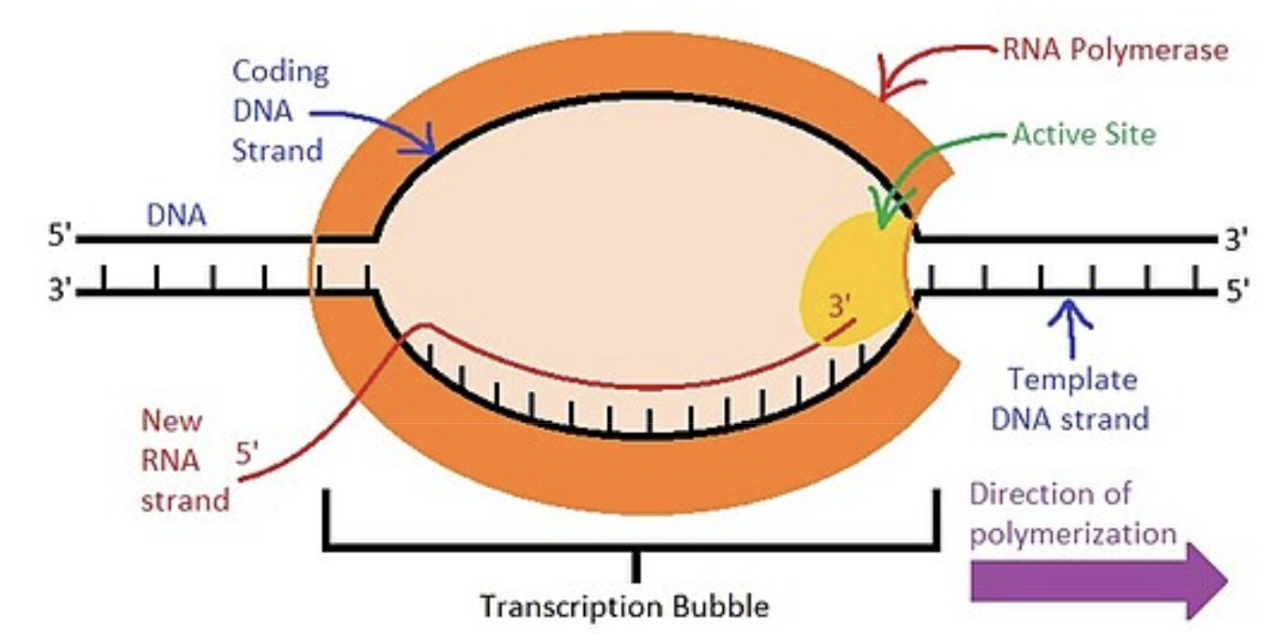
Hur går translationen till? (anabola reaktion som återbildar proteiner)
Ribosomens stora enhet söker efter startsekvensen AUG (alla mRNA strängar startar med metionin) då mRNA:t har skyddande kvävebaser innan startkodon och efter stoppkodon. Först läser ett säte i ribosomens stora enhet av en bokstav i taget för att hitta startkodon. Sedan kommer ett säte läsa av 3 kvävebaser(ett kodon) när den hittat startkodon.
När AUG är i A-sätet(annealing) kommer en tRNA med aminosyra med motsvarande antikodon (UAC) också fästa in i annealingssätet. Nu kommer ribosomen flytta 3 steg och så att nästa kodon hamnar i A-sätet. Då kommer motsvarande tRNA dit (t.ex med antikodonet GGA mot mRNAs CCU) med sin aminosyra. Nu kan en peptidbindning bildas mellan de två aminosyrorna.
Ribosomen flyttas igen : AUG i E-sätet, CCU i P-sätet, CAG i A-sätet. (2 peptidbindningar)
I E-sätet kommer tRNA:t släppa aminosyran och ribosomen och mRNA kedjan (AUG) och flyta runt och leta efter en ny aminosyra.
När ett stoppkodon hamnar i A-sätet släpper ribosomen från mRNA:t och polypeptidkedjan bildas. mRNA:t åker tillbaka till kärnan och återanvänds. Polypeptiden färdigställs till sin 3D-form (protein) i Golgiapparaten.
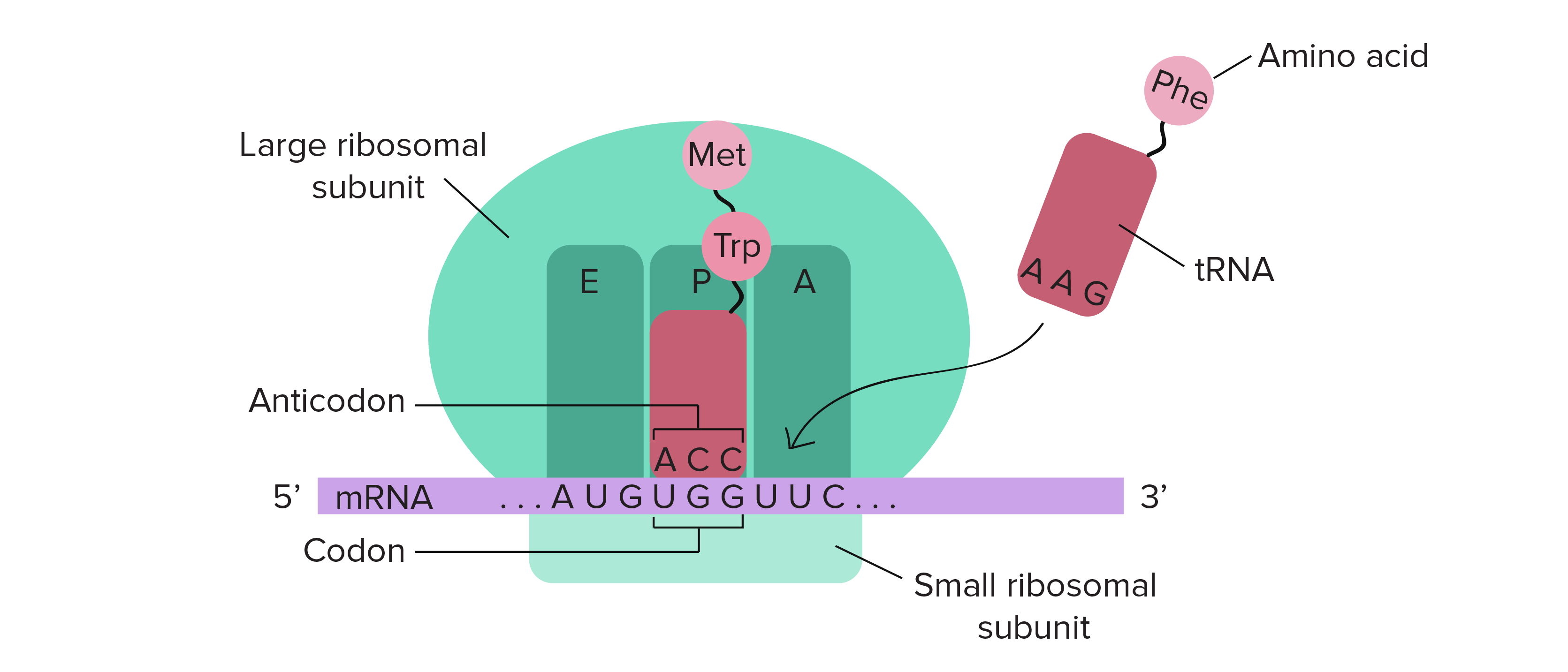
Vad kollar man på när man översätter kvävebaser till aminosyror?
mRNAs kodon som kommer matchas till en tRNA med korresponderande antikodon och aminosyra. Alltså är det mRNA som bestämmer aminosyran och dens kodon man kollar på i aminosyratabell.
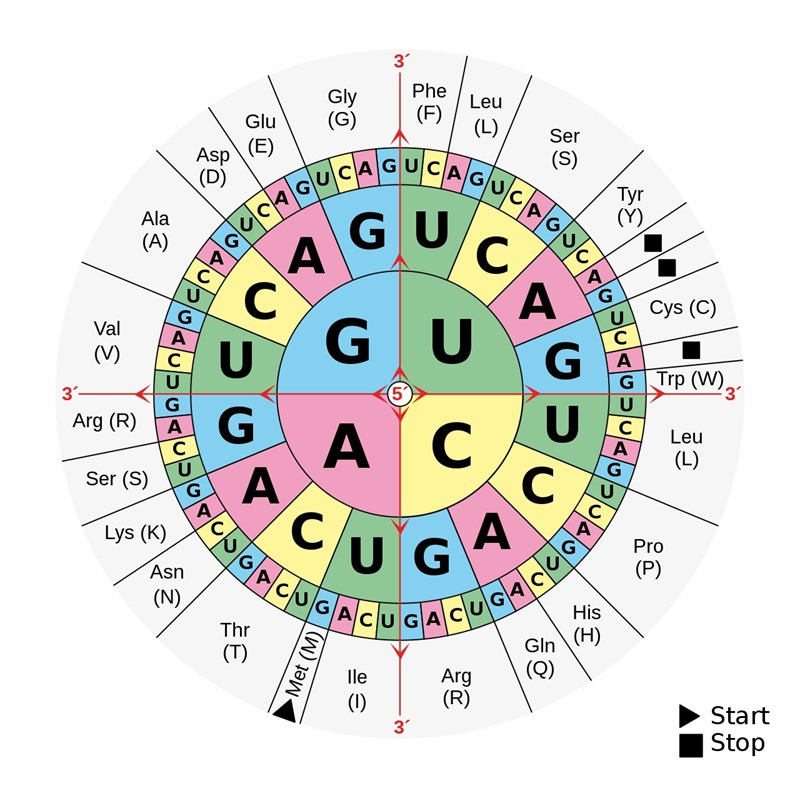
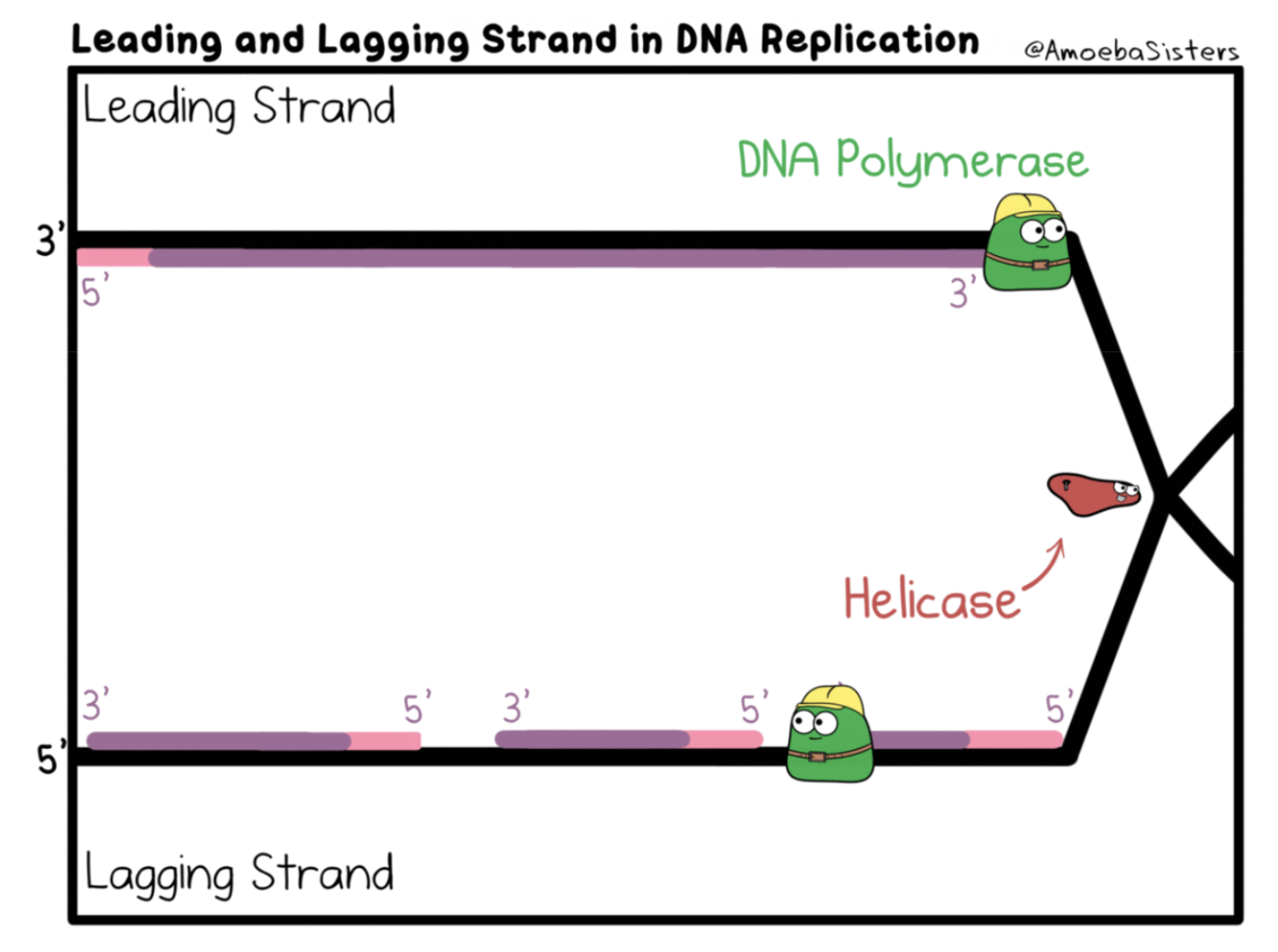
Hur sker DNA-replikationen?
DNA Replikation: Kopiering av hela DNA:t inför celldelning (mitos/meios)
Helikas öppnar upp en replikationsgaffel
Prime:rar fäster in(basparar till DNA:t) för att DNA polymeras ska kunna ha en del att fästas in i (en kort bit basparade nukleotider) primern består av mRNA nukleotider som sen behöver bytas ut
DNA polymeras läser av och börjar bygga på kvävebaserna och gör den komplementära DNA strängen till den övre (read up build down) Den läser 3’-5’ och bygger 5’-3’. Ena strängen kan byggas i ett svep (leading strand) men i lagging strand kommer vi få okazaki fragment eftersom de bara kan bygga det som redan har öppnats
Primerarna måste ersättas med DNA:nukleotider och sedan gör man en korrekturläsning
i dessa celler vi skapar får båda halva original DNA:t och halva nybyggda DNA:t
Vilka reaktioner består ämnesomsättningen av?
Energin i maten vi äter behöver först brytas ner (katabola reaktioner -frigör mer energi) för att sedan byggas upp (anabola reaktioner - kostar mer energi)
Katabolism + anabolism = metabolism (hela ämnesomsättningen)
Vad bryter de katabola reaktionerna ner och till vad?
Fett —> fettsyror
Kolhydrat —> glukos
Protein —> aminosyror
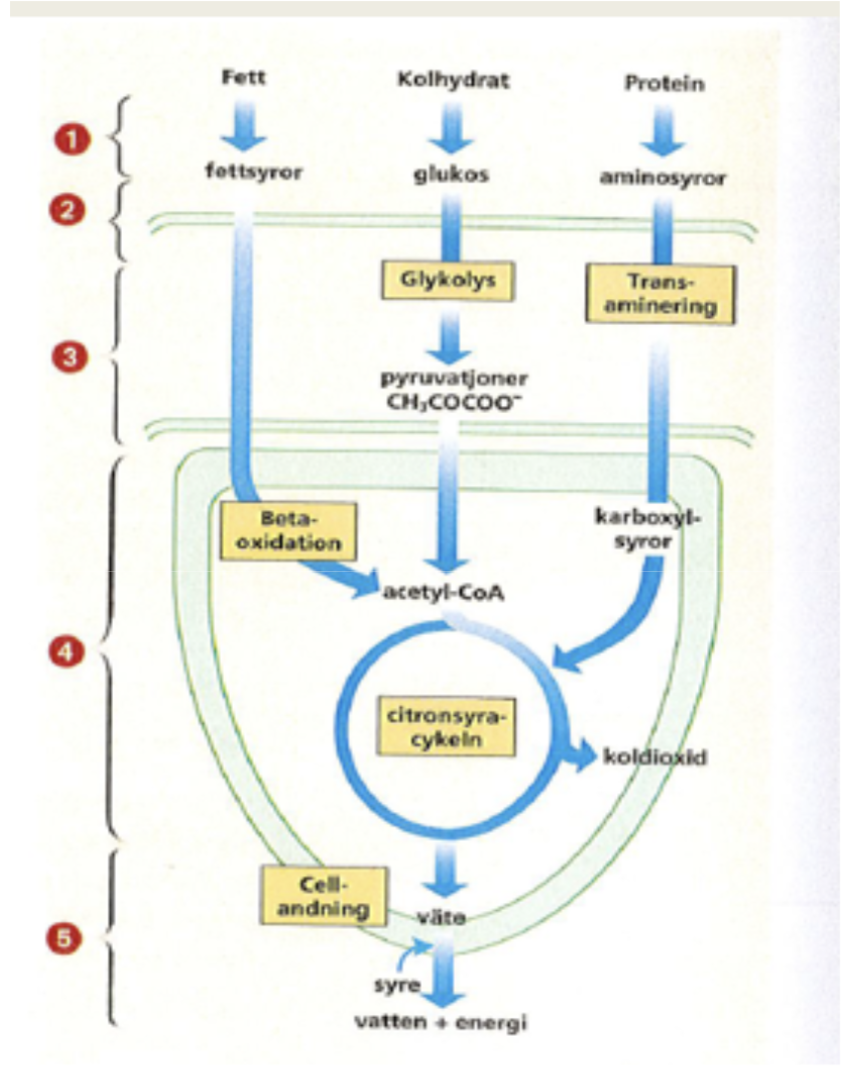
Vad händer med fettsyrorna i den katabola fasen?
De genomgår beta-oxidering i mitokondriens matrix där de blir till Acetyl CoA som används i citronsyracykeln som producerar: CO2 och väte där vätet genomgår ETK över mitokondriens membran och blir mha syre till vatten och ATP.
Vad händer med kolhydraterna i den katabola fasen?
Glukos i blodet tas upp av cellerna och genomgår sedan glykolys i cellplasman där de blir pyruvatjoner som blir till AcetylCoA via pyruvatlänken i mitokondriens matrix och används där till citronsyracykeln som producerar: CO2 och väte där vätet genomgår ETK över mitokondriens membran och blir mha syre till vatten och ATP.
Vad händer med aminosyrorna i den katabola fasen?
De genomgår transaminering i cellplasman och blir till karboxylsyror som används i citronsyracykeln i mitokondriens matrix som producerar: CO2 och väte där vätet genomgår ETK över mitokondriens membran och blir mha syre till vatten och ATP.
Vad bär bärarmolekyler på och vilka ska vi kunna?
energi
ATP, NADH / FADH2 och Acetyl CoA
Har vi ett ATP-lager?
Nej, kroppen i sig kan inte lagra ATP i jättestora mängder utan kroppen kräver kontinuerlig tillförsel. Därför dör man snabbt av syrebrist (ATP processen avstannar och vi har inget “ATP lager”)
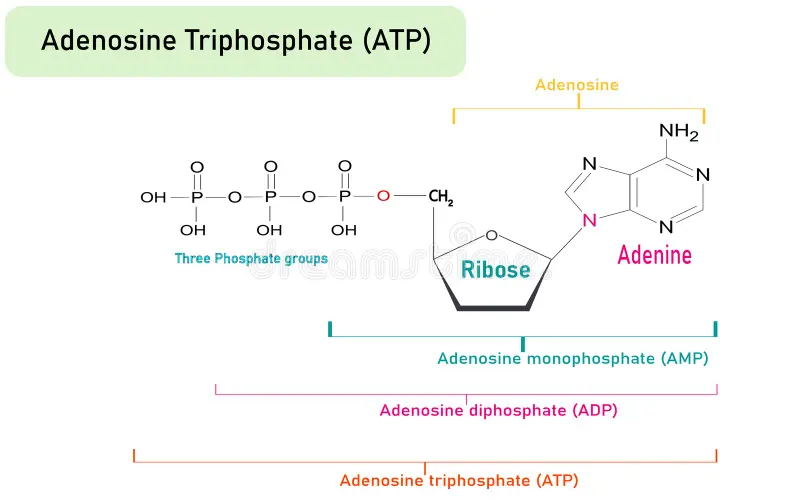
Hur ser strukturen för ATP, ADP, och AMP ut?
om ATP: “ni ska kunna känna igen den men inte rita upp hela”
istället för fosfatgrupperna kan man skriva X st Pi för inorganic fosfatgrupp
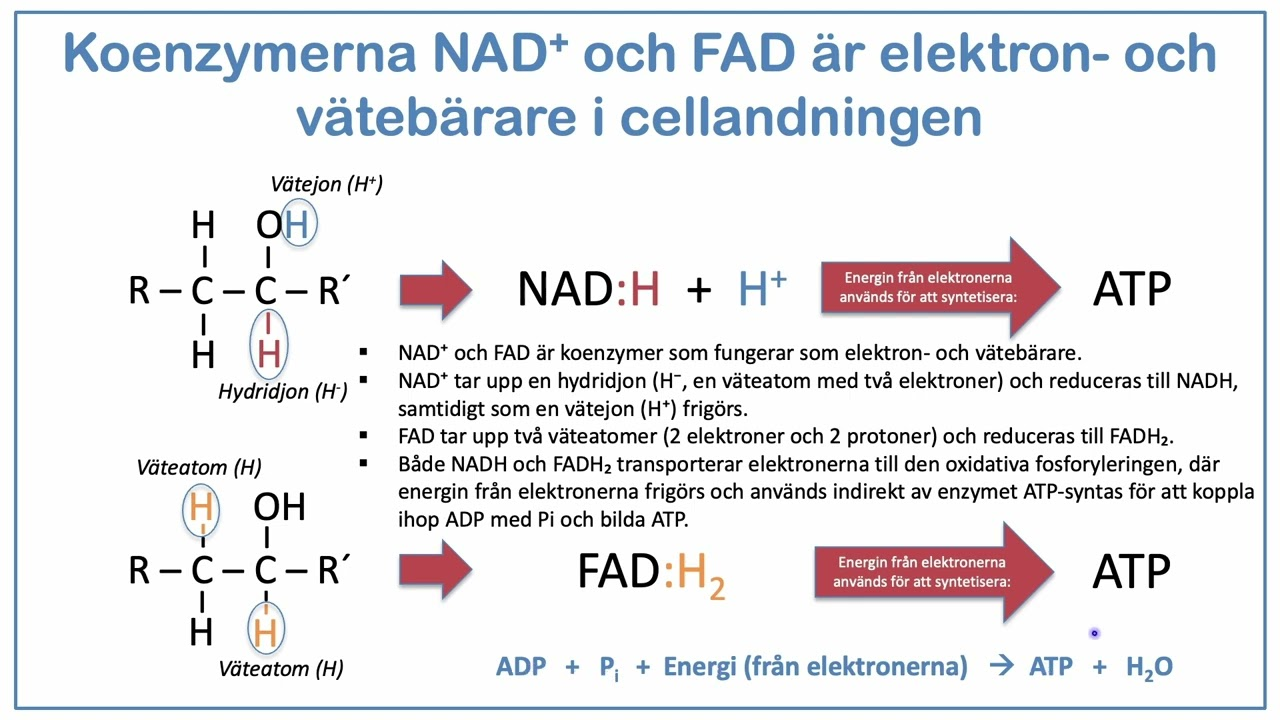
vad kallas NADH och FADH2?
sekundära energibärare som bär på energi från tex glukos
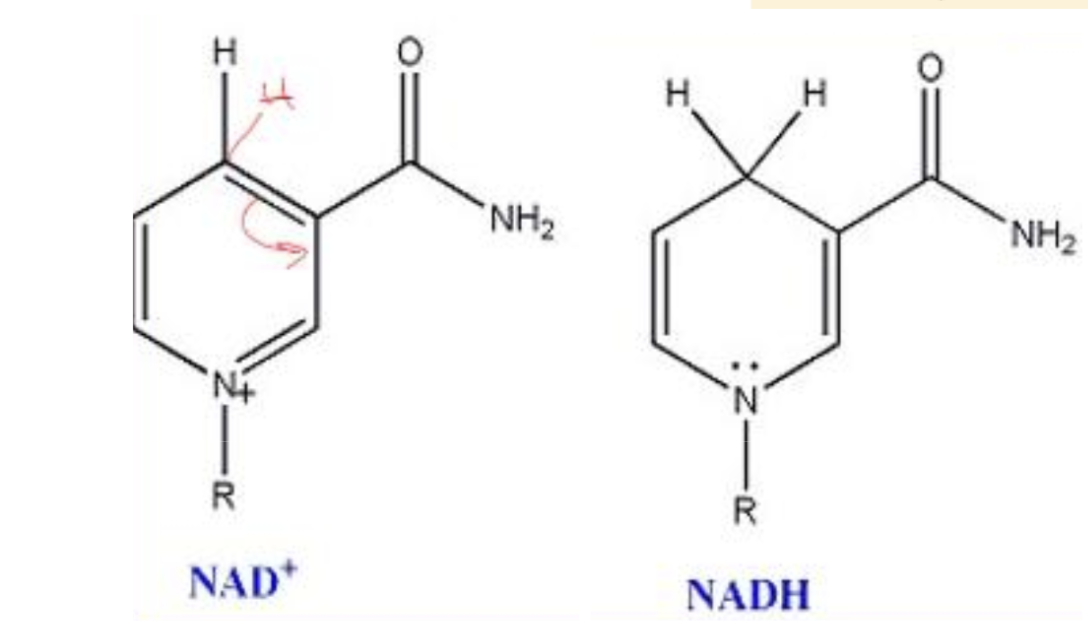
Hur används NADH/NAD+
NADH/NAD+ alterneringen används för att generera nya ATP molekyler enligt: NAD+ + 2H → NADH + H+ “behöver inte veta varför”. från 2H så tar ett H 1e- från det andra H, bildar då H- och H+. H- binds in till NAD+ som då blir NADH och en fri H+ bildas. Kallas för en sekundär energibärare (även FAD+ och FADH2)
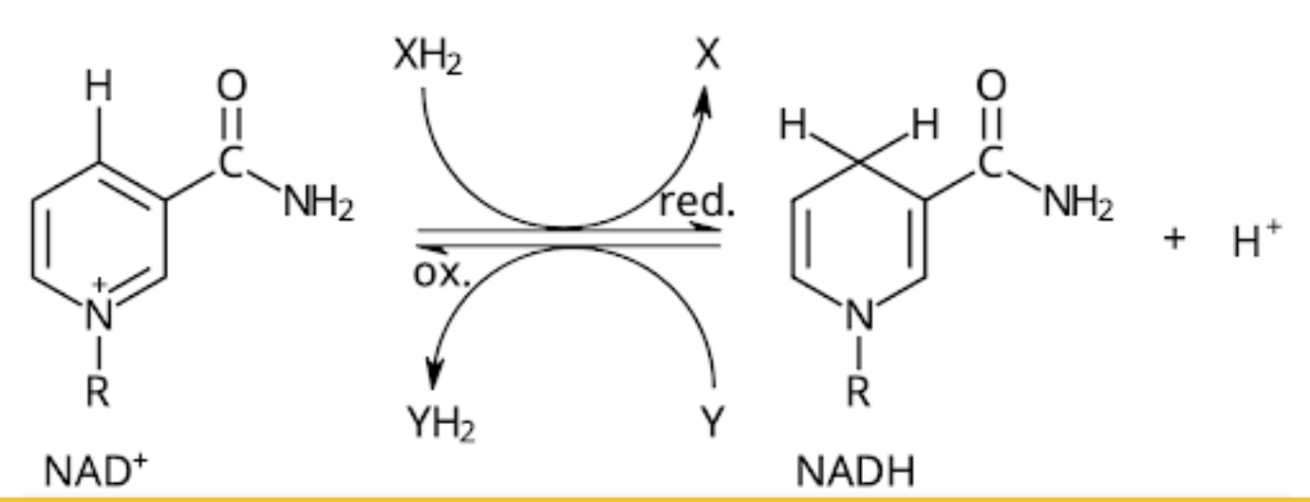
Är NADH eller NAD+ respektive FAD+ eller FADH2 den energirika formen?
NADH och FADH2
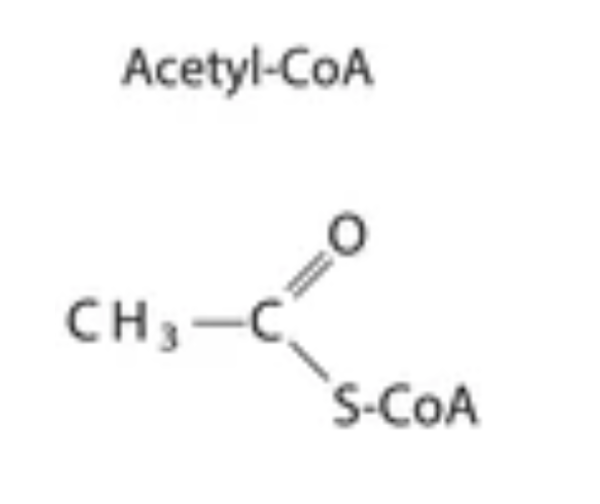
Hur används Acetyl CoA?
Acetyl CoA: används i citronsyracykeln. Består av en acetylgrupp + coenzym A.
(Ser nästan ut som ättiksyra CH3COOH men OH utbytt till svavel och CoA) AcetylCoA bär vidare acetylgrupper från glykolysen samt beta-oxideringen till citronsyracykeln.
Hur bryts kolhydrater ner och vad händer med dem? (katabola reaktionerna)
glykolys
pyruvatlänken
citronsyracykeln
elektrontransportskedjan
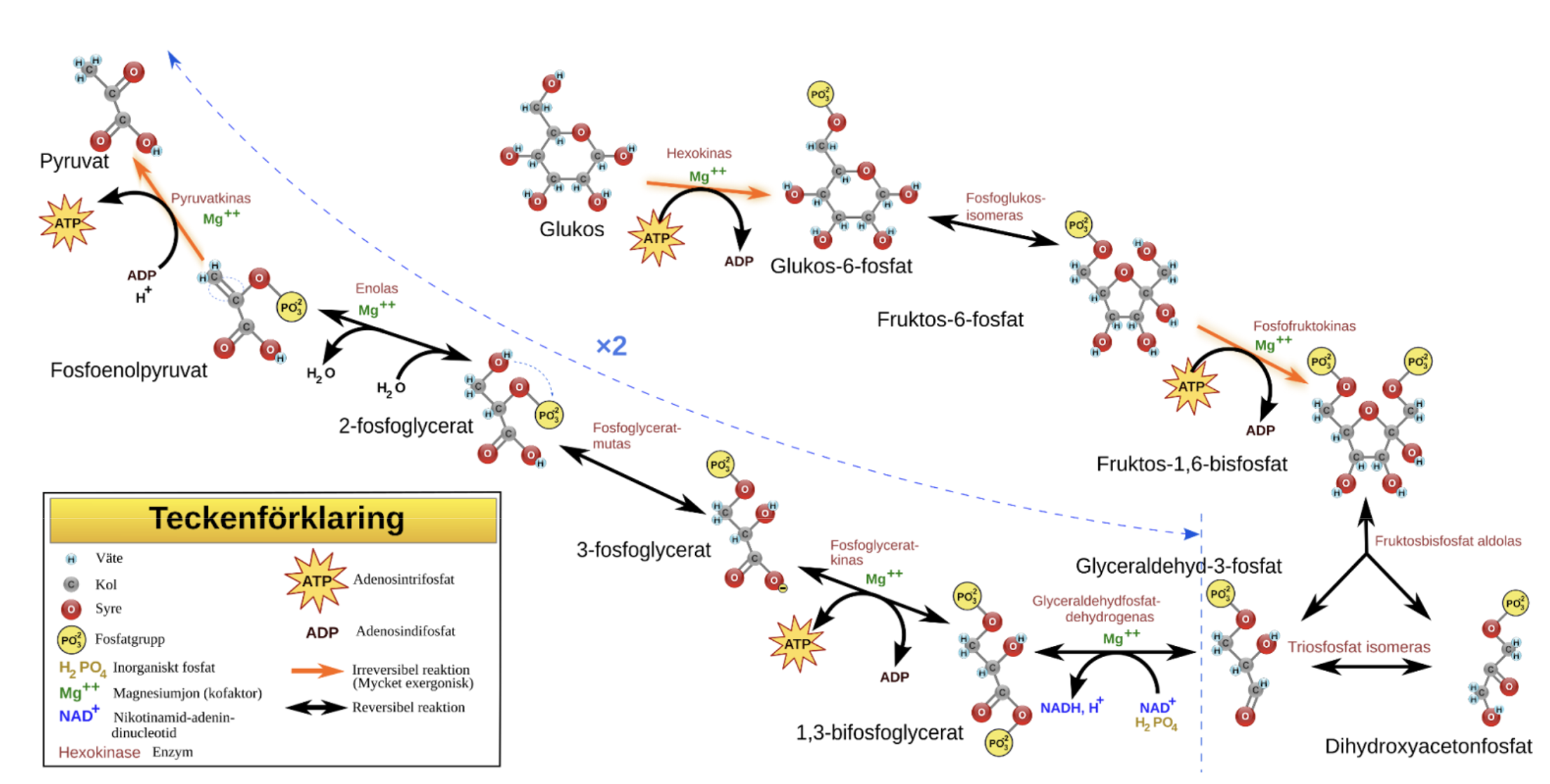
Allmänt om glykolysen (1)
Mål: bryta ner glukos till 2 pyruvatjoner
sker i alla levande celler (prokaryota + eukaryota) då den inte kräver syre
sker i cytoplasman (cellvätskan)
Detta behöver ske i flera delreaktioner för att inte generera mer värme än cellerna tål.
Energi per glukosmolekyl: 2 ATP + 2 NADH+H+
Steg 5-9 sker två gånger eftersom bara ena produkten i steg 4 kan reagera vidare
Den består av 1 energiinvesterande del som kräver energi - 2 ATP.
Nästa del är 1 energiutvinnande del där vi per glukosmolekyl får ut 4 ATP och 2 NADH (& H+) och nettoprodukten blir 2 ATP.
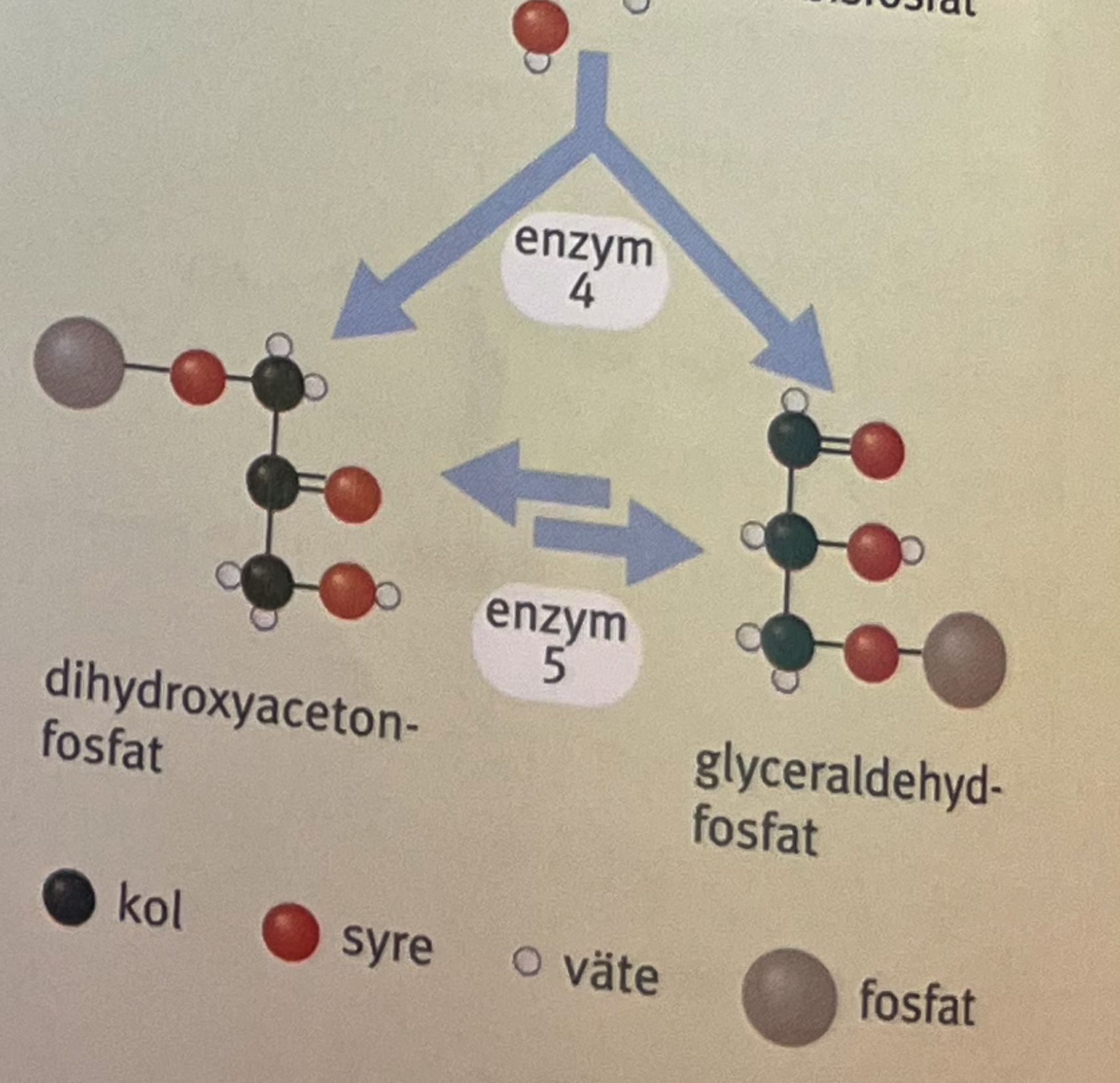
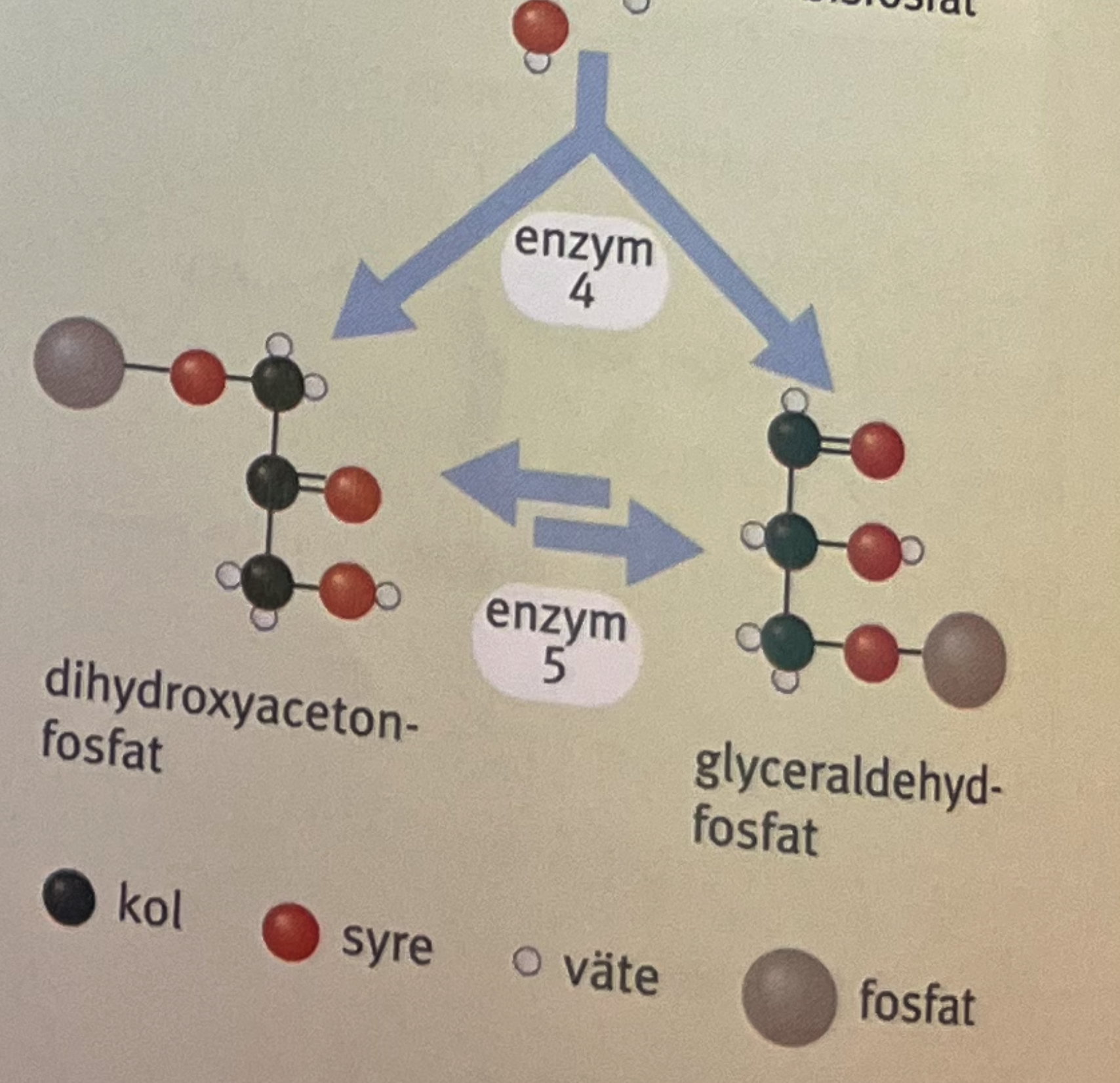
förklara bilden (glykolys)
molekylen klyvs i två delar och glyceraldehyd-3-fosfat är den som kan reagera vidare och när den minskar i antal kommer jämvikten driva dihydroxyacetonfosfat till att isomeras till glyceraldehyd-3-fosfat vilket skapar ett 100% utbyte av fruktoset som bildas i steg 4.
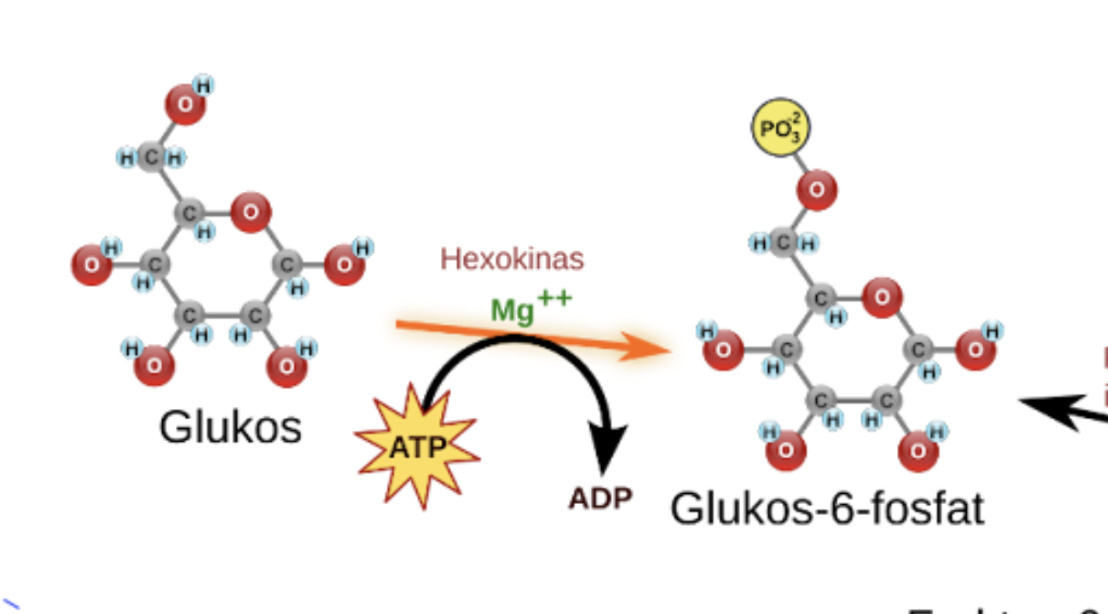
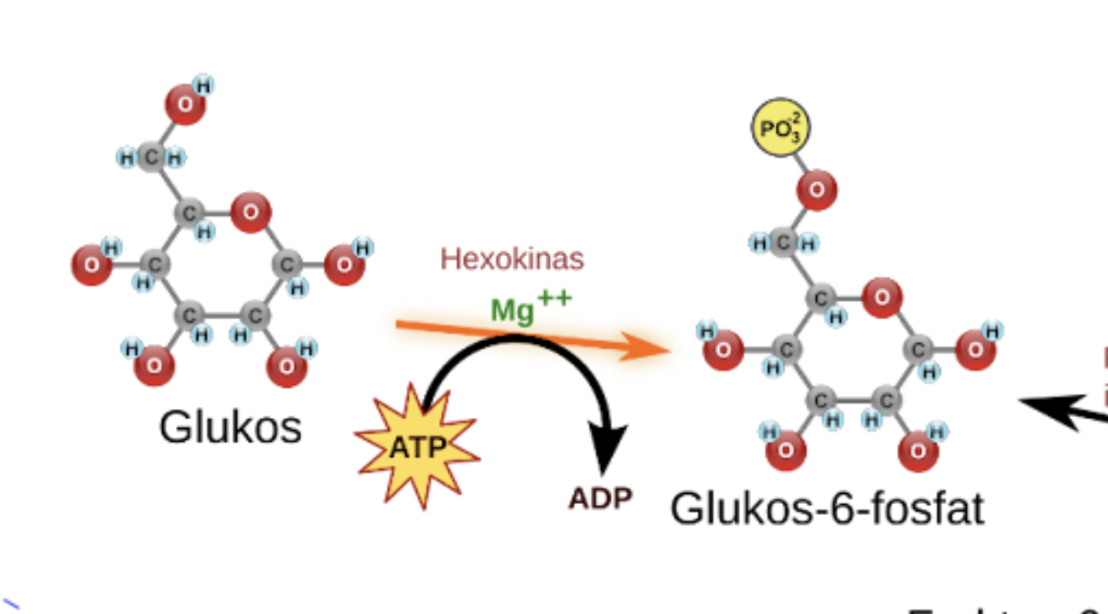
Förklara bilden (steg 1 glykolys)
Glukos blir till glukos-6-fosfat genom att den tar upp en fosfatgrupp => gör att den inte åker tillbaks ut ur cellmembranet pga att fosfatgruppen är laddad PO4-3
samtidigit ökar molekylen i energi då ATP —> ADP + Pi + energi
Att det sker i små steg som dessa förklaras också av att man vill minska värmeproduktionen
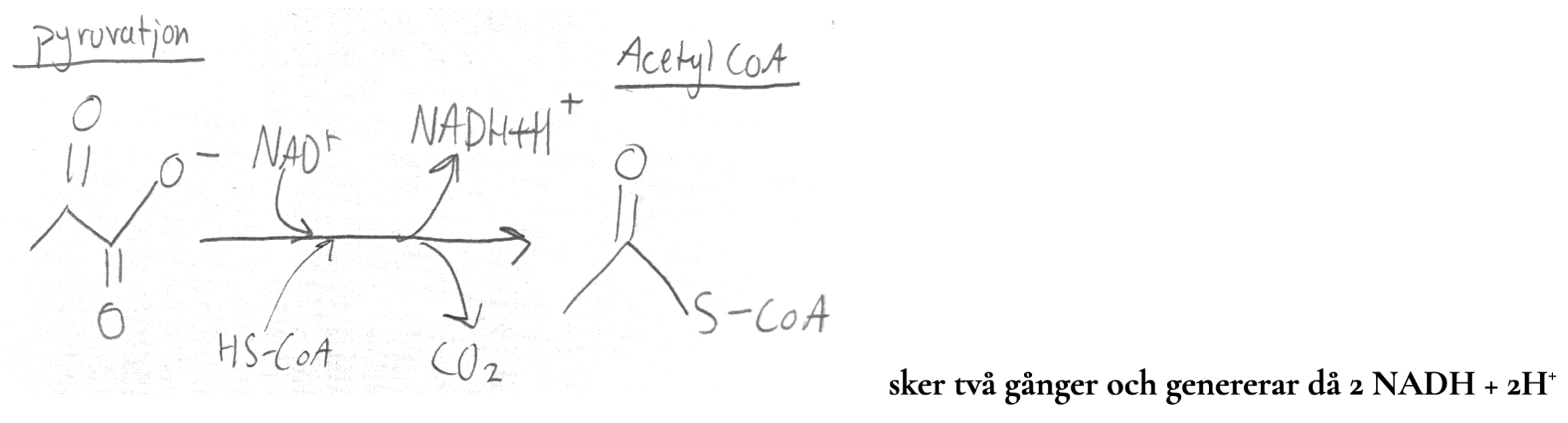
allmänt om pyruvatlänken (2)
sker två gånger per glukos då det bildats 2 pyruvatjoner från glykolysen
vill skapa AcetylCoA som kan gå in i citronsyracykeln, vi skapar även koldioxid som vi andas ut, och NADH + H+.
Pyruvatlänken sker över mitokondriens yttre membran (?)
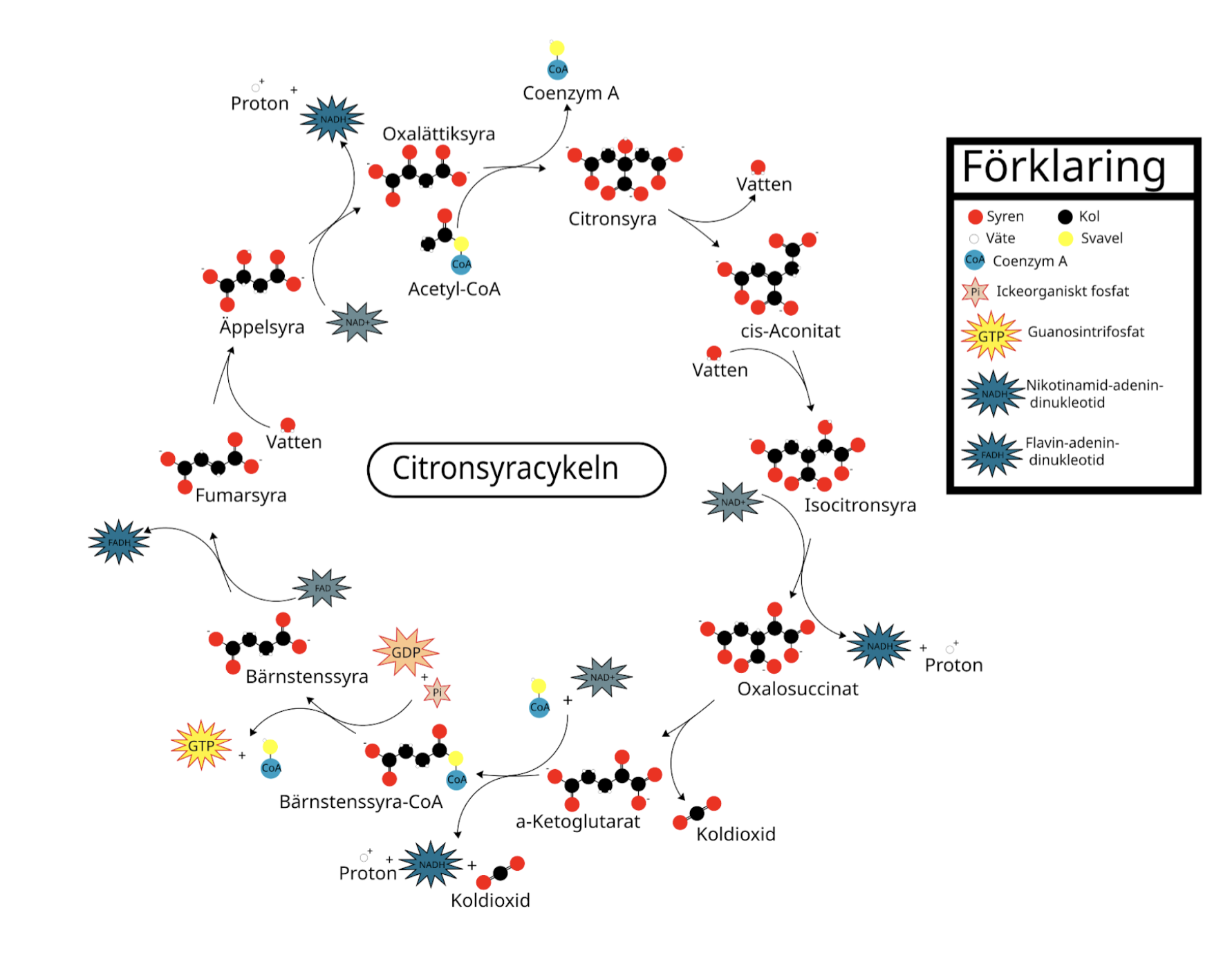
allmänt om csc (3)
sker två gånger per glukos eftersom två pyruvat har genererat 2 acetylCoA
sker i mitokondriens matrix: utgångsmaterial = oxalättiksyra
Huvudmål: använda Acetyl-CoA för att generera NADH + H+, FADH2 som skickas till ETK för att bilda ATP.
vi bildar koldioxid här och i pyruvattransporten.
Vad genererar citronsyracykeln per glukosmolekyl? (två varv)-
6 NADH + H+
2 FADH2
2 GTP
4 CO2
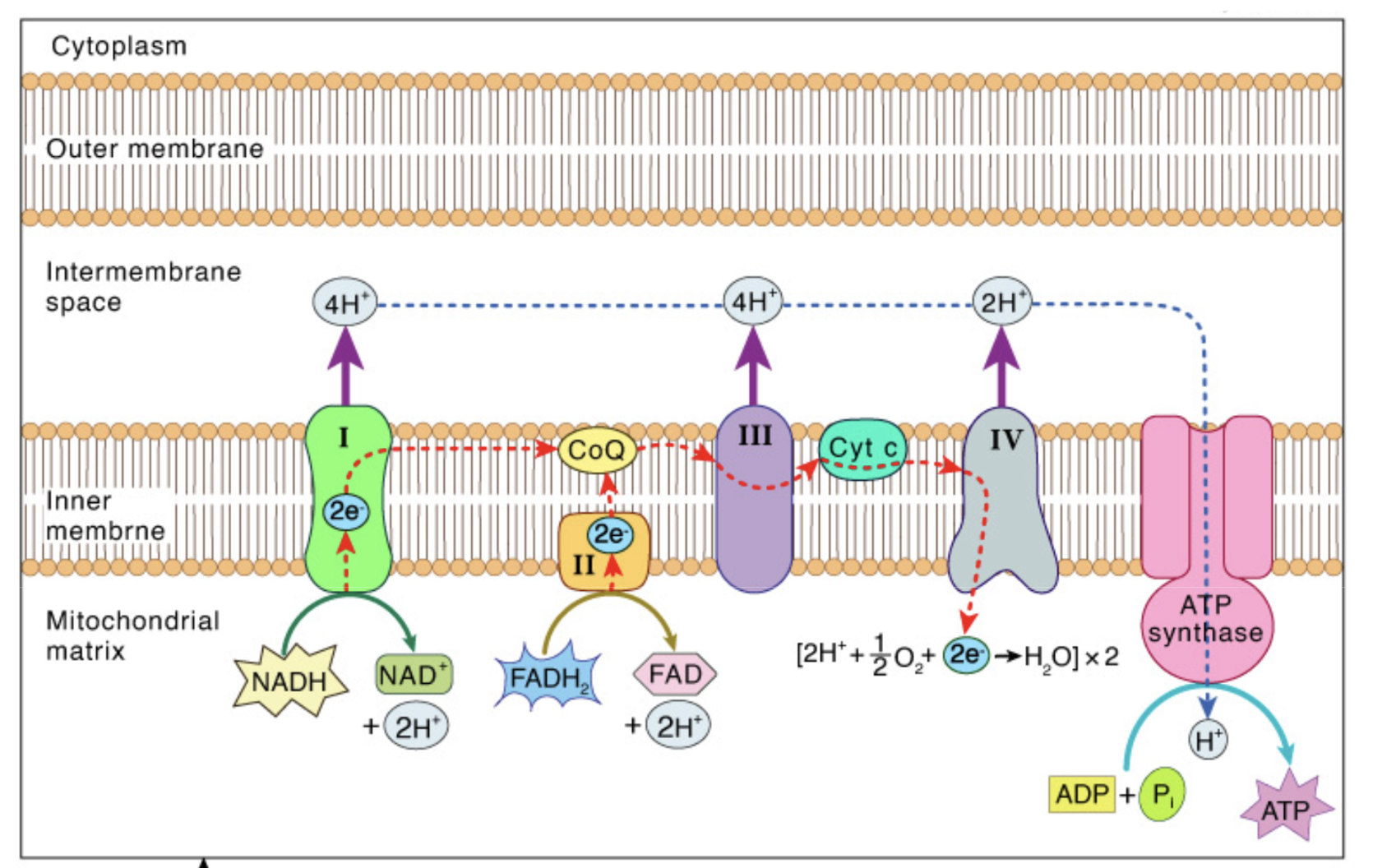
allmänt om ETK (4)
sker över mitokondriens inre membran
Mål: flytta vätejoner till intermembranområdet med hjälp av energi från elektrontransporten
Aktiv pumpning - kräver energi som vi får från flödet av elektroner (ej ATP)
Kräver att syre agerar elektronacceptor
Vi använder vätejonkoncentrationsgradienten (fler H+ i intermembranområdet än i matrixen) som transporteras genom ATP syntasen för att hjälpa reaktionen: ADP + Pi → ATP
Hur många ATP bildas totalt från glykolysen —> ETK?
30-38 per glukos
Vilka kriterier finns för att kunna bilda ATP?
NADH + H+ (lämnar elektroner)
FADH2 (lämnar elektroner)
O2 (elektronacceptor) - inte från luften vi andas in
förhöjd vätejonkoncentration på ena sidan
ifall dessa saknas avstannar ETK - händer även om bara O2 saknas då elektroner inte kan transporteras
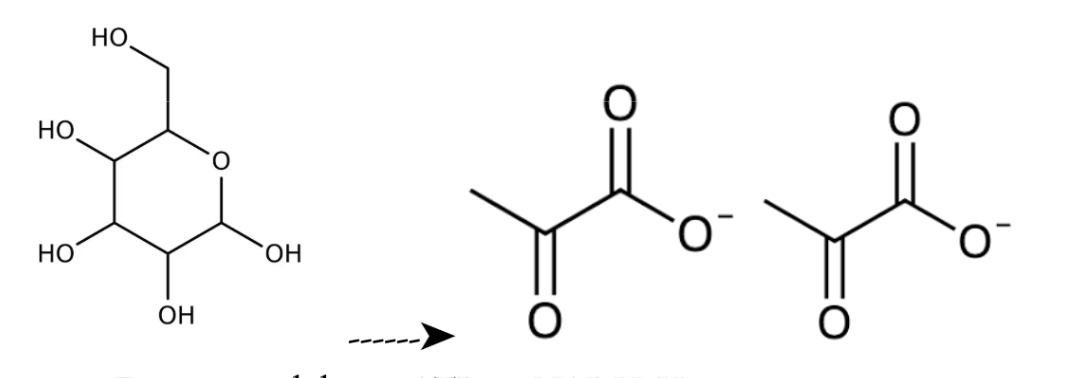
varför bildas mjölksyra?
Mjölksyra bildas då kroppen får ett överskott av pyruvat vilket kan ske tex vid syrebrist. Det leder till att elektrontransportkedjan minskar i hastighet, detta gör att varken ATP eller NAD+ inte skapas. Det blir brist på NAD+.
NAD+ bildas av det enzym som omvandlar pyruvat till mjölksyra. Det gör att glykolysen kan fortsätta att producera 2 ATP (kräver NAD+).
juhigytfr
Citronsyracykeln är dock direkt kopplad till elektrontransportkedjan då de delar ett gemensamt enzym. Citronsyracykeln stannar därför ändå.