sequencing
La méthode Sanger (fonctionne pour un gène)
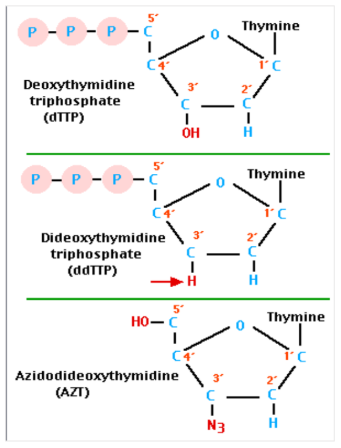
repose sur l'utilisation de didésoxynucléotides (ddNTP). Les ddNTP sont des nucléotides modifiés qui ne possèdent pas le groupe hydroxyle en 3' nécessaire à la formation de la liaison phosphodiester qui relie les nucléotides entre eux. Par conséquent, lorsqu'un ddNTP est incorporé dans un brin d'ADN en cours de synthèse, la synthèse s'arrête. Ensuite on fait une éléctrophorèse et la
détection:
autoradiographie, je crois que les ddNTP sont visibles
Les ddNTP sont marqués avec des fluorophores de couleurs différentes, ce qui permet d'identifier le nucléotide présent à l'extrémité de chaque fragment. On voit des bande de couleur avec un détecteur
Illumina /Deep sequencing (fonctionne pour genome)
aussi appelé séquençage à haut-débit. Ca pause problème quand on a des séquences répétitives
étapes
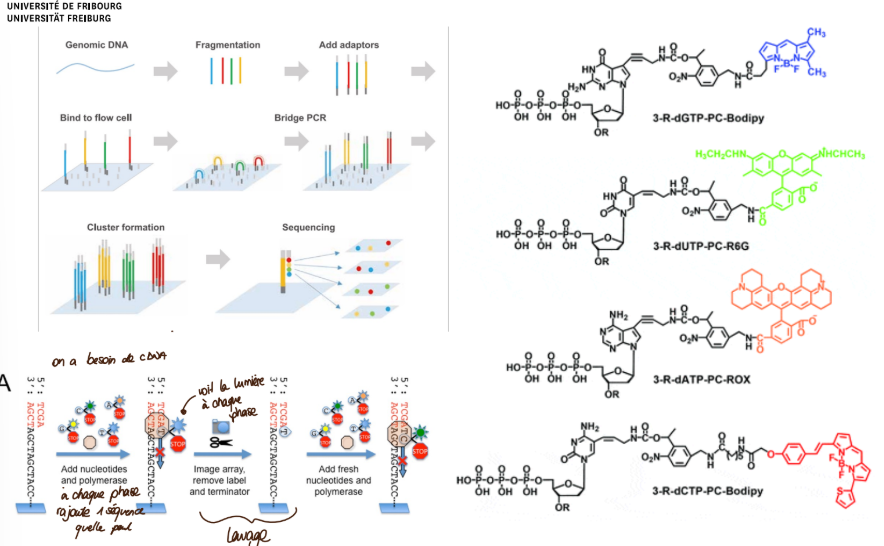
Préparation de l'échantillon : L'ADN à séquencer est fragmenté en petits morceaux, puis des adaptateurs sont ajoutés à chaque fragment. Ces adaptateurs contiennent des séquences nécessaires à l'amplification et au séquençage.
Amplification clonale : Chaque fragment d'ADN est amplifié par PCR sur une "flow cell", une surface solide contenant des millions de brins d'ADN complémentaires aux adaptateurs. Chaque fragment est ainsi cloné en un amas de molécules identiques.
Séquençage par synthèse : Des nucléotides fluorescents sont ajoutés un par un à chaque brin d'ADN en cours de synthèse. Chaque nucléotide émet une fluorescence spécifique qui est détectée par un système optique. L'ordre des nucléotides est ainsi déterminé pour chaque fragment d'ADN.
→ il faut faire beaucoup de cycle
Analyse des données : Les données de séquençage sont analysées par des logiciels bioinformatiques pour reconstituer la séquence complète de l'ADN.
Nanopore sequencing
passage d'un brin d'ADN à travers un nanopore, chaque base provoque une variation caractéristique du courant électrique. Ces variations sont enregistrées et analysées pour déterminer la séquence de chaque fragment d'ADN. Il peut même voir la méthylation et analyser une partie de l’épigénétique.
avantages:
Lectures longues
Séquençage direct de l'ARN, pas besoin de transformer en ADN
Analyse en temps réel
Portabilité
désavantages:
coût
Taux d'erreur plus élevé